IDENTIFIKASI MOLEKULER BROAD BEAN WILT VIRUS 2 (BBWV2) DAN CYMBIDIUM MOSAIC VIRUS (CYMMV) ASAL TANAMAN NILAM (POGOSTEMON CABLIN BENTH.
|
|
|
- Sugiarto Halim
- 6 tahun lalu
- Tontonan:
Transkripsi
1 J. HPT Tropika. ISSN J. HPT Tropika Vol. 15, No. 2: , September 2015 Vol. 15 No. 2, 2015: IDENTIFIKASI MOLEKULER BROAD BEAN WILT VIRUS 2 (BBWV2) DAN CYMBIDIUM MOSAIC VIRUS (CYMMV) ASAL TANAMAN NILAM (POGOSTEMON CABLIN BENTH.) Miftakhurohmah1, Gede Suastika2, Tri Asmira Damayanti2, & Rita Noveriza1 1 Balai Penelitian Tanaman Rempah dan Obat Jl. Tentara Pelajar No. 3, Bogor Departemen Proteksi Tanaman, Fakultas Pertanian, Institut Pertanian Bogor Jl. Kamper, Kampus IPB Dramaga, Bogor miftah_tia05@yahoo.co.id ABSTRACT Molecular identification Broad Bean Wilt Virus 2 (BBWV2) and Cymbidium Mosaic Virus (CymMV) from patchouli plant (Pogostemon cablin Benth.). Several viruses have been reported to be associated with mosaic disease on patchouli plant in Indonesia. This study aims to identify the two viruses in patchouli cultivation in West Java by studying the molecular characterization. Mosaic symptomatic leaf samples taken from patchouli cultivation in Manoko (Bandung Barat District, West Java Province). RNA extraction was performed using Xprep Plant RNA mini kit. RNA amplification with RT-PCR technique using primers for the cp gene region of BBWV2 and CymMV. The PCR product was sent to PT. Science Genetics Indonesia to do sequencing, then analyzed nucleotide sequences. Results of RT-PCR were performed successfully obtained DNA bands with size accordance with the predictions of the primer design for BBWV2 and CymMV cp region. Further, based on nucleotide and amino acid sequence analyses, the two virus isolates were confirmed as BBWV2 and CymMV respectively. Phylogenetic analyses revealed that BBWV2 Manoko clustered with BBWV2 from Singapore (original host of Brazilian red-cloak), China (pepper) and South Korea (chili). Whereas, CymMV Manoko become one cluster with CymMV from India (Phaius sp.), Indonesia (Dendrobium), China (vanilla), Thailand (Oncidium), Hawai (Dendrobium) and South Korea (Cymbidium). Key words: nucleotide sequence, virus, patchouli, BBWV2, CymMV ABSTRAK Identifikasi molekuler Broad Bean Wilt Virus 2 (BBWV2) dan Cymbidium Mosaic Virus (CymMV) asal tanaman nilam (Pogostemon cablin Benth.). Beberapa virus dilaporkan berasosiasi dengan penyakit mosaik pada tanaman nilam di Indonesia. Penelitian ini bertujuan mengidentifikasi dua virus pada pertanaman nilam di Jawa Barat dengan mempelajari karakterisasi molekulnya. Sampel daun bergejala mosaik diambil dari pertanaman nilam di Manoko (Kabupaten Bandung Barat, Provinsi Jawa Barat). Ekstraksi RNA dilakukan menggunakan Xprep Plant RNA mini kit. Amplifikasi RNA dengan teknik RT-PCR menggunakan primer untuk daerah gen cp BBWV2 dan CymMV. Produk PCR yang dihasilkan dikirimkan ke PT. Genetika Science Indonesia untuk dilakukan perunutan nukleotida, dan selanjutnya dianalisis runutan nukleotidanya. Hasil RT-PCR yang dilakukan berhasil didapatkan pita DNA dengan ukuran sesuai prediksi dari desain primer untuk bagian cp BBWV2 dan CymMV. Berdasarkan analisis runutan nukleotida dan asam amino, dua virus yang ditemukan merupakan BBWV2 dan CymMV. Analisis homologi dan filogenetik menunjukkan bahwa BBWV2 Manoko mengelompok dengan BBWV2 dari Singapura (Brazilian red-cloak), (lada) dan Korea Selatan (cabai). Sedangkan CymMV Manoko berada dalam satu kelompok dengan CymMV dari India (Phaius sp.), Indonesia (Dendrobium), China (vanili), Thailand (Oncidium), Hawai (Dendrobium) dan Korea Selatan (Cymbidium). Kata kunci: sekuen nukleotida, virus, nilam, BBWV2, CymMV PENDAHULUAN Infeksi virus pada tanaman nilam di Indonesia telah ditemukan sejak tahun 1996 oleh Sumardiyono et al. (1996), yang berdasarkan uji serologi dengan antibodi patchouli mottle virus (PatMoV), menunjukkan reaksi positif. Pada pertanaman nilam di Cianjur dan Bogor, ditemukan infeksi campuran antara cucumber mosaic virus (CMV) dan genus Potyvirus (Sukamto et al., 2007). Gejala mosaik ditemukan pada beberapa pertanaman nilam di Jawa Tengah, Jawa Barat, Sumatera Utara dan Sumatera Barat. Berdasarkan hasil
2 Miftakhurohmah et al. deteksi dan identifikasi, penyakit berasosiasi dengan telosma mosaic virus (TeMV) yang tergolong ke dalam genus Potyvirus (Noveriza et al., 2012). Selain genus Potyvirus dan CMV, juga ditemukan infeksi virus lain pada pertanaman nilam di Manoko (Kabupaten Bandung Barat, Provinsi Jawa Barat) yang berdasarkan deteksi secara serologi merupakan BBWV2 dan CymMV. Kedua virus tersebut merupakan virus pada tanaman nilam yang tergolong patogen A1, dalam arti belum pernah ada laporan serangan virus ini pada tanaman di Indonesia (Badan Karantina Pertanian, 2011). Berdasarkan pengamatan, saat ini sebagian besar bibit nilam hasil perbanyakan vegetatif sudah terserang virus dengan berbagai gejala sebelum ditanam di lapangan. Berdasarkan hal tersebut diatas, perlu dilakukan identifikasi lanjut BBWV2 dan CymMV yang menginfeksi pertanaman nilam. Deteksi secara serologi memiliki kelemahan, yaitu tidak bisa membedakan virus yang sekerabat, terutama bila yang digunakan antiserum universal genus. Selain itu, beberapa antigenic site dimiliki oleh virus yang tidak sekerabat, sehingga memungkinkan terjadinya reaksi silang (Putnam, 1995). Oleh karena itu, hasil deteksi secara serologi perlu dilanjutkan dengan identifikasi berdasarkan asam nukleat. Hasil identifikasi digunakan sebagai salah satu dasar dalam pengambilan tindakan pengendalian. Identifikasi berdasarkan asam nukleat dilakukan secara molekuler, dengan teknik Polymerase chain reaction (PCR). Untuk diagnosis virus tanaman yang memiliki asam nukleat RNA, RNA target dikonversikan menjadi complementary DNA (cdna) yang dikopi dengan transkripsi balik sebelum PCR dimulai (Naidu & Hughes, 2003). Dari hasil RT-PCR, selanjutnya dilakukan perunutan nukleotidanya, yang dapat digunakan untuk mengklasifikasikan virus berdasarkan genomnya. Penelitian terdahulu menunjukkan bahwa analisis runutan nukleotida coat protein (cp) sangat berguna dalam kegiatan identifikasi BBWV1 dan BBWV2 (Kobayashi et al., 2005; Kondo et al., 2005). Beberapa software telah tersedia untuk mengklasifikasikan virus berdasarkan genomnya, diantaranya BioEdit, MEGA, dan GeneDoc (Tamura et al., 2007; Hall, 1999). Penelitian bertujuan mengidentifikasi BBWV2 dan CymMV pada tanaman nilam di Jawa Barat dengan mempelajari karakterisasi molekulnya. METODE PENELITIAN Tempat dan Waktu. Penelitian dilaksanakan di Laboratorium Virologi Tumbuhan, Fakultas Pertanian, Identifikasi Molekuler BBWV2 dan CYMMV 189 Institut Pertanian Bogor, dari bulan Februari sampai dengan Agustus Sumber Virus. Virus diambil dari daun bergejala mosaik pada pertanaman nilam di Kebun Percobaan (KP) Manoko (Kabupaten Bandung Barat). Gejala mosaik yang ditemukan bervariasi, dari mosaik lemah, mosaik kuning hijau, mosaik hijau muda hijau tua, mosaik dengan penebalan dan mosaik dengan perubahan bentuk daun (malformasi). Reverse transcription polymerase chain reaction (RT-PCR) Ekstraksi RNA. Ekstraksi RNA dilakukan dengan Xprep Plant RNA mini kit (PKT-Philekorea Technology). Bufer XPRB disiapkan dengan menambahkan 1% mercaptoethanol (ME). Sampel daun nilam sebanyak 0,1 g digerus menggunakan nitrogen cair pada mortar, sampai menjadi serbuk. Serbuk sampel ditambah bufer XPRB yang telah ditambah ME, dimasukkan ke dalam kolom filter dan disentrifugasi selama dua menit pada kecepatan rpm. Supernatan dipindahkan ke tabung eppendorf baru dan etanol absolut ditambahkan sebanyak 0,5 kali volume supernatan, dan dicampur dengan cara dipipet atau dibolak-balik. Kemudian supernatan dalam alkohol dimasukkan ke dalam kolom XPPLR mini, dan disentrifugasi selama satu menit pada kecepatan rpm. Setelah supernatan dibuang, kolom diberi wash buffer 1 (WB1) sebanyak 500 µl, disentrifugasi selama satu menit, dan supernatan dibuang. Wash buffer 2 (WB2) sebanyak 750 µl ditambahkan ke dalam kolom, disentrifugasi selama satu menit, dan supernatan dibuang. Selanjutnya, untuk mengeringkan kolom, dilakukan sentrifugasi kolom selama tiga menit pada kecepatan rpm. RNA total dikoleksi dengan cara memberikan air bebas nuklease sebanyak 50 µl ke pusat membran kolom XPPLR yang diletakkan pada tabung eppendorf baru, dibiarkan selama satu menit, lalu disentrifugasi selama satu menit. RNA yang telah diperoleh disimpan di freezer -80 oc, sampai digunakan. Sintesis complementary DNA (c-dna ). Reaksi reverse transcription (RT) dilakukan untuk membuat cdna dengan menggunakan enzim reverse transcriptase. Pereaksi yang digunakan terdiri atas air bebas nuklease (3,7 µl), bufer RT 5x (2 µl), DTT 50 mm (0,35 µl), dntp 10 mm (0,5 µl), M-MuLV Rev (Fermentas) (0,35 µl), RNase Inhibitor (0,35 µl), Oligo d(t) 10 µm (0,75 µl) dan RNA templat (2 µl) dengan total volume sebanyak 10 µl. Setiap komponen reaksi dipipet satu persatu, dimasukkan ke dalam tabung
3 190 J. HPT Tropika Vol. 15 No. 2, 2015: 188 eppendorf berukuran 0,5 µl, kemudian dimasukkan ke dalam mesin PCR. Reaksi RT dilakukan selama satu jam pada suhu 42 oc. Amplifikasi cdna. Untuk amplifikasi DNA, digunakan sepasang primer degenerate untuk BBWV (Kondo et al., 2005) dan satu pasang primer spesifik CymMV (Lee & Chang, 2008) dengan urutan nukletotida yang dapat dilihat pada Tabel 1. cdna yang dihasilkan dari hasil RT, diamplifikasi dengan teknik PCR pada volume 25 µl yang terdiri atas: air bebas nuklease 9,5 µl, PCR mix (Go Green Taq-Promega) 12,5 µl, primer forward 10 µm dan reverse 10 µm, masing masing 1 µl dan DNA templat 1 µl. Setiap komponen reaksi dipipet satu persatu, dimasukkan ke dalam tabung eppendorf berukuran 0,5 µl, kemudian dimasukkan dalam mesin PCR. Program PCR diatur berbeda, tergantung pasangan primer yang digunakan (Tabel 2). Visualisasi DNA. DNA hasil amplifikasi dari PCR diseparasi pada gel agarose 1,5% yang telah ditambah etidium bromida (0,5 µl/10 ml TBE). Sampel dimasukkan ke dalam sumuran gel agarose, kemudian dielektroforesis pada 50 V selama 60 menit. Adanya pita DNA pada gel agarose dilihat di bawah transilluminator ultraviolet dan didokumentasi dengan kamera digital. Analisis Runutan Nukleotida cp BBWV2, CymMV, dan Asam Amino CP BBWV2 dan CymMV Perunutan Nukleotida. Perunutan nukleotida menggunakan mesin sequencer ABI-Prism 3100-Avant Genetic Analyzer di Laboratorium Research and Development Centre PT. Genetika Science. Indonesia Hasil runutan dianalisis menggunakan software Blast (www. NCBI. Nml. Niv.gov) dan software Wu-Blast ( Contiq hasil perunutan DNA dilakukan dengan bantuan program Sequenche r4.8 dan software Complementor ( Selanjutnya, hasil runutan yang sudah diolah, ditranslasi menjadi urutan protein (asam amino), dengan bantuan software Translate ( Analisis Identitas Matriks dan Filogenetika. Runutan nukleotida yang diperoleh dibandingkan dengan data runutan nukleotida yang ada di GenBank. Matriks identitas nukleotida dan asam amino diperoleh dengan menggunakan software BioEdit versi 7.0. Selanjutnya, gambar pensejajaran runutan nukleotida didapatkan dengan menggunakan program GeneDoc versi Pohon filogenetika dikonstruksi dengan menggunakan software MEGA 4.0 (Molecular Evolutionary Genetic Analysis software) (Tamura et al., 2007), dengan metode neighbour-joining menggunakan bootstrap 1000 kali ulangan. HASIL DAN PEMBAHASAN Broad Bean Wilt Virus 2 RT-PCR. Primer yang digunakan yaitu BBWV25 dan BBWV3487M merupakan primer degenerate untuk mengamplifikasi gen coat protein (cp) BBWV baik BBWV1 maupun BBWV2, sehingga produk yang dihasilkan merupakan gen cp BBWV. Pasangan primer ini telah berhasil digunakan untuk mengamplifikasi gen cp BBWV2 dari tanaman Chinese yam (Dioscorea opposita Thunb.) di Ojima, (Kondo et al., 2005). Tabel 1. Primer-primer yang digunakan untuk deteksi virus mosaik nilam No Primer BBWV25 BBW3487M CyCP-F1 CyCP-R1 Urutan basa Ukuran DNA Referensi 2000 pb Kondo et al. ( 2005) 679 pb Lee & Chang (2008) 5 -AATGARRTKGTNCTCAAYTA-3 5 -AMAMAGGTCATGGAACCCA-3. 5-ATGGGAGAGYCCACTCCARCYCCAGC-3' 5'-ATCGCTCGAGTTCAGTAGGGGGTGCAGGCA-3' Tabel 2. Program PCR untuk setiap primer yang digunakan untuk kegiatan PCR No Primer BBWV25 BBW3487M CyCP-F1 CyCP-R1 Program PCR o Referensi o Denaturasi awal pada suhu 95 C ( 5 menit); 35 siklus: 99 C (1 menit), 55 oc (2 menit) dan 72 oc (3 menit); diakhiri dengan 72 oc (5 menit) Denaturasi awal pada suhu 96 oc (5 menit); 30 siklus: 96 oc (30 detik), 52 oc (30 detik) dan 72 oc (30 detik); diakhiri dengan 72 oc (7 menit) Kondo et al. (2005) Lee & Chang (2008)
4 Miftakhurohmah et al. Identifikasi Molekuler BBWV2 dan CYMMV Produk berukuran 2000 pb (pasang basa), berhasil teramplifikasi dari RNA total yang diekstraksi dari daun nilam asal Manoko (Gambar 1). Ukuran pita DNA yang didapatkan sesuai dengan prediksi desain primer yang digunakan, yang menunjukkan terdeteksinya BBWV2 pada sampel daun nilam asal Manoko. Selanjutnya dilakukan perunutan nukleotida terhadap isolat Manoko yang didapatkan. Homologi runutan nukleotida scp dan asam amino CP BBWV2. Dari hasil kegiatan PCR untuk mengamplifikasi keseluruhan gen cp BBWV2, didapatkan pita DNA berukuran 2000 pb. Pada perunutan nukleotida, pembacaan hanya berhasil dilakukan sampai 591 pb (ditranslasikan menjadi 197 asam amino) yang merupakan gen Small Coat Protein (scp). Analisis M 191 homologi dan filogenetika dilakukan menggunakan gen scp. Broad bean wilt virus 2 yang menginfeksi tanaman Yam dibandingkan homologi asam amino bagian LCP dan SCPnya dengan beberapa isolat BBWV2 secara terpisah, dimana homologi asam amino SCP cenderung lebih rendah dibandingkan homologi LCP (Kondo et al., 2005). Penggunaan gen scp juga dilakukan untuk melihat variasi genetik beberapa isolat BBWV2 dari beberapa negara (Ferrer et al., 2011). Runutan nukleotida scp dan asam amino SCP isolat BBWV2 Manoko dibandingkan dengan 8 isolat BBWV2 dari beberapa negara, satu isolat patchouli mild mosaic virus (PatMMV) dari dan sebagai isolat di luar grup, digunakan broad bean wilt virus 1 (BBWV1) (Tabel 3) pb Gambar 1. Hasil visualisasi reverse transcription polymerase chain reaction (RT-PCR) BBWV2 pada gel agarose 1%. M: Penanda DNA 1 kb plus, 1-2: Isolat Manoko Tabel 3. Isolat BBWV2, PatMMV dan BBWV1 dari database GenBank yang digunakan untuk membandingkan homologi gen scp BBWV2 Manoko Spesies Asal isolat Inang/strain Kode aksesi BBWV2 Taiwan Singapura Korsel Spanyol Tomat/Alstroemeria/ Rs Salvia dorisiana/fruit sage Chinese yam/nagaimo Megakepasma erythrochlamys/me Lada/ XJP1 Gentiana triflora/cabai /RP7 Nilam/Cabai/Ben JQ AB EF AB AF HQ AB JX NC_ AY PatMMV BBWV1
5 192 J. HPT Tropika Vol. 15 No. 2, 2015: 188 Hasil analisis homologi runutan nukleotida dan asam amino menunjukkan bahwa gen scp isolat asal Manoko menunjukkan homologi tertinggi sebesar 93,0% dan 93,9% dengan BBWV2 asal Singapura. Sedangkan dengan isolat BBWV2 lain dan PatMMV, homologi berdasarkan runutan nukleotida berkisar antara 78,8 90,0%, dan berdasarkan asam amino berkisar antara 88,8 93,4%. Homologi isolat asal Manoko dengan BBWV1, hanya sebesar 63,6% berdasarkan runutan nukleotida, dan sebesar 58,8% berdasarkan asam amino (Tabel 4). Hasil ini menunjukkan bahwa virus yang ditemukan merupakan salah satu spesies BBWV2. Dalam genus Fabavirus, virus diklasifikasikan ke dalam spesies yang sama bila homologi gen cp lebih dari 75% (Fauquet et al., 2005). Genus Fabavirus nilam di diidentifikasi sebagai PatMMV. PatMMV memiliki kemiripan morfologi partikel, berat molekul CP dan hubungan serologi dengan isolat BBWV dan lamium mild mosaic virus (LMMV). Namun, PatMMV menunjukkan perbedaan kisaran inang dan gejalanya pada Vicia faba dan Nicotiana tabacum, sehingga digolongkan sebagai spesies baru dalam genus Fabavirus (Natsuaki et al., 1994). Genus Fabavirus yang menginfeksi pertanaman nilam di Indonesia, menunjukkan homologi nukleotida dan asam amino lebih tinggi terhadap BBWV2 asal Singapura, dibandingkan dengan PatMMV. Dengan demikian, genus Fabavirus yang menginfeksi tanaman nilam merupakan BBWV2. Selain itu, PatMMV akhirnya juga diklasifikasikan sebagai salah satu strain BBWV2, karena perbedaan gen cp-nya hanya berkisar antara 3 21% dengan BBWV2 (Fauquet et al., 2005). BBWV2 memiliki kisaran inang yang luas, menginfeksi tanaman holtikultura dan hias (Ferrer et al., ), namun belum pernah dilaporkan menginfeksi nilam. Secara serologi BBWV2 terdeteksi menginfeksi nilam (Noveriza et al., 2012). Penelitian ini berhasil mengidentifikasi BBWV2 secara molekuler melalui teknik RT-PCR menggunakan primer dengan target gen cp serta analisis runutan nukleotida dan asam aminonya. Pohon Filogenetika Runutan Nukleotida dan Asam Amino Gen scp BBWV2. Hasil analisis filogenetika berdasarkan runutan nukleotida gen scp menunjukkan terbentuknya dua kelompok/cluster. BBWV2 Manoko berada dalam satu kelompok dengan BBWV2 Singapura (yang menginfeksi Megakepasma erythroclamys/me), (lada) dan Korea Selatan (cabai). Isolat PatMMV (nilam) berada pada kelompok lain dengan BBWV2 Taiwan (S. dorisiana), (Gentiana, yam, Alstroemeria) dan (tomat) (Gambar 2). Hasil analisa filogenetik ini mendukung hasil analisa homologi runutan nukleotida dan asam amino, dimana BBWV2 Manoko memiliki homologi tertinggi dengan BBWV2 Singapura, dan pada pohon filogeni berada dalam satu kelompok. Hasil analisis filogenetika menunjukkan bahwa pengelompokan isolat-isolat BBWV2 tidak berdasarkan asal isolat. Hal ini terlihat pada kedua isolat, berada pada kelompok yang berbeda. Hasil yang sama juga terjadi pada analisis filogenetika isolat-isolat BBWV2 dari beberapa negara dan dari inang yang berbeda berdasarkan gen scp, terlihat bahwa pengelompokkan tidak berdasarkan inang dan asal isolat (Ferrer et al., 2011). Cymbidium Mosaic Virus RT-PCR. Primer yang digunakan untuk mengamplifikasi gen cp CymMV adalah primer Tabel 4. Homologi runutan nukleotida dan asam amino gen scp BBWV2 Manoko dengan beberapa anggota genus Fabavirus Spesies BBWV2 PatMMV BBWV1 Asal isolat Taiwan Singapura Korsel Spanyol Inang/strain Tomat/Alatroemeria/Rs Salvia dorisiana/fruit Sage Megakepasma erythroclamys/me Lada/XJP1 Gentiana triflora/cabai/rp7 Chinese yam/nagaimo Nilam/Cabai/Ben Homologi (%) Nukleotida Asam amino 80,5 91,3 78,8 88,8 80,0 88,0 93,0 94,9 90,0 93,4 80,3 89,3 88,1 92,8 80,7 86,8 79,6 89,8 63,6 58,8
6 Miftakhurohmah et al. Identifikasi Molekuler BBWV2 dan CYMMV degenerate yang disusun dari 3 genom CymMV (AF016914, AY571289, U62963) yang diambil dari GenBank (Lee & Chang, 2008). Ketiga genom CymMV tersebut memiliki homologi yang tinggi dengan isolat CymMV asal Manoko berdasarkan analisa BLAST (Miftakhurohmah et al., 2013). Hasil RT-PCR menunjukkan 2 sampel dari Manoko teramplifikasi pita DNA berukuran 679 pb, yang berukuran sama dengan kontrol positif (CymMV asal anggrek) (Gambar 3). Hasil ini menunjukkan bahwa dua sampel daun nilam asal Manoko yang dideteksi, positif terinfeksi CymMV. 193 Selanjutnya, dilakukan perunutan nukleotida terhadap isolat CymMV asal Manoko yang didapatkan. Homologi Runutan Nukleotida dan Asam Amino Gen cp CymMV. Gen cp CymMV berhasil dirunut berukuran 681 pb, yang ditranslasikan menjadi 227 asam amino, dimana hasil translasi menunjukkan CP penuh. Pensejajaran gen cp CymMV dilakukan dengan membandingkan homologinya dengan 8 isolat CymMV dari beberapa negara, satu isolat CymMV Indonesia, dan sebagai pembanding di luar grup, digunakan satu isolat PVX (Tabel 5). -Tomat 92 -Gentiana 99 -Yam -Alstroemeria Taiwan-S.dorisiana PatMMV-Nilam 99 Indonesia-Nilam Singapura-ME 93 -Lada 99 Korsel-Cabai BBWV1-Cabai Gambar 2. Pohon filogenetika BBWV2 isolat Manoko berdasarkan runutan nukleotida gen scp. Pohon filogenetika dibuat dengan menggunakan software MEGA 4.0, metode neighbour-joining, dengan bootstrap sebanyak 1000 kali. BBWV1 digunakan sebagai pembanding di luar grup M K- K pb Gambar 3. Hasil visualisasi reverse transcription-polymerase chain reaction (RT-PCR) CymMV pada gel agarose 1,5%. M: Penanda DNA 100 pb, K-: kontrol negatif, K+: kontrol positif, 1-2: sampel Manoko
7 194 J. HPT Tropika Vol. 15 No. 2, 2015: grup, seperti halnya isolat-isolat CymMV lain, tingkat kemiripannya rendah, hanya sebesar 35,8% (Tabel 6). CymMV Manoko mengalami mutasi nukleotida pada beberapa titik dibandingkan dengan 9 isolat CymMV dari beberapa negara, termasuk CymMV Indonesia asal Dendrobium. Mutasi pada urutan nukleotida ke-10 dan ke-82 menyebabkan perubahan asam amino pada posisi ke-4, yaitu dari proline menjadi serine, dan ke-28, dari alanine menjadi threonine (Gambar 4). Sedangkan mutasi pada titik yang lain tidak menyebabkan perubahan asam amino. CymMV Manoko memiliki perbedaan nukleotida pada titik ke , serta tambahan 9 nukleotida di akhir runutan gen cp, dibandingkan dengan gen cp CymMV Indonesia dan beberapa CymMV yang lain. Nukleotida TAA yang berada pada posisi , yang mengkode stop kodon, bergeser posisinya ke titik Pada titik , merupakan tambahan 9 Runutan nukleotida gen cp CymMV isolat Manoko terlihat memiliki kemiripan yang tinggi (88,5 96,8%) dengan sembilan isolat CymMV dari beberapa negara. Homologi tertinggi yaitu sebesar 96,8% dengan isolat CymMV dari Korea Selatan (Cymbidium), dan homologi terendah sebesar 88,5% dengan isolat CymMV Thailand (Oncydium). CymMV isolat Manoko memiliki homologi sebesar 95,8% dengan CymMV Indonesia (Dendrobium). Sedangkan dengan PVX sebagai isolat di luar grup, hanya memiliki homologi sebesar 48,6% (Tabel 6). Tingkat homologi yang tinggi dengan isolat-isolat CymMV dari negara lain juga didapatkan dari hasil penghitungan homologi runutan asam amino CP CymMV asal Manoko, dengan kisaran antara 94,6 99,1%. Homologi tertinggi dengan isolat CymMV asal Korea Selatan, sedangkan homologi terendah dengan CymMV Thailand. Sedangkan dengan PVX sebagai isolat di luar Tabel 5. Isolat CymMV dari database GenBank yang digunakan untuk membandingkan homologi gen cp CymMV Manoko Spesies CymMV PVX Asal Isolat Korea Selatan Indonesia Hawai Thailand India Singapura India Inang/Strain Kode Aksesi Cymbidium/CYK9 Vanili/HNXL Dendrobium Dendrobium/2 Oncidium/Cymbidium/GD3 Vanili/Dendrobium/Phaius tancarvilleae Terong AB HQ AB EF AY AY DQ AF AJ AF Tabel 6. Homologi nukleotida dan asam amino gen CP CymMV Manoko dengan beberapa CymMV asal beberapa negara Spesies CymMV PVX Negara Korea Selatan India Indonesia India Thailand Hawai Singapura Inang/Strain Cymbidium/GD3 Cymbidium/CYK9 Phaius tancarvilleae Vanili/HNXL Dendrobium/Vanili/Oncidium/Dendrobium/2 Dendrobium/Terong Homologi (%) Asam Amino Nukleotida 96,1 98,2 96,8 99,1 95,5 96,4 95,8 98,6 95,8 97,7 95,3 97,3 88,5 94,6 89,4 97,7 94,7 96,8 48,6 35,8
8 Miftakhurohmah et al. nukleotida, yang ditranslasikan menjadi asam amino leucine, glutamic acid dan arginine (Gambar 5). Perubahan dan tambahan beberapa asam amino CP CymMV Manoko ini diduga mempengaruhi perbedaan inang CymMV Manoko dan isolat CymMV lain. CymMV dilaporkan hanya menginfeksi tanaman dalam famili Orchidaceae, sedangkan CymMV Manoko menginfeksi tanaman nilam yang tergolong ke dalam famili Lamiaceae. Hal ini terjadi karena gen cp genus Potexvirus selain berperan sebagai pembentuk selubung protein, juga berperan dalam pergerakan virus antar sel (sebagai tambahan), yang mempengaruhi penyebaran virus (Scholthof, 2005). Gen cp CymMV M1 berperan penting dalam perpindahan sel ke sel. Perbedaan empat asam amino pada CP dua strain CymMV asal anggrek Identifikasi Molekuler BBWV2 dan CYMMV 195 menyebabkan CymMV M1 mampu berpindah ke seluruh bagian tanaman tembakau (Nicotiana tabacum) yang menyebabkan gejala sistemik, sedangkan CymMV M2 hanya menyebabkan gejala lokal (Lu et al., 2009). Genus Potexvirus pada nilam di Brazil diidentifikasi sebagai virus baru, yang dinamakan dengan PatVX (Filho et al., 2002). Namun demikian, peneliti dari Brazil tersebut hanya melakukan pembuatan antiserum, uji serologi baik dengan antiserum dan dengan uji protein, tanpa melakukan sekuensing. Dengan demikian, runutan nukleotida dan asam amino isolat CymMV yang didapatkan dari nilam tidak bisa dibandingkan homologinya dengan genom PatVX yang ditemukan di Brazil. Gambar 4. Hasil alignment asam amino antara genom CymMV isolat Manoko dengan nukleotida genom- genom CymMV yang didapatkan dari database GeneBank; keterangan: latar belakang warna hitam menunjukkan kesamaan runutan nukleotida antar isolat, sedangkan warna abu-abu menunjukkan ketidaksamaan. Pensejajaran dilakukan dengan program Bioedit. dilanjutkan dengan program GeneDog Ver (
9 196 J. HPT Tropika Vol. 15 No. 2, 2015:
10 Miftakhurohmah et al. Identifikasi Molekuler BBWV2 dan CYMMV 197 Gambar 5. Hasil alignment nukleotida antara genom CymMV isolat Manoko dengan nukleotida genom-genom CymMV yang didapatkan dari database GeneBank; keterangan: latar belakang warna hitam menunjukkan kesamaan runutan nukleotida antar isolat, sedangkan warna abu-abu menunjukkan ketidaksamaan. Pensejajaran dilakukan dengan program Bioedit. dilanjutkan dengan program GeneDog Ver ( CymMV telah dilaporkan menginfeksi tanaman anggrek di beberapa negara. Selain tanaman anggrek, CymMV juga dilaporkan menginfeksi tanaman vanili (Grisoni et al., 2004). Di Indonesia, CymMV telah dilaporkan menginfeksi tanaman anggrek (Lakani et al., 2010). Namun demikian, infeksi CymMV pada tanaman nilam belum pernah dilaporkan. Dengan demikian, penelitian ini merupakan laporan pertama infeksi CymMV pada tanaman nilam. Pohon Filogenetika Runutan Nukleotida cp dan Asam Amino CP CymMV. Hasil analisis filogenetika runutan nukleotida gen cp membentuk 2 kelompok/ cluster. Isolat Manoko berada dalam satu kelompok dengan CymMV Indonesia (Dendrobium), (Cymbidium), Korea Selatan (Cymbidium), India (Phaius sp.), Thailand (Oncidium) dan Hawai (Dendrobium). Isolat Singapura (Dendrobium) dan India (vanili) membentuk kelompok terpisah (Gambar 6). Hasil analisa homologi asam amino dan nukleotida serta filogenetik menunjukkan bahwa isolat Manoko yang ditemukan merupakan CymMV. Virus diklasifikasikan ke dalam spesies yang sama bila gennya memiliki homologi nukleotida lebih dari 72% atau asam amino lebih dari 80% (Fauquet et al., 2005).
11 198 J. HPT Tropika Vol. 15 No. 2, 2015: Mnk(Ind)-nilam Indonesia-Dendrobium -Cymbidium 65 -Vanili Korsel-Cymbidium India-Phaius sp Thailand-Oncidium 99 Hawai-Dendrobium Singapura-Dendrobium India-Vanili PVX-Terong Gambar 6. Pohon filogenetika CymMV isolat Manoko (Lembang) berdasarkan runutan nukleotida gen cp. Pohon filogenetika dibuat menggunakan software MEGA 4.0, metode neighbour-joining, dengan bootstrap sebanyak 1000 kali. PVX digunakan sebagai pembanding di luar grup SIMPULAN Virus yang berasosiasi dengan gejala mosaik pada tanaman nilam adalah BBWV2 dan CymMV. Hasil analisis homologi dan pohon filogenetika menunjukkan bahwa BBWV2 asal Manoko mengelompok dengan BBWV2 dari Singapura asal tanaman hias Megakepasma erythroclamys/me), asal tanaman lada dan Korea Selatan asal tanaman cabai. Sedangkan CymMV asal Manoko berada dalam satu kelompok dengan CymMV dari Indonesia,, Korea Selatan, India, Thailand, dan Hawai yang berasal dari beberapa jenis anggrek. Isolat CymMV yang ditemukan merupakan laporan pertama teridentifikasi pada nilam di Indonesia. SANWACANA Penulis mengucapkan terima kasih kepada Dr. Irwan Lakani yang telah membantu kegiatan analisis runutan nukleotida gen cp BBWV2 dan CymMV serta asam amino CP BBWV2 dan CymMV. DAFTAR PUSTAKA Badan Karantina Pertanian Basis Data Organisme Pengganggu Tumbuhan Karantina. Badan Karantina Pertanian. Departemen Pertanian Republik Indonesia. Diakses tanggal 14 April Fauquet CM, Mayo MA, Maniloff J, Desselberger U, & Ball LA Virus Taxonomy. Classification and Nomenclature of Viruses. Elsevier Academic Press. New York. Ferrer RM, Ferrior I, Moreno P, Guerri J, & Rubio L Genetic variation and evolutionary analysis of Broad bean wilt virus 2. Arch. Virol. 156(8): Filho PEM, Resende RO, Lima MI, & Kitajima EW Pantchouli virus x, a new potexvirus from Pogostemon clabin. Annu. Appl. Biol. 141: Grisoni M, Davidson F, Hyrondelle C, Farreyrol K, Caruana ML, & Pearson M Nature, incidence and symptomatology of viruses infecting Vanilla tahitensis in French Polysenia. Plant Dis. 88(2): Hall TA BioEdit: a user-friendly biological sequence alignment editor and analysis program for Windows 95/98/NT. Nucleic Acid Symp. Ser. 41: Kondo T, Fuji S, Yamashita K, Kang DK, & Chang MU Broad bean wilt virus 2 in yams. J. Gen. Plant Pathol. 71: Kobayashi YO, Kobayashi A, Hagiwara K, Uga H, Mikoshiba Y, Naito T, Honda Y, & Omura T Gentian mosaic virus: a new spesies in the genus Fabavirus. Phytopathology 95(2):
12 Miftakhurohmah et al. Identifikasi Molekuler BBWV2 dan CYMMV 199 Lakani I, Suastika G, Mattjik N, & Damayanti TA Identification and molecular characterization of Odontoglossum ringspot virus (ORSV) from Bogor, Indonesia. Hayati J. Biosci. 17(2): Noveriza R, Suastika G, Hidayat SH, & Kartosuwondo U Potyvirus associated with mosaic disease on patchouli (Pogostemon cablin (Blanco) Benth.) plants in Indonesia. J. ISSAAS. 18(1): Lee SC & Chang YC Performances and application of antisera produced by recombinant capsid proteins of Cymbidium mosaic virus and Odontoglossum ringspot virus. Eur. J. Plant Pathol. 122: Putnam ML Evaluation of selected methods of plant diagnosis. Crop Prot. 14(6): Scholthof HB Plant virus transport: motions of functional equivalence. Trends Plant Sci. 10(8): Lu HC, Chen CE, Tsai MH, Wang H, Su HJ, & Yeh HH Cymbidium mosaic potexvirus isolate-dependent host movement systems reveal two movement control determinants and the coat protein is the dominant. Virology 388(1): Sukamto, Rahardjo IB, & Sulyo Y Detection of Potyvirus on patchouli plant (Pogostemon cablin BENTH) from Indonesia. Proceeding of International Seminar on Essential Oil. pp Jakarta. 7 9 November Miftakhurohmah, Suastika G, & Damayanti TA Deteksi secara serologi dan PCR beberapa jenis virus yang berasosiasi dengan penyakit mosaik pada tanaman nilam (Pogostemon cablin Benth). J. Littri. 19(3): Sumardiyono YB, Sulandari S, & Hartono S Penyakit mosaik kuning pada nilam (Pogostemon cablin). Risalah Konggres Nasional XII dan Seminar Ilmiah Perhimpunan Fitopatologi Indonesia. pp Yogyakarta. 6-8 September Naidu RA & Hughes JDA Methods for the detection of plant viral diseases of plant viral diseases in plant virology in sub-saharan Africa. Proceedings of Plant Virology. pp Nigeria. pdf_files / pdf. Accessed on 2011 June 16. Natsuaki KT, Tomaru K, Ushiku S, Ichikawa Y, Sugimura Y, Natsuaki T, Okuda S, & Teranaka M Characterization of two viruses isolated from patchouli in Japan. Plant Dis. 78(1): Tamura K, Dudley J, Nei M, & Kumar S MEGA 4: molecular evolutionary genetic analysis (MEGA) software version 4.0. Mol. Biol. Evol. 24(8):
HASIL DAN PEMBAHASAN
 HASIL DAN PEMBAHASAN Deteksi Fabavirus pada Tanaman Nilam Deteksi Fabavirus Melalui Uji Serologi Tanaman nilam dari sampel yang telah dikoleksi dari daerah Cicurug dan Gunung Bunder telah berhasil diuji
HASIL DAN PEMBAHASAN Deteksi Fabavirus pada Tanaman Nilam Deteksi Fabavirus Melalui Uji Serologi Tanaman nilam dari sampel yang telah dikoleksi dari daerah Cicurug dan Gunung Bunder telah berhasil diuji
HASIL DAN PEMBAHASAN
 HASIL DAN PEMBAHASAN Kisaran Inang Potyvirus Isolat Nilam Bogor Tanaman nilam sakit banyak terdapat di daerah Bogor yang memperlihatkan gejala mosaik dengan ciri-ciri hampir sama dengan yang pernah diutarakan
HASIL DAN PEMBAHASAN Kisaran Inang Potyvirus Isolat Nilam Bogor Tanaman nilam sakit banyak terdapat di daerah Bogor yang memperlihatkan gejala mosaik dengan ciri-ciri hampir sama dengan yang pernah diutarakan
IDENTIFIKASI MOLEKULER BROAD BEAN WILT VIRUS 2 (BBWV2) DAN CYMBIDIUM MOSAIC VIRUS (CYMMV) ASAL TANAMAN NILAM (POGOSTEMON CABLIN BENTH.
 J. HPT Tropika. ISSN 1411-7525 188 J. HPT Tropika Vol. 15, No. 2: 188 199, September 2015 Vol. 15 No. 2, 2015: 188-198 IDENTIFIKASI MOLEKULER BROAD BEAN WILT VIRUS 2 (BBWV2) DAN CYMBIDIUM MOSAIC VIRUS
J. HPT Tropika. ISSN 1411-7525 188 J. HPT Tropika Vol. 15, No. 2: 188 199, September 2015 Vol. 15 No. 2, 2015: 188-198 IDENTIFIKASI MOLEKULER BROAD BEAN WILT VIRUS 2 (BBWV2) DAN CYMBIDIUM MOSAIC VIRUS
7 KARAKTER MOLEKULER Chili veinal mottle virus ISOLAT LEMAH (Molecular Characterization of Weak Isolates of Chili veinal mottle virus)
 55 7 AKTER MOLEKULER Chili veinal mottle virus ISOLAT LEMAH (Molecular Characterization of Weak Isolates of Chili veinal mottle virus) Abstrak Pre-imunisasi dengan isolat-isolat lemah Chili veinal mottle
55 7 AKTER MOLEKULER Chili veinal mottle virus ISOLAT LEMAH (Molecular Characterization of Weak Isolates of Chili veinal mottle virus) Abstrak Pre-imunisasi dengan isolat-isolat lemah Chili veinal mottle
DETEKSI SECARA SEROLOGI DAN MOLEKULER BEBERAPA JENIS VIRUS YANG BERASOSIASI DENGAN PENYAKIT MOSAIK TANAMAN NILAM (Pogostemon cablin Benth)
 Jurnal Littri 19(3), September 2013. Hlm. 130 JURNAL - 138 LITTRI VOL. 19 NO. 3, SEPTEMBER 2013 : 130-138 ISSN 0853-8212 DETEKSI SECARA SEROLOGI DAN MOLEKULER BEBERAPA JENIS VIRUS YANG BERASOSIASI DENGAN
Jurnal Littri 19(3), September 2013. Hlm. 130 JURNAL - 138 LITTRI VOL. 19 NO. 3, SEPTEMBER 2013 : 130-138 ISSN 0853-8212 DETEKSI SECARA SEROLOGI DAN MOLEKULER BEBERAPA JENIS VIRUS YANG BERASOSIASI DENGAN
BAHAN DAN METODE. Metode Penelitian
 BAHAN DAN METODE Tempat dan Waktu Penelitian Survei penyakit mosaik dan koleksi sampel tanaman nilam sakit dilakukan di Kebun Percobaan Balai Tanaman Obat dan Aromatik (BALITTRO) di daerah Gunung Bunder
BAHAN DAN METODE Tempat dan Waktu Penelitian Survei penyakit mosaik dan koleksi sampel tanaman nilam sakit dilakukan di Kebun Percobaan Balai Tanaman Obat dan Aromatik (BALITTRO) di daerah Gunung Bunder
BAHAN DAN METODE Tempat dan Waktu Penelitian Bahan dan Alat
 12 BAHAN DAN METODE Tempat dan Waktu Penelitian Survei penyakit klorosis dan koleksi sampel tanaman tomat sakit dilakukan di sentra produksi tomat di daerah Cianjur, Cipanas, Lembang, dan Garut. Deteksi
12 BAHAN DAN METODE Tempat dan Waktu Penelitian Survei penyakit klorosis dan koleksi sampel tanaman tomat sakit dilakukan di sentra produksi tomat di daerah Cianjur, Cipanas, Lembang, dan Garut. Deteksi
MATERI DAN METODE. Lokasi dan Waktu. Materi. Tabel 1. Jumah Sampel Darah Ternak Sapi Indonesia Ternak n Asal Sapi Bali 2 4
 MATERI DAN METODE Lokasi dan Waktu Penelitian dilaksanakan di Laboratorium Genetika Molekuler Ternak, Bagian Pemuliaan dan Genetika Ternak, Fakultas Peternakan, Institut Pertanian Bogor. penelitian ini
MATERI DAN METODE Lokasi dan Waktu Penelitian dilaksanakan di Laboratorium Genetika Molekuler Ternak, Bagian Pemuliaan dan Genetika Ternak, Fakultas Peternakan, Institut Pertanian Bogor. penelitian ini
IDENTIFIKASI DAN DETEKSI MULTIPLEX REVERSE TRANSCRIPTION POLYMERASE CHAIN REACTION
 IDENTIFIKASI DAN DETEKSI MULTIPLEX REVERSE TRANSCRIPTION POLYMERASE CHAIN REACTION VIRUS VIRUS PENYEBAB GEJALA MOSAIK PADA NILAM (Pogostemon cablin BENTH.) MIFTAKHUROHMAH SEKOLAH PASCASARJANA INSTITUT
IDENTIFIKASI DAN DETEKSI MULTIPLEX REVERSE TRANSCRIPTION POLYMERASE CHAIN REACTION VIRUS VIRUS PENYEBAB GEJALA MOSAIK PADA NILAM (Pogostemon cablin BENTH.) MIFTAKHUROHMAH SEKOLAH PASCASARJANA INSTITUT
METODOLOGI PENELITIAN. Tempat dan Waktu Penelitian. Bahan dan Alat Penelitian
 14 METODOLOGI PENELITIAN Tempat dan Waktu Penelitian Tempat penelitian dilakukan di Laboratorium Unit Pelayanan Mikrobiologi Terpadu, Bagian Mikrobiologi Kesehatan, Departemen Ilmu Penyakit Hewan dan Kesehatan
14 METODOLOGI PENELITIAN Tempat dan Waktu Penelitian Tempat penelitian dilakukan di Laboratorium Unit Pelayanan Mikrobiologi Terpadu, Bagian Mikrobiologi Kesehatan, Departemen Ilmu Penyakit Hewan dan Kesehatan
DETEKSI POTYVIRUS PADA NILAM (Pogostemon Cablin (BLANCO) BENTH) DENGAN TEKNIK ELISA DI SULAWESI TENGGARA
 JURNAL AGROTEKNOS Maret 2014 Vol. 4 No. 1. Hal 53-57 ISSN: 2087-7706 DETEKSI POTYVIRUS PADA NILAM (Pogostemon Cablin (BLANCO) BENTH) DENGAN TEKNIK ELISA DI SULAWESI TENGGARA Detection of Potyvirus on Patchouli
JURNAL AGROTEKNOS Maret 2014 Vol. 4 No. 1. Hal 53-57 ISSN: 2087-7706 DETEKSI POTYVIRUS PADA NILAM (Pogostemon Cablin (BLANCO) BENTH) DENGAN TEKNIK ELISA DI SULAWESI TENGGARA Detection of Potyvirus on Patchouli
EFISIENSI PENULARAN VIRUS MOSAIK TANAMAN NILAM (Pogostemon cablin. Benth) MELALUI SERANGGA Myzus persicae
 EFISIENSI PENULARAN VIRUS MOSAIK TANAMAN NILAM (Pogostemon cablin. Benth) MELALUI SERANGGA Myzus persicae NINING TRIANI THAMRIN Program Studi Agroteknologi Fakultas Pertanian Universitas Cokroaminoto Palopo
EFISIENSI PENULARAN VIRUS MOSAIK TANAMAN NILAM (Pogostemon cablin. Benth) MELALUI SERANGGA Myzus persicae NINING TRIANI THAMRIN Program Studi Agroteknologi Fakultas Pertanian Universitas Cokroaminoto Palopo
Identifikasi Carmovirus pada Tanaman Anyelir melalui Teknik Reverse Transcription-Polymerase Chain Reaction dan Analisis Sikuen Nukleotida
 ISSN:0215-7950 Volume 10, Nomor 3, Juni 2014 Halaman 87 92 DOI: 10.14692/jfi.10.3.87 Identifikasi Carmovirus pada Tanaman Anyelir melalui Teknik Reverse Transcription-Polymerase Chain Reaction dan Analisis
ISSN:0215-7950 Volume 10, Nomor 3, Juni 2014 Halaman 87 92 DOI: 10.14692/jfi.10.3.87 Identifikasi Carmovirus pada Tanaman Anyelir melalui Teknik Reverse Transcription-Polymerase Chain Reaction dan Analisis
Jurnal Littri 23(1), Juni Hlm DOI: v23n ISSN e-issn
 Jurnal Littri 23(1), Juni 2017. Hlm. 11-17 DOI: http://dx.doi.org/10.21082/littri. v23n1.2017.11-17 ISSN 0853-8212 e-issn 2528-6870 IDENTIFIKASI MOLEKULER CUCUMBER MOSAIC VIRUS (CMV) ASAL TANAMAN NILAM
Jurnal Littri 23(1), Juni 2017. Hlm. 11-17 DOI: http://dx.doi.org/10.21082/littri. v23n1.2017.11-17 ISSN 0853-8212 e-issn 2528-6870 IDENTIFIKASI MOLEKULER CUCUMBER MOSAIC VIRUS (CMV) ASAL TANAMAN NILAM
MATERI DAN METODE. Kota Padang Sumatera Barat pada bulan Oktober Amplifikasi gen Growth
 III. MATERI DAN METODE 3.1 Waktu dan Tempat Pengambilan sampel darah domba dilakukan di Kecamatan Koto Tengah Kota Padang Sumatera Barat pada bulan Oktober 2012. Amplifikasi gen Growth Hormone menggunakan
III. MATERI DAN METODE 3.1 Waktu dan Tempat Pengambilan sampel darah domba dilakukan di Kecamatan Koto Tengah Kota Padang Sumatera Barat pada bulan Oktober 2012. Amplifikasi gen Growth Hormone menggunakan
Patchouli Viruses: Identification, Biological and Physical Characters, and Control Strategy
 Virus J. nilam: Litbang Identifikasi, Pert. Vol. karakter 32 No. 2 biologi Juni 2013: dan...-... (Miftakhurohmah dan Rita Noveriza) 1 VIRUS NILAM: IDENTIFIKASI, KARAKTER BIOLOGI DAN FISIK, SERTA UPAYA
Virus J. nilam: Litbang Identifikasi, Pert. Vol. karakter 32 No. 2 biologi Juni 2013: dan...-... (Miftakhurohmah dan Rita Noveriza) 1 VIRUS NILAM: IDENTIFIKASI, KARAKTER BIOLOGI DAN FISIK, SERTA UPAYA
TINJAUAN PUSTAKA. Tanaman Nilam (Pogostemon cablin Benth)
 TINJAUAN PUSTAKA Tanaman Nilam (Pogostemon cablin Benth) Nilam (Pogostemon cablin Benth) merupakan bahan baku minyak nilam (patchouli oil) yang merupakan komoditi ekspor terbesar (60%) dari ekspor minyak
TINJAUAN PUSTAKA Tanaman Nilam (Pogostemon cablin Benth) Nilam (Pogostemon cablin Benth) merupakan bahan baku minyak nilam (patchouli oil) yang merupakan komoditi ekspor terbesar (60%) dari ekspor minyak
MATERI DAN METODE. Lokasi dan Waktu. Materi
 MATERI DAN METODE Lokasi dan Waktu Penelitian ini dilaksanakan di Laboratorium Genetika Molekuler, Bagian Pemuliaan dan Genetika Ternak, Departemen Ilmu Produksi dan Teknologi Peternakan, Fakultas Peternakan,
MATERI DAN METODE Lokasi dan Waktu Penelitian ini dilaksanakan di Laboratorium Genetika Molekuler, Bagian Pemuliaan dan Genetika Ternak, Departemen Ilmu Produksi dan Teknologi Peternakan, Fakultas Peternakan,
IDENTIFIKASI SPESIES POTYVIRUS PENYEBAB PENYAKIT MOSAIK PADA TANAMAN CABAI (Capsicum frutescens L.) MELALUI SIKUEN NUKLEOTIDA GEN Coat Protein
 IDENTIFIKASI SPESIES POTYVIRUS PENYEBAB PENYAKIT MOSAIK PADA TANAMAN CABAI (Capsicum frutescens L.) MELALUI SIKUEN NUKLEOTIDA GEN Coat Protein I Gede Rian Pramarta 1, I Gede Rai Maya Temaja 1*), I Dewa
IDENTIFIKASI SPESIES POTYVIRUS PENYEBAB PENYAKIT MOSAIK PADA TANAMAN CABAI (Capsicum frutescens L.) MELALUI SIKUEN NUKLEOTIDA GEN Coat Protein I Gede Rian Pramarta 1, I Gede Rai Maya Temaja 1*), I Dewa
BAB III METODE PENELITIAN. Penelitian ini merupakan penelitian yang dilakukan dengan metode
 16 BAB III METODE PENELITIAN A. Jenis Penelitian Penelitian ini merupakan penelitian yang dilakukan dengan metode deskriptif. Penelitian deskriptif adalah suatu metode penelitian untuk membuat deskripsi,
16 BAB III METODE PENELITIAN A. Jenis Penelitian Penelitian ini merupakan penelitian yang dilakukan dengan metode deskriptif. Penelitian deskriptif adalah suatu metode penelitian untuk membuat deskripsi,
DETEKSI DAN IDENTIFIKASI Pineapple Mealybug Wilt-associated Virus PENYEBAB PENYAKIT LAYU PADA TANAMAN NANAS DI INDONESIA RENO TRYONO
 DETEKSI DAN IDENTIFIKASI Pineapple Mealybug Wilt-associated Virus PENYEBAB PENYAKIT LAYU PADA TANAMAN NANAS DI INDONESIA RENO TRYONO SEKOLAH PASCASARJANA INSTITUT PERTANIAN BOGOR BOGOR 2006 PERNYATAAN
DETEKSI DAN IDENTIFIKASI Pineapple Mealybug Wilt-associated Virus PENYEBAB PENYAKIT LAYU PADA TANAMAN NANAS DI INDONESIA RENO TRYONO SEKOLAH PASCASARJANA INSTITUT PERTANIAN BOGOR BOGOR 2006 PERNYATAAN
DAFTAR ISI Halaman HALAMAN JUDUL... i HALAMAN PENGESAHAN... KATA PENGANTAR... DAFTAR ISI... DAFTAR TABEL... DAFTAR GAMBAR... DAFTAR LAMPIRAN...
 DAFTAR ISI HALAMAN JUDUL... i HALAMAN PENGESAHAN... KATA PENGANTAR...... DAFTAR ISI... DAFTAR TABEL... DAFTAR GAMBAR... DAFTAR LAMPIRAN... INTISARI... ABSTRACT... PENDAHULUAN... 1 A. Latar Belakang...
DAFTAR ISI HALAMAN JUDUL... i HALAMAN PENGESAHAN... KATA PENGANTAR...... DAFTAR ISI... DAFTAR TABEL... DAFTAR GAMBAR... DAFTAR LAMPIRAN... INTISARI... ABSTRACT... PENDAHULUAN... 1 A. Latar Belakang...
HASIL DAN PEMBAHASAN
 HASIL DAN PEMBAHASAN Virus Hepatitis B Gibbon Regio Pre-S1 Amplifikasi Virus Hepatitis B Regio Pre-S1 Hasil amplifikasi dari 9 sampel DNA owa jawa yang telah berstatus serologis positif terhadap antigen
HASIL DAN PEMBAHASAN Virus Hepatitis B Gibbon Regio Pre-S1 Amplifikasi Virus Hepatitis B Regio Pre-S1 Hasil amplifikasi dari 9 sampel DNA owa jawa yang telah berstatus serologis positif terhadap antigen
LAPORAN PRAKTIKUM REKAYASA GENETIKA
 LAPORAN PRAKTIKUM REKAYASA GENETIKA LAPORAN IV (ISOLASI RNA DARI TANAMAN) KHAIRUL ANAM P051090031/BTK BIOTEKNOLOGI SEKOLAH PASCASARJANA INSTITUT PERTANIAN BOGOR 2010 0 ISOLASI RNA DARI TANAMAN TUJUAN Tujuan
LAPORAN PRAKTIKUM REKAYASA GENETIKA LAPORAN IV (ISOLASI RNA DARI TANAMAN) KHAIRUL ANAM P051090031/BTK BIOTEKNOLOGI SEKOLAH PASCASARJANA INSTITUT PERTANIAN BOGOR 2010 0 ISOLASI RNA DARI TANAMAN TUJUAN Tujuan
IDENTIFIKASI SPESIES POTYVIRUS
 TESIS IDENTIFIKASI SPESIES POTYVIRUS YANG BERASOSIASI DENGAN PENYAKIT MOSAIK PADA TANAMAN KACANG PANJANG (Vignasinensis L.) BERDASARKAN SEKUEN NUKLEOTIDA I WAYAN SUKADA PROGRAM PASCASARJANA UNIVERSITAS
TESIS IDENTIFIKASI SPESIES POTYVIRUS YANG BERASOSIASI DENGAN PENYAKIT MOSAIK PADA TANAMAN KACANG PANJANG (Vignasinensis L.) BERDASARKAN SEKUEN NUKLEOTIDA I WAYAN SUKADA PROGRAM PASCASARJANA UNIVERSITAS
TEMUAN PENYAKIT BARU. Tomato yellow leaf curl Kanchanaburi virus Penyebab Penyakit Mosaik Kuning pada Tanaman Terung di Jawa
 ISSN: 2339-2479 Volume 9, Nomor 4, Agustus 2013 Halaman 127-131 DOI: 10.14692/jfi.9.4.127 TEMUAN PENYAKIT BARU Tomato yellow leaf curl Kanchanaburi virus Penyebab Penyakit Mosaik Kuning pada Tanaman Terung
ISSN: 2339-2479 Volume 9, Nomor 4, Agustus 2013 Halaman 127-131 DOI: 10.14692/jfi.9.4.127 TEMUAN PENYAKIT BARU Tomato yellow leaf curl Kanchanaburi virus Penyebab Penyakit Mosaik Kuning pada Tanaman Terung
4.1. Alat dan Bahan Penelitian a. Alat Penelitian. No. URAIAN ALAT. A. Pengambilan sampel
 7 IV. METODE PENELITIAN Ikan Lais diperoleh dari hasil penangkapan ikan oleh nelayan dari sungaisungai di Propinsi Riau yaitu S. Kampar dan S. Indragiri. Identifikasi jenis sampel dilakukan dengan menggunakan
7 IV. METODE PENELITIAN Ikan Lais diperoleh dari hasil penangkapan ikan oleh nelayan dari sungaisungai di Propinsi Riau yaitu S. Kampar dan S. Indragiri. Identifikasi jenis sampel dilakukan dengan menggunakan
BAB I PENDAHULUAN. 1.1 Latar Belakang Kacang panjang (Vigna sinensis L.) merupakan salah satu sayuran yang
 BAB I PENDAHULUAN 1.1 Latar Belakang Kacang panjang (Vigna sinensis L.) merupakan salah satu sayuran yang sering ditemui di pasar tradisional dan merupakan komoditas yang dapat dikembangkan untuk perbaikan
BAB I PENDAHULUAN 1.1 Latar Belakang Kacang panjang (Vigna sinensis L.) merupakan salah satu sayuran yang sering ditemui di pasar tradisional dan merupakan komoditas yang dapat dikembangkan untuk perbaikan
PRAKATA. Alhamdulillah syukur senantiasa penulis panjatkan kepada Allah swt., atas
 PRAKATA Alhamdulillah syukur senantiasa penulis panjatkan kepada Allah swt., atas segala nikmat dan karunia-nya, penulisan Tugas Akhir dengan judul Keragaman Genetik Abalon (Haliotis asinina) Selat Lombok
PRAKATA Alhamdulillah syukur senantiasa penulis panjatkan kepada Allah swt., atas segala nikmat dan karunia-nya, penulisan Tugas Akhir dengan judul Keragaman Genetik Abalon (Haliotis asinina) Selat Lombok
IDENTIFIKASI MOLEKULER VIRUS PENYEBAB PENYAKIT DAUN KUNING PADA TANAMAN MENTIMUN DI KECAMATAN BATURITI KABUPATEN TABANAN
 TESIS IDENTIFIKASI MOLEKULER VIRUS PENYEBAB PENYAKIT DAUN KUNING PADA TANAMAN MENTIMUN DI KECAMATAN BATURITI KABUPATEN TABANAN I DEWA MADE PUTRA WIRATAMA PROGRAM PASCASARJANA UNIVERSITAS UDAYANA DENPASAR
TESIS IDENTIFIKASI MOLEKULER VIRUS PENYEBAB PENYAKIT DAUN KUNING PADA TANAMAN MENTIMUN DI KECAMATAN BATURITI KABUPATEN TABANAN I DEWA MADE PUTRA WIRATAMA PROGRAM PASCASARJANA UNIVERSITAS UDAYANA DENPASAR
BAHAN DAN METODE Tempat dan Waktu Metode Penelitian Pengambilan Sampel Kutukebul dan Tanaman Tomat Sumber TICV
 BAHAN DAN METODE Tempat dan Waktu Kegiatan survei dan pengambilan sampel kutukebul dilakukan di sentra produksi tomat di Kecamatan Cikajang (kabupaten Garut), Kecamatan Pacet (Kabupaten Cianjur), Kecamatan
BAHAN DAN METODE Tempat dan Waktu Kegiatan survei dan pengambilan sampel kutukebul dilakukan di sentra produksi tomat di Kecamatan Cikajang (kabupaten Garut), Kecamatan Pacet (Kabupaten Cianjur), Kecamatan
Departemen Proteksi Tanaman, Fakultas Pertanian, Institut Pertanian Bogor Jl. Kamper, Kampus Dramaga Bogor 16680
 PENGARUH INFEKSI VIRUS MOSAIK TERHADAP PRODUKSI DAN KADAR MINYAK TIGA VARIETAS NILAM Rita Noveriza 1), Gede Suastika 2), Sri Hendrastuti Hidayat 2) dan Utomo Kartosuwondo 2) 1) Balai Penelitian Tanaman
PENGARUH INFEKSI VIRUS MOSAIK TERHADAP PRODUKSI DAN KADAR MINYAK TIGA VARIETAS NILAM Rita Noveriza 1), Gede Suastika 2), Sri Hendrastuti Hidayat 2) dan Utomo Kartosuwondo 2) 1) Balai Penelitian Tanaman
BAB III BAHAN DAN METODE
 9 BAB III BAHAN DAN METODE 3.1 Waktu dan Tempat Penelitian Penelitian dilaksanakan pada bulan September 2011 sampai dengan Juli 2012. Kegiatan ekstraksi DNA sampai PCR-RFLP dilakukan di laboratorium Analisis
9 BAB III BAHAN DAN METODE 3.1 Waktu dan Tempat Penelitian Penelitian dilaksanakan pada bulan September 2011 sampai dengan Juli 2012. Kegiatan ekstraksi DNA sampai PCR-RFLP dilakukan di laboratorium Analisis
BAB III METODE PENELITIAN. Dalam penelitian ini dilakukan lima tahap utama yang meliputi tahap
 BAB III METODE PENELITIAN Dalam penelitian ini dilakukan lima tahap utama yang meliputi tahap penyiapan templat mtdna, amplifikasi fragmen mtdna pada daerah D-loop mtdna manusia dengan teknik PCR, deteksi
BAB III METODE PENELITIAN Dalam penelitian ini dilakukan lima tahap utama yang meliputi tahap penyiapan templat mtdna, amplifikasi fragmen mtdna pada daerah D-loop mtdna manusia dengan teknik PCR, deteksi
KATAPENGANTAR. Pekanbaru, Desember2008. Penulis
 KATAPENGANTAR Fuji syukut ke Hadirat Allah SWT. berkat rahmat dan izin-nya penulis dapat menyelesaikan skripsi yang beijudul "Skrining Bakteri Vibrio sp Penyebab Penyakit Udang Berbasis Teknik Sekuens
KATAPENGANTAR Fuji syukut ke Hadirat Allah SWT. berkat rahmat dan izin-nya penulis dapat menyelesaikan skripsi yang beijudul "Skrining Bakteri Vibrio sp Penyebab Penyakit Udang Berbasis Teknik Sekuens
III. BAHAN DAN METODE
 III. BAHAN DAN METODE Tempat dan Waktu Penelitian dilakukan di Laboratorium BIORIN (Biotechnology Research Indonesian - The Netherlands) Pusat Penelitian Sumberdaya Hayati dan Bioteknologi IPB. Penelitian
III. BAHAN DAN METODE Tempat dan Waktu Penelitian dilakukan di Laboratorium BIORIN (Biotechnology Research Indonesian - The Netherlands) Pusat Penelitian Sumberdaya Hayati dan Bioteknologi IPB. Penelitian
DETEKSI DIFERENSIAL POTYVIRUS DAN FABAVIRUS DENGAN REVERSE TRANSCRIPTION-POLYMERASE CHAIN REACTION (RT-PCR) VISHORA SATYANI
 DETEKSI DIFERENSIAL POTYVIRUS DAN FABAVIRUS DENGAN REVERSE TRANSCRIPTION-POLYMERASE CHAIN REACTION (RT-PCR) VISHORA SATYANI DEPARTEMEN PROTEKSI TANAMAN FAKULTAS PERTANIAN INSTITUT PERTANIAN BOGOR BOGOR
DETEKSI DIFERENSIAL POTYVIRUS DAN FABAVIRUS DENGAN REVERSE TRANSCRIPTION-POLYMERASE CHAIN REACTION (RT-PCR) VISHORA SATYANI DEPARTEMEN PROTEKSI TANAMAN FAKULTAS PERTANIAN INSTITUT PERTANIAN BOGOR BOGOR
TEMUAN PENYAKIT BARU. Penyakit Mosaik pada Koro Pedang. Mosaic Disease on Jack Bean
 ISSN: 0215-7950 Volume 11, Nomor 1, Februari 2015 Halaman 29 35 DOI: 10.14692/jfi.11.1.29 TEMUAN PENYAKIT BARU Penyakit Mosaik pada Koro Pedang Mosaic Disease on Jack Bean Tri Asmira * Institut Pertanian
ISSN: 0215-7950 Volume 11, Nomor 1, Februari 2015 Halaman 29 35 DOI: 10.14692/jfi.11.1.29 TEMUAN PENYAKIT BARU Penyakit Mosaik pada Koro Pedang Mosaic Disease on Jack Bean Tri Asmira * Institut Pertanian
BAB III. METODOLOGI PENELITIAN. Pengambilan sampel. Penyiapan templat mtdna dengan metode lisis sel
 16 BAB III. METODOLOGI PENELITIAN Bab ini menggambarkan tahapan penelitian yang terdiri dari pengambilan sampel, penyiapan templat mtdna dengan metode lisis sel, amplifikasi D-loop mtdna dengan teknik
16 BAB III. METODOLOGI PENELITIAN Bab ini menggambarkan tahapan penelitian yang terdiri dari pengambilan sampel, penyiapan templat mtdna dengan metode lisis sel, amplifikasi D-loop mtdna dengan teknik
PERBANDINGAN METODE EKSTRAKSI REAL TIME PCR VIRUS INFLUENZA A ANTARA METODE GUANIDIUM,-THIOCYANATE-PHENOL- CHLOROFORM DAN METODE SPIN KOLOM
 PERBANDINGAN METODE EKSTRAKSI REAL TIME PCR VIRUS INFLUENZA A ANTARA METODE GUANIDIUM,-THIOCYANATE-PHENOL- CHLOROFORM DAN METODE SPIN KOLOM YUNI YUPIANA Balai Besar Pengujian Mutu dan Sertifikasi Obat
PERBANDINGAN METODE EKSTRAKSI REAL TIME PCR VIRUS INFLUENZA A ANTARA METODE GUANIDIUM,-THIOCYANATE-PHENOL- CHLOROFORM DAN METODE SPIN KOLOM YUNI YUPIANA Balai Besar Pengujian Mutu dan Sertifikasi Obat
Penelitian akan dilaksanakan pada bulan Februari-Agustus 2010 di Laboratorium Zoologi Departemen Biologi, FMIPA, IPB.
 Kolokium Ajeng Ajeng Siti Fatimah, Achmad Farajallah dan Arif Wibowo. 2009. Karakterisasi Genom Mitokondria Gen 12SrRNA - COIII pada Ikan Belida Batik Anggota Famili Notopteridae. Kolokium disampaikan
Kolokium Ajeng Ajeng Siti Fatimah, Achmad Farajallah dan Arif Wibowo. 2009. Karakterisasi Genom Mitokondria Gen 12SrRNA - COIII pada Ikan Belida Batik Anggota Famili Notopteridae. Kolokium disampaikan
PEPPER VEIN YELLOW VIRUS (PeVYV) PENYEBAB PENYAKIT KUNING (YELLOWING) PADA TANAMAN MENTIMUN DI DAERAH BALI
 TESIS PEPPER VEIN YELLOW VIRUS (PeVYV) PENYEBAB PENYAKIT KUNING (YELLOWING) PADA TANAMAN MENTIMUN DI DAERAH BALI M. TINNY LESTARININGSIH. T PROGRAM PASCASARJANA UNIVERSITAS UDAYANA DENPASAR 2016 TESIS
TESIS PEPPER VEIN YELLOW VIRUS (PeVYV) PENYEBAB PENYAKIT KUNING (YELLOWING) PADA TANAMAN MENTIMUN DI DAERAH BALI M. TINNY LESTARININGSIH. T PROGRAM PASCASARJANA UNIVERSITAS UDAYANA DENPASAR 2016 TESIS
BAB XII. REAKSI POLIMERISASI BERANTAI
 BAB XII. REAKSI POLIMERISASI BERANTAI Di dalam Bab XII ini akan dibahas pengertian dan kegunaan teknik Reaksi Polimerisasi Berantai atau Polymerase Chain Reaction (PCR) serta komponen-komponen dan tahapan
BAB XII. REAKSI POLIMERISASI BERANTAI Di dalam Bab XII ini akan dibahas pengertian dan kegunaan teknik Reaksi Polimerisasi Berantai atau Polymerase Chain Reaction (PCR) serta komponen-komponen dan tahapan
HASIL DAN PEMBAHASAN
 HASIL DAN PEMBAHASAN Metode deteksi yang dilakukan untuk mengetahui keberadaan Potyvirus dan Fabavirus di pertanaman nilam yaitu dengan DAS-ELISA untuk mendeteksi Fabavirus, I-ELISA untuk mendeteksi Potyvirus
HASIL DAN PEMBAHASAN Metode deteksi yang dilakukan untuk mengetahui keberadaan Potyvirus dan Fabavirus di pertanaman nilam yaitu dengan DAS-ELISA untuk mendeteksi Fabavirus, I-ELISA untuk mendeteksi Potyvirus
BAHAN DAN METODE. Tahapan Analisis DNA S. incertulas
 11 BAHAN DAN METODE Waktu dan Tempat Penelitian Penelitian ini dilaksanakan pada bulan Juli 2010 sampai dengan Mei 2011. Koleksi sampel dilakukan pada beberapa lokasi di Jawa Tengah, Daerah Istimewa Yogyakarta
11 BAHAN DAN METODE Waktu dan Tempat Penelitian Penelitian ini dilaksanakan pada bulan Juli 2010 sampai dengan Mei 2011. Koleksi sampel dilakukan pada beberapa lokasi di Jawa Tengah, Daerah Istimewa Yogyakarta
III. METODE PENELITIAN
 III. METODE PENELITIAN 3.1 Waktu dan Tempat Penelitian Penelitian ini dilaksanakan mulai bulan November 2007 hingga Juli 2009, bertempat di Laboratorium Reproduksi dan Genetika Organisme Akuatik Departemen
III. METODE PENELITIAN 3.1 Waktu dan Tempat Penelitian Penelitian ini dilaksanakan mulai bulan November 2007 hingga Juli 2009, bertempat di Laboratorium Reproduksi dan Genetika Organisme Akuatik Departemen
BAB III METODOLOGI PENELITIAN. Pada penelitian ini terdapat lima tahapan penelitian yang dilakukan yaitu
 BAB III METODOLOGI PENELITIAN Pada penelitian ini terdapat lima tahapan penelitian yang dilakukan yaitu pengumpulan sampel berupa akar rambut, ekstraksi mtdna melalui proses lisis akar rambut, amplifikasi
BAB III METODOLOGI PENELITIAN Pada penelitian ini terdapat lima tahapan penelitian yang dilakukan yaitu pengumpulan sampel berupa akar rambut, ekstraksi mtdna melalui proses lisis akar rambut, amplifikasi
BAHAN DAN METODE Waktu dan Tempat Bahan dan Alat
 12 BAHAN DAN METODE Waktu dan Tempat Penelitian ini dilakukan dari bulan April 2006 sampai dengan bulan April 2007. Penelitian dilakukan di rumah kaca, laboratorium Biologi Molekuler Seluler Tanaman, dan
12 BAHAN DAN METODE Waktu dan Tempat Penelitian ini dilakukan dari bulan April 2006 sampai dengan bulan April 2007. Penelitian dilakukan di rumah kaca, laboratorium Biologi Molekuler Seluler Tanaman, dan
BAB III METODE PENELITIAN
 BAB III METODE PENELITIAN A. Jenis Penelitian deskriptif. Jenis penelitian yang digunakan adalah penelitian dasar dengan metode B. Objek Penelitian Objek penelitian ini adalah sampel DNA koleksi hasil
BAB III METODE PENELITIAN A. Jenis Penelitian deskriptif. Jenis penelitian yang digunakan adalah penelitian dasar dengan metode B. Objek Penelitian Objek penelitian ini adalah sampel DNA koleksi hasil
3 METODOLOGI 3.1 Waktu dan Tempat 3.2 Bahan dan Alat
 3 METODOLOGI 3.1 Waktu dan Tempat Penelitian Autentikasi Bahan Baku Ikan Tuna (Thunnus sp.) dalam Rangka Peningkatan Keamanan Pangan dengan Metode Berbasis DNA dilaksanakan pada bulan Januari sampai dengan
3 METODOLOGI 3.1 Waktu dan Tempat Penelitian Autentikasi Bahan Baku Ikan Tuna (Thunnus sp.) dalam Rangka Peningkatan Keamanan Pangan dengan Metode Berbasis DNA dilaksanakan pada bulan Januari sampai dengan
3 METODE. Tempat dan Waktu
 13 3 METODE Tempat dan Waktu Penelitian terdiri atas dua kegiatan utama, yaitu (1) survei kejadian penyakit di lapangan dan (2) deteksi virus dan identifikasi kutukebul. Kegiatan pertama dilakukan di areal
13 3 METODE Tempat dan Waktu Penelitian terdiri atas dua kegiatan utama, yaitu (1) survei kejadian penyakit di lapangan dan (2) deteksi virus dan identifikasi kutukebul. Kegiatan pertama dilakukan di areal
II. BAHAN DAN METODE
 II. BAHAN DAN METODE 2.1. Waktu dan Lokasi Penelitian Penelitian ini dilaksanakan dari bulan Agustus sampai September tahun 2011. Sampel ikan berasal dari 3 lokasi yaitu Jawa (Jawa Barat), Sumatera (Jambi),
II. BAHAN DAN METODE 2.1. Waktu dan Lokasi Penelitian Penelitian ini dilaksanakan dari bulan Agustus sampai September tahun 2011. Sampel ikan berasal dari 3 lokasi yaitu Jawa (Jawa Barat), Sumatera (Jambi),
BAB IV HASIL DAN PEMBAHASAN. Deteksi genom virus avian influenza pada penelitian dilakukan
 30 BAB IV HASIL DAN PEMBAHASAN A. KONDISI OPTIMAL REAKSI AMPLIFIKASI Deteksi genom virus avian influenza pada penelitian dilakukan menggunakan primer NA. Primer NA dipilih karena protein neuraminidase,
30 BAB IV HASIL DAN PEMBAHASAN A. KONDISI OPTIMAL REAKSI AMPLIFIKASI Deteksi genom virus avian influenza pada penelitian dilakukan menggunakan primer NA. Primer NA dipilih karena protein neuraminidase,
FAKULTAS BIOLOGI LABORATORIUM GENETIKA & PEMULIAAN INSTRUKSI KERJA UJI
 ISOLASI TOTAL DNA TUMBUHAN DENGAN KIT EKSTRAKSI DNA PHYTOPURE Halaman : 1 dari 5 1. RUANG LINGKUP Metode ini digunakan untuk mengisolasi DNA dari sampel jaringan tumbuhan, dapat dari daun, akar, batang,
ISOLASI TOTAL DNA TUMBUHAN DENGAN KIT EKSTRAKSI DNA PHYTOPURE Halaman : 1 dari 5 1. RUANG LINGKUP Metode ini digunakan untuk mengisolasi DNA dari sampel jaringan tumbuhan, dapat dari daun, akar, batang,
BAHAN DAN METODE. Analisis Kekerabatan Rayap Tanah M. gilvus dengan Pendekatan Perilaku
 BAHAN DAN METODE Tempat dan Waktu Sampel rayap diambil dari Cagar Alam Yanlappa-Jasinga dan Kampus IPB- Dramaga, Bogor. Rayap diidentifikasi dan diuji perilaku agonistiknya di Laboratorium Biosistematika
BAHAN DAN METODE Tempat dan Waktu Sampel rayap diambil dari Cagar Alam Yanlappa-Jasinga dan Kampus IPB- Dramaga, Bogor. Rayap diidentifikasi dan diuji perilaku agonistiknya di Laboratorium Biosistematika
BAB III METODE PENELITIAN. Penelitian ini merupakan penelitian eksperimental dengan 7 sampel dari 7
 BAB III METODE PENELITIAN 3.1 Rancangan Penelitian Penelitian ini merupakan penelitian eksperimental dengan 7 sampel dari 7 individu udang Jari yang diambil dari Segara Anakan Kabupaten Cilacap Jawa Tengah.
BAB III METODE PENELITIAN 3.1 Rancangan Penelitian Penelitian ini merupakan penelitian eksperimental dengan 7 sampel dari 7 individu udang Jari yang diambil dari Segara Anakan Kabupaten Cilacap Jawa Tengah.
DETEKSI DAN IDENTIFIKASI Cymbidium Mosaik Virus (CyMV) PADA TANAMAN ANGGREK FITRI MENISA
 DETEKSI DAN IDENTIFIKASI Cymbidium Mosaik Virus (CyMV) PADA TANAMAN ANGGREK FITRI MENISA DEPARTEMEN PROTEKSI TANAMAN FAKULTAS PERTANIAN INSTITUT PERTANIAN BOGOR 2009 ABSTRAK FITRI MENISA. Deteksi dan Identifikasi
DETEKSI DAN IDENTIFIKASI Cymbidium Mosaik Virus (CyMV) PADA TANAMAN ANGGREK FITRI MENISA DEPARTEMEN PROTEKSI TANAMAN FAKULTAS PERTANIAN INSTITUT PERTANIAN BOGOR 2009 ABSTRAK FITRI MENISA. Deteksi dan Identifikasi
BAB III BAHAN DAN CARA KERJA. Penelitian dilakukan di Laboratorium Institute of Human Virology and
 23 BAB III BAHAN DAN CARA KERJA A. LOKASI DAN WAKTU PENELITIAN Penelitian dilakukan di Laboratorium Institute of Human Virology and Cancer Biology of the University of Indonesia (IHVCB-UI), Jl. Salemba
23 BAB III BAHAN DAN CARA KERJA A. LOKASI DAN WAKTU PENELITIAN Penelitian dilakukan di Laboratorium Institute of Human Virology and Cancer Biology of the University of Indonesia (IHVCB-UI), Jl. Salemba
Pengaruh Infeksi Beberapa Jenis Virus terhadap Penurunan Hasil pada Tanaman Cabai Rawit (Capsicum frutescens L.)
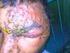 Pengaruh Infeksi Beberapa Jenis Virus terhadap Penurunan Hasil pada Tanaman Cabai Rawit (Capsicum frutescens L.) I WAYAN SUKADA I MADE SUDANA I DEWA NYOMAN NYANA *) GEDE SUASTIKA KETUT SIADI 1 1 Program
Pengaruh Infeksi Beberapa Jenis Virus terhadap Penurunan Hasil pada Tanaman Cabai Rawit (Capsicum frutescens L.) I WAYAN SUKADA I MADE SUDANA I DEWA NYOMAN NYANA *) GEDE SUASTIKA KETUT SIADI 1 1 Program
3. METODE PENELITIAN
 29 3. METODE PENELITIAN 3.1. Lokasi dan Waktu Penelitian Lokasi penelitian meliputi Laut Sulawesi, Selat Makassar, Teluk Bone, Laut Flores, Laut Banda, Teluk Tolo, Laut Maluku dan Teluk Tomini (Gambar
29 3. METODE PENELITIAN 3.1. Lokasi dan Waktu Penelitian Lokasi penelitian meliputi Laut Sulawesi, Selat Makassar, Teluk Bone, Laut Flores, Laut Banda, Teluk Tolo, Laut Maluku dan Teluk Tomini (Gambar
BAB III METODE PENELITIAN
 BAB III METODE PENELITIAN A. Jenis penelitian Jenis penelitian ini adalah penelitian deskriptif yang mengangkat fenomena alam sebagai salah satu masalah dalam penelitian, sehingga dapat menerangkan arti
BAB III METODE PENELITIAN A. Jenis penelitian Jenis penelitian ini adalah penelitian deskriptif yang mengangkat fenomena alam sebagai salah satu masalah dalam penelitian, sehingga dapat menerangkan arti
IDENTIFIKASI Telosma mosaic virus PENYEBAB PENYAKIT MOSAIK PADA TANAMAN NILAM (Pogostemon cablin Benth.) RITA KURNIA APINDIATI
 IDENTIFIKASI Telosma mosaic virus PENYEBAB PENYAKIT MOSAIK PADA TANAMAN NILAM (Pogostemon cablin Benth.) RITA KURNIA APINDIATI DEPARTEMEN PROTEKSI TANAMAN FAKULTAS PERTANIAN INSTITUT PERTANIAN BOGOR BOGOR
IDENTIFIKASI Telosma mosaic virus PENYEBAB PENYAKIT MOSAIK PADA TANAMAN NILAM (Pogostemon cablin Benth.) RITA KURNIA APINDIATI DEPARTEMEN PROTEKSI TANAMAN FAKULTAS PERTANIAN INSTITUT PERTANIAN BOGOR BOGOR
AMPLIFIKASI GEN CYTOCHROME OXIDASE SUBUNIT I (COI) DARI SAMPEL SIRIP IKAN HIU DENGAN MENGGUNAKAN BEBERAPA PASANGAN PRIMER
 AMPLIFIKASI GEN CYTOCHROME OXIDASE SUBUNIT I (COI) DARI SAMPEL SIRIP IKAN HIU DENGAN MENGGUNAKAN BEBERAPA PASANGAN PRIMER (Amplification of Cytochrome Oxidase Subunit I (COI) Gene from Shark Fin Samples
AMPLIFIKASI GEN CYTOCHROME OXIDASE SUBUNIT I (COI) DARI SAMPEL SIRIP IKAN HIU DENGAN MENGGUNAKAN BEBERAPA PASANGAN PRIMER (Amplification of Cytochrome Oxidase Subunit I (COI) Gene from Shark Fin Samples
II. BAHAN DAN METODE. Betina BEST BB NB RB. Nirwana BN NN RN. Red NIFI BR NR RR
 II. BAHAN DAN METODE Ikan Uji Ikan uji yang digunakan adalah ikan nila hibrida hasil persilangan resiprok 3 strain BEST, Nirwana dan Red NIFI koleksi Balai Riset Perikanan Budidaya Air Tawar Sempur, Bogor.
II. BAHAN DAN METODE Ikan Uji Ikan uji yang digunakan adalah ikan nila hibrida hasil persilangan resiprok 3 strain BEST, Nirwana dan Red NIFI koleksi Balai Riset Perikanan Budidaya Air Tawar Sempur, Bogor.
BAB III METODE PENELITIAN
 39 BAB III METODE PENELITIAN A. Desain Penelitian Penelitian yang dilakukan merupakan penelitian deskriptif. Penelitian membuat deskripsi secara sistematis, faktual dan akurat mengenai fakta-fakta dan
39 BAB III METODE PENELITIAN A. Desain Penelitian Penelitian yang dilakukan merupakan penelitian deskriptif. Penelitian membuat deskripsi secara sistematis, faktual dan akurat mengenai fakta-fakta dan
BAB III METODE PENELITIAN
 BAB III METODE PENELITIAN A. Jenis Penelitian Jenis penelitian yang dilakukan adalah penelitian deskriptif. Penelitian deskriptif adalah penelitian yang mendeskripsikan suatu gambaran yang sistematis dengan
BAB III METODE PENELITIAN A. Jenis Penelitian Jenis penelitian yang dilakukan adalah penelitian deskriptif. Penelitian deskriptif adalah penelitian yang mendeskripsikan suatu gambaran yang sistematis dengan
BAB IV METODE PENELITIAN. Ruang lingkup dari penelitian ini meliputi bidang ilmu sitogenetika.
 BAB IV METODE PENELITIAN 4.1 Ruang lingkup penelitian Ruang lingkup dari penelitian ini meliputi bidang ilmu sitogenetika. 4.2 Tempat dan waktu penelitian Penelitian ini dilaksanakan di Pusat Riset Biomedik
BAB IV METODE PENELITIAN 4.1 Ruang lingkup penelitian Ruang lingkup dari penelitian ini meliputi bidang ilmu sitogenetika. 4.2 Tempat dan waktu penelitian Penelitian ini dilaksanakan di Pusat Riset Biomedik
BAB III METODOLOGI PENELITIAN. Penelitian akan diawali dengan preparasi alat dan bahan untuk sampling
 16 BAB III METODOLOGI PENELITIAN Penelitian akan diawali dengan preparasi alat dan bahan untuk sampling sel folikel akar rambut. Sampel kemudian dilisis, diamplifikasi dan disekuensing dengan metode dideoksi
16 BAB III METODOLOGI PENELITIAN Penelitian akan diawali dengan preparasi alat dan bahan untuk sampling sel folikel akar rambut. Sampel kemudian dilisis, diamplifikasi dan disekuensing dengan metode dideoksi
BAB III METODE PENELITIAN. Secara garis besar langkah-langkah yang dilakukan dalam penelitian ini
 BAB III METODE PENELITIAN Secara garis besar langkah-langkah yang dilakukan dalam penelitian ini adalah: pengumpulan sampel; lisis terhadap sampel mtdna yang telah diperoleh; amplifikasi daerah D-loop
BAB III METODE PENELITIAN Secara garis besar langkah-langkah yang dilakukan dalam penelitian ini adalah: pengumpulan sampel; lisis terhadap sampel mtdna yang telah diperoleh; amplifikasi daerah D-loop
BAB I PENDAHULUAN. Penggunaan mikroorganisme antagonis sebagai agen pengendali hayati
 BAB I PENDAHULUAN A. Latar Belakang Penggunaan mikroorganisme antagonis sebagai agen pengendali hayati memberikan harapan baru untuk pengendalian hama pertanian terutama fungi yang bersifat patogen. Secara
BAB I PENDAHULUAN A. Latar Belakang Penggunaan mikroorganisme antagonis sebagai agen pengendali hayati memberikan harapan baru untuk pengendalian hama pertanian terutama fungi yang bersifat patogen. Secara
Dr. Tri Asmira Damayanti (Institut Pertanian Bogor ) Dr. Giyanto (Institut Pertanian Bogor )
 Dr. Tri Asmira Damayanti (Institut Pertanian Bogor ) Dr. Giyanto (Institut Pertanian Bogor ) Ir. Lilik Koesmihartono Putra, M.AgSt (Pusat Penelitian dan Pengembangan Gula Indonesia) Tahun-3 1. Konstruksi
Dr. Tri Asmira Damayanti (Institut Pertanian Bogor ) Dr. Giyanto (Institut Pertanian Bogor ) Ir. Lilik Koesmihartono Putra, M.AgSt (Pusat Penelitian dan Pengembangan Gula Indonesia) Tahun-3 1. Konstruksi
Deteksi Molekuler Cucumber Mosaic Virus (Cmv) pada Tanaman Gamal (Gliricidia Sepium) Sebagai Barier pada Pertanaman Cabai
 Deteksi Molekuler Cucumber Mosaic Virus (Cmv) pada Tanaman Gamal (Gliricidia Sepium) Sebagai Barier pada Pertanaman Cabai IDA BAGUS GDE PRANATAYANA I GEDE RAI MAYA TEMAJA*) KETUT AYU YULIADHI 1 I DEWA
Deteksi Molekuler Cucumber Mosaic Virus (Cmv) pada Tanaman Gamal (Gliricidia Sepium) Sebagai Barier pada Pertanaman Cabai IDA BAGUS GDE PRANATAYANA I GEDE RAI MAYA TEMAJA*) KETUT AYU YULIADHI 1 I DEWA
IDENTIFIKASI MOLEKULER BEAN COMMON MOSAIC VIRUS YANG BERASOSIASI DENGAN PENYAKIT MOSAIK KUNING KACANG PANJANG
 J. HPT Tropika. ISSN 1411-7525 132 J. HPT Tropika Vol. 15 No. 2, 2015: 132-140 Vol. 15, No. 2: 132 140, September 2015 IDENTIFIKASI MOLEKULER BEAN COMMON MOSAIC VIRUS YANG BERASOSIASI DENGAN PENYAKIT MOSAIK
J. HPT Tropika. ISSN 1411-7525 132 J. HPT Tropika Vol. 15 No. 2, 2015: 132-140 Vol. 15, No. 2: 132 140, September 2015 IDENTIFIKASI MOLEKULER BEAN COMMON MOSAIC VIRUS YANG BERASOSIASI DENGAN PENYAKIT MOSAIK
PENYEBAB PENYAKIT KERDIL PADA TANAMAN LADA SECARA
 DETEKSI Piper yellow mottle virus (PYMoV) PENYEBAB PENYAKIT KERDIL PADA TANAMAN LADA SECARA Polymerase Chain Reaction (PCR) Detection of piper yellow mottle virus (PYMoV), the cause of dwarf disease on
DETEKSI Piper yellow mottle virus (PYMoV) PENYEBAB PENYAKIT KERDIL PADA TANAMAN LADA SECARA Polymerase Chain Reaction (PCR) Detection of piper yellow mottle virus (PYMoV), the cause of dwarf disease on
IDENTIFIKASI SPESIES POLEROVIRUS PENYEBAB PENYAKIT KLOROSIS PADA TANAMAN CABAI MELALUI SEKUEN NUKLEOTIDA TITIN RAHAYUNINGSIH
 1 IDENTIFIKASI SPESIES POLEROVIRUS PENYEBAB PENYAKIT KLOROSIS PADA TANAMAN CABAI MELALUI SEKUEN NUKLEOTIDA TITIN RAHAYUNINGSIH DEPARTEMEN PROTEKSI TANAMAN FAKULTAS PERTANIAN INSTITUT PERTANIAN BOGOR BOGOR
1 IDENTIFIKASI SPESIES POLEROVIRUS PENYEBAB PENYAKIT KLOROSIS PADA TANAMAN CABAI MELALUI SEKUEN NUKLEOTIDA TITIN RAHAYUNINGSIH DEPARTEMEN PROTEKSI TANAMAN FAKULTAS PERTANIAN INSTITUT PERTANIAN BOGOR BOGOR
BAB III METODE PENELITIAN
 BAB III METODE PENELITIAN A. Jenis Penelitian Jenis penelitian ini adalah penelitian deskriptif yang mengangkat fenomena alam sebagai salah satu masalah dalam penelitian. Penelitian ini dapat menerangkan
BAB III METODE PENELITIAN A. Jenis Penelitian Jenis penelitian ini adalah penelitian deskriptif yang mengangkat fenomena alam sebagai salah satu masalah dalam penelitian. Penelitian ini dapat menerangkan
IDENTIFIKASI SPESIES BEGOMOVIRUS
 TESIS IDENTIFIKASI SPESIES BEGOMOVIRUS YANG BERASOSIASI DENGAN PENYAKIT KUNING PADA TANAMAN KACANG PANJANG (Vigna sinensis L.) BERDASARKAN SEKUEN GEN TRAP DAN REP I GEDE PUTU DARMAWAN PROGRAM PASCASARJANA
TESIS IDENTIFIKASI SPESIES BEGOMOVIRUS YANG BERASOSIASI DENGAN PENYAKIT KUNING PADA TANAMAN KACANG PANJANG (Vigna sinensis L.) BERDASARKAN SEKUEN GEN TRAP DAN REP I GEDE PUTU DARMAWAN PROGRAM PASCASARJANA
BAB III METODE PENELITIAN. amplifikasi daerah HVI mtdna sampel dengan menggunakan teknik PCR;
 BAB III METODE PENELITIAN Secara garis besar, langkah-langkah yang dilakukan dalam penelitian ini adalah: pengumpulan sampel; lisis terhadap sampel mtdna yang telah diperoleh; amplifikasi daerah HVI mtdna
BAB III METODE PENELITIAN Secara garis besar, langkah-langkah yang dilakukan dalam penelitian ini adalah: pengumpulan sampel; lisis terhadap sampel mtdna yang telah diperoleh; amplifikasi daerah HVI mtdna
BIOMA, Juni 2014 ISSN: Vol. 16, No. 1, Hal
 BIOMA, Juni 2014 ISSN: 1410-8801 Vol. 16, No. 1, Hal. 18-25 Karakterisasi Genetik Fragmen Gen Penyandi RNA Polimerase Infectious Myonecrosis Virus (IMNV) yang Menginfeksi Udang Vannamei (Litopenaeus vannamei
BIOMA, Juni 2014 ISSN: 1410-8801 Vol. 16, No. 1, Hal. 18-25 Karakterisasi Genetik Fragmen Gen Penyandi RNA Polimerase Infectious Myonecrosis Virus (IMNV) yang Menginfeksi Udang Vannamei (Litopenaeus vannamei
DETEKSI Pepper vein yellow virus (PeVYV) PENYEBAB PENYAKIT DAUN MERAH PADA TANAMAN WORTEL DI JAWA BARAT IKA ELY SUSANTI
 i DETEKSI Pepper vein yellow virus (PeVYV) PENYEBAB PENYAKIT DAUN MERAH PADA TANAMAN WORTEL DI JAWA BARAT IKA ELY SUSANTI DEPARTEMEN PROTEKSI TANAMAN FAKULTAS PERTANIAN INSTITUT PERTANIAN BOGOR BOGOR 2014
i DETEKSI Pepper vein yellow virus (PeVYV) PENYEBAB PENYAKIT DAUN MERAH PADA TANAMAN WORTEL DI JAWA BARAT IKA ELY SUSANTI DEPARTEMEN PROTEKSI TANAMAN FAKULTAS PERTANIAN INSTITUT PERTANIAN BOGOR BOGOR 2014
DIAGRAM FILOGENIK HASIL SEKUENS BASA DNA MENGGUNAKAN PROGRAM MEGA-7 (MOLECULAR EVOLUTIONARY GENETICS ANALYSIS)
 DIAGRAM FILOGENIK HASIL SEKUENS BASA DNA MENGGUNAKAN PROGRAM MEGA-7 (MOLECULAR EVOLUTIONARY GENETICS ANALYSIS) Harumi Yuniarti* ), Bambang Cholis S* ), Astri Rinanti** ) *) Jurusan Teknik Industri, Fakultas
DIAGRAM FILOGENIK HASIL SEKUENS BASA DNA MENGGUNAKAN PROGRAM MEGA-7 (MOLECULAR EVOLUTIONARY GENETICS ANALYSIS) Harumi Yuniarti* ), Bambang Cholis S* ), Astri Rinanti** ) *) Jurusan Teknik Industri, Fakultas
BAB III METODE PENELITIAN Bagan Alir Penelitian ini secara umum dapat digambarkan pada skema berikut:
 BAB III METODE PENELITIAN Tahapan-tahapan yang dilakukan dalam penelitian ini adalah: pengumpulan sampel, lisis terhadap sampel mtdna yang telah diperoleh, amplifikasi daerah HVI mtdna sampel dengan menggunakan
BAB III METODE PENELITIAN Tahapan-tahapan yang dilakukan dalam penelitian ini adalah: pengumpulan sampel, lisis terhadap sampel mtdna yang telah diperoleh, amplifikasi daerah HVI mtdna sampel dengan menggunakan
UJI KISARAN INANG POTYVIRUS PENYEBAB MOSAIK NILAM (Pogostemon cablin (Blanco) Benth) ASAL SULAWESI TENGGARA
 JURNAL AGROTEKNOS Nopember 2014 Vol. 4 No. 3. Hal 194-201 ISSN: 2087-7706 UJI KISARAN INANG POTYVIRUS PENYEBAB MOSAIK NILAM (Pogostemon cablin (Blanco) Benth) ASAL SULAWESI TENGGARA Host Range Test of
JURNAL AGROTEKNOS Nopember 2014 Vol. 4 No. 3. Hal 194-201 ISSN: 2087-7706 UJI KISARAN INANG POTYVIRUS PENYEBAB MOSAIK NILAM (Pogostemon cablin (Blanco) Benth) ASAL SULAWESI TENGGARA Host Range Test of
DAFTAR ISI. Halaman ABSTRAK... i ABSTRACT... ii DAFTAR ISI... iii DAFTAR GAMBAR... vi DAFTAR TABEL... vii DAFTAR LAMPIRAN... viii
 DAFTAR ISI ABSTRAK... i ABSTRACT... ii DAFTAR ISI... iii DAFTAR GAMBAR... vi DAFTAR TABEL... vii DAFTAR LAMPIRAN... viii BAB I PENDAHULUAN... 1 A. Latar Belakang Penelitian... 1 B. Rumusan Masalah Penelitian...
DAFTAR ISI ABSTRAK... i ABSTRACT... ii DAFTAR ISI... iii DAFTAR GAMBAR... vi DAFTAR TABEL... vii DAFTAR LAMPIRAN... viii BAB I PENDAHULUAN... 1 A. Latar Belakang Penelitian... 1 B. Rumusan Masalah Penelitian...
BIO306. Prinsip Bioteknologi
 BIO306 Prinsip Bioteknologi KULIAH 7. PUSTAKA GENOM DAN ANALISIS JENIS DNA Konstruksi Pustaka DNA Pustaka gen merupakan sumber utama isolasi gen spesifik atau fragmen gen. Koleksi klon rekombinan dari
BIO306 Prinsip Bioteknologi KULIAH 7. PUSTAKA GENOM DAN ANALISIS JENIS DNA Konstruksi Pustaka DNA Pustaka gen merupakan sumber utama isolasi gen spesifik atau fragmen gen. Koleksi klon rekombinan dari
FAKULTAS BIOLOGI LABORATORIUM GENETIKA & PEMULIAAN INSTRUKSI KERJA UJI
 Halaman : 1 dari 5 ISOLASI TOTAL DNA HEWAN DENGAN KIT EKSTRAKSI DNA 1. RUANG LINGKUP Metode ini digunakan untuk mengisolasi DNA dari sampel jaringan hewan, dapat dari insang, otot, darah atau jaringan
Halaman : 1 dari 5 ISOLASI TOTAL DNA HEWAN DENGAN KIT EKSTRAKSI DNA 1. RUANG LINGKUP Metode ini digunakan untuk mengisolasi DNA dari sampel jaringan hewan, dapat dari insang, otot, darah atau jaringan
BAHAN DAN METODE Tempat dan Waktu Bahan dan Alat Metode Penelitian Isolasi Aktinomiset
 BAHAN DAN METODE Tempat dan Waktu Penelitian dilaksanakan di Laboratorium Bakteriologi Tumbuhan, Departemen Proteksi Tanaman, Fakultas Pertanian, Institut Pertanian Bogor, dari bulan Februari sampai dengan
BAHAN DAN METODE Tempat dan Waktu Penelitian dilaksanakan di Laboratorium Bakteriologi Tumbuhan, Departemen Proteksi Tanaman, Fakultas Pertanian, Institut Pertanian Bogor, dari bulan Februari sampai dengan
HASIL DAN PEMBAHASAN. DNA Genom
 IV. HASIL DAN PEMBAHASAN A. Isolasi DNA Metode isolasi dilakukan untuk memisahkan DNA dari komponen sel yang lain (Ilhak dan Arslan, 2007). Metode isolasi ini sesuai dengan protokol yang diberikan oleh
IV. HASIL DAN PEMBAHASAN A. Isolasi DNA Metode isolasi dilakukan untuk memisahkan DNA dari komponen sel yang lain (Ilhak dan Arslan, 2007). Metode isolasi ini sesuai dengan protokol yang diberikan oleh
BAB 4. METODE PENELITIAN
 BAB 4. METODE PENELITIAN Penelitian penanda genetik spesifik dilakukan terhadap jenis-jenis ikan endemik sungai paparan banjir Riau yaitu dari Genus Kryptopterus dan Ompok. Penelitian ini bertujuan untuk
BAB 4. METODE PENELITIAN Penelitian penanda genetik spesifik dilakukan terhadap jenis-jenis ikan endemik sungai paparan banjir Riau yaitu dari Genus Kryptopterus dan Ompok. Penelitian ini bertujuan untuk
2015 ISOLASI DNA PARSIAL GEN
 1 BAB I PENDAHULUAN A. Latar Belakang Penelitian Ikan gurame (Osphronemus merupakan salah satu ikan air tawar yang termasuk ke dalam infraclass Teleostei (Integrated Taxonomic Information System, 2012).
1 BAB I PENDAHULUAN A. Latar Belakang Penelitian Ikan gurame (Osphronemus merupakan salah satu ikan air tawar yang termasuk ke dalam infraclass Teleostei (Integrated Taxonomic Information System, 2012).
BAB III METODE PENELITIAN
 BAB III METODE PENELITIAN A. Jenis Penelitian Jenis penelitian yang digunakan adalah penelitian dasar dengan metode deskriptif (Nazir, 1983). B. Populasi dan Sampel Populasi dalam penelitian ini adalah
BAB III METODE PENELITIAN A. Jenis Penelitian Jenis penelitian yang digunakan adalah penelitian dasar dengan metode deskriptif (Nazir, 1983). B. Populasi dan Sampel Populasi dalam penelitian ini adalah
I. PENDAHULUAN. Iridoviridae yang banyak mendapatkan perhatian karena telah menyebabkan
 I. PENDAHULUAN 1.1 Latar Belakang Megalocytivirus merupakan salah satu genus terbaru dalam famili Iridoviridae yang banyak mendapatkan perhatian karena telah menyebabkan kerugian ekonomi serta kerugian
I. PENDAHULUAN 1.1 Latar Belakang Megalocytivirus merupakan salah satu genus terbaru dalam famili Iridoviridae yang banyak mendapatkan perhatian karena telah menyebabkan kerugian ekonomi serta kerugian
III. IDENTIFIKASI DAN KARAKTERISASI BEBERAPA VIRUS YANG MENGINFEKSI TANAMAN ANGGREK DI PULAU JAWA
 41 III. IDENTIFIKASI DAN KARAKTERISASI BEBERAPA VIRUS YANG MENGINFEKSI TANAMAN ANGGREK DI PULAU JAWA ABSTRAK IRWAN LAKANI. Identifikasi dan Karakterisasi Beberapa Virus yang Menginfeksi Tanaman Anggrek
41 III. IDENTIFIKASI DAN KARAKTERISASI BEBERAPA VIRUS YANG MENGINFEKSI TANAMAN ANGGREK DI PULAU JAWA ABSTRAK IRWAN LAKANI. Identifikasi dan Karakterisasi Beberapa Virus yang Menginfeksi Tanaman Anggrek
4 HASIL DAN PEMBAHASAN
 4 HASIL DAN PEMBAHASAN 4.1 Karakteristik Morfologi Pada penelitian ini digunakan lima sampel koloni karang yang diambil dari tiga lokasi berbeda di sekitar perairan Kepulauan Seribu yaitu di P. Pramuka
4 HASIL DAN PEMBAHASAN 4.1 Karakteristik Morfologi Pada penelitian ini digunakan lima sampel koloni karang yang diambil dari tiga lokasi berbeda di sekitar perairan Kepulauan Seribu yaitu di P. Pramuka
MATERI DAN METODE. Materi
 MATERI DAN METODE Lokasi dan Waktu Penelitian dilaksanakan di Laboratorium Genetika Molekuler Ternak, Departemen Ilmu Produksi dan Teknologi Peternakan, Fakultas Peternakan IPB dan Laboratorium Terpadu,
MATERI DAN METODE Lokasi dan Waktu Penelitian dilaksanakan di Laboratorium Genetika Molekuler Ternak, Departemen Ilmu Produksi dan Teknologi Peternakan, Fakultas Peternakan IPB dan Laboratorium Terpadu,
HASIL DAN PEMBAHASAN TICV Isolat Indonesia
 23 HASIL DAN PEMBAHASAN TICV Isolat Indonesia Penyakit klorosis saat ini sudah ditemukan di Indonesia. Pertama kali ditemukan di sentra pertanaman tomat di Magelang, Jawa Tengah dan Purwakarta, Jawa Barat
23 HASIL DAN PEMBAHASAN TICV Isolat Indonesia Penyakit klorosis saat ini sudah ditemukan di Indonesia. Pertama kali ditemukan di sentra pertanaman tomat di Magelang, Jawa Tengah dan Purwakarta, Jawa Barat
DETEKSI DAN IDENTIFIKASI PENYEBAB PENYAKIT BELANG (MOTTLE) PADA TANAMAN LADA (Piper nigrum L.) DI INDONESIA IRWAN LAKANI
 DETEKSI DAN IDENTIFIKASI PENYEBAB PENYAKIT BELANG (MOTTLE) PADA TANAMAN LADA (Piper nigrum L.) DI INDONESIA IRWAN LAKANI SEKOLAH PASCASARJANA INSTITUT PERTANIAN BOGOR BOGOR 2006 ii ABSTRAK IRWAN LAKANI.
DETEKSI DAN IDENTIFIKASI PENYEBAB PENYAKIT BELANG (MOTTLE) PADA TANAMAN LADA (Piper nigrum L.) DI INDONESIA IRWAN LAKANI SEKOLAH PASCASARJANA INSTITUT PERTANIAN BOGOR BOGOR 2006 ii ABSTRAK IRWAN LAKANI.
HASIL DAN PEMBAHASAN
 HASIL DAN PEMBAHASAN Amplifikasi ini membutuhkan primer spesifik (sekuen oligonukelotida khusus) untuk daerah tersebut. Primer biasanya terdiri dari 10-20 nukleotida dan dirancang berdasarkan daerah konservatif
HASIL DAN PEMBAHASAN Amplifikasi ini membutuhkan primer spesifik (sekuen oligonukelotida khusus) untuk daerah tersebut. Primer biasanya terdiri dari 10-20 nukleotida dan dirancang berdasarkan daerah konservatif
IDENTIFIKASI SPESIES POLEROVIRUS PADA TANAMAN WORTEL MELALUI ANALISIS SEKUEN NUKLEOTIDA GEN COAT PROTEIN INA RUBIATUL HASANAH
 IDENTIFIKASI SPESIES POLEROVIRUS PADA TANAMAN WORTEL MELALUI ANALISIS SEKUEN NUKLEOTIDA GEN COAT PROTEIN INA RUBIATUL HASANAH DEPARTEMEN PROTEKSI TANAMAN FAKULTAS PERTANIAN INSTITUT PERTANIAN BOGOR BOGOR
IDENTIFIKASI SPESIES POLEROVIRUS PADA TANAMAN WORTEL MELALUI ANALISIS SEKUEN NUKLEOTIDA GEN COAT PROTEIN INA RUBIATUL HASANAH DEPARTEMEN PROTEKSI TANAMAN FAKULTAS PERTANIAN INSTITUT PERTANIAN BOGOR BOGOR
TUGAS TERSTRUKTUR PENGELOLAAN ORGANISME PENGGANGGU TANAMAN TERPADU
 TUGAS TERSTRUKTUR PENGELOLAAN ORGANISME PENGGANGGU TANAMAN TERPADU PROSES INFEKSI DAN GEJALA SERANGAN TOBACCO MOZAIC VIRUS PADA TANAMAN TEMBAKAU Oleh: Gregorius Widodo Adhi Prasetyo A2A015009 KEMENTERIAN
TUGAS TERSTRUKTUR PENGELOLAAN ORGANISME PENGGANGGU TANAMAN TERPADU PROSES INFEKSI DAN GEJALA SERANGAN TOBACCO MOZAIC VIRUS PADA TANAMAN TEMBAKAU Oleh: Gregorius Widodo Adhi Prasetyo A2A015009 KEMENTERIAN
