Desain Primer PCR Secara Manual untuk Amplifikasi Gen dtx Bakteri Penyebab Difteri dengan Masalah Homologi Sekuens DNA
|
|
|
- Yenny Kartawijaya
- 5 tahun lalu
- Tontonan:
Transkripsi
1 Artikel Penelitian Desain Primer PCR Secara Manual untuk Amplifikasi Gen dtx Bakteri Penyebab Difteri dengan Masalah Homologi Sekuens DNA Sunarno, 1 Harly Novriani 2 1 Puslitbang Biomedis dan Teknologi Dasar Kesehatan, Badan Litbangkes, Jakarta 2 Puslitbang Sumber Daya dan Pelayanan Kesehatan, Badan Litbangkes, Jakarta Abstrak Pendahuluan Salah satu faktor yang menentukan keberhasilan pemeriksaan polymerase chain reaction (PCR) adalah ketepatan susunan primer PCR yang digunakan. Beberapa software dapat digunakan untuk merancang primer PCR secara cepat sesuai dengan kebutuhan.namun, untuk beberapa kasus seperti adanya masalah homologi sekuens DNA gen target dapat menjadi kendala tersendiri dalam desain primer. Salah satu gen yang memiliki masalah homologi sekuens DNA adalah gen dtxatau tox yang merupakan penanda toksigenisitas bakteri penyebab difteri. Penelitian ini bertujuan untuk mendapatkan susunan primer PCR yang tepat dalam identifikasi toksigenisitas bakteri penyebab difteri dengan PCR konvensional, termasuk membedakan strain non-toxigenic tox gene bearing (NTTB) dari strain toksigenik. Metode Primer PCR didesain secara manual berdasarkan data sekuens DNA gen dtx dan pseudogene bakteri penyebab difteri yang terdaftar di GeneBank atau dipubliksasi dalam jurnalilmiah.sebanyak 26 sekuens gen dtx dan 10 pseudogen di-align menggunakan program BioEdit. Penilaian terhadap daerah yang berpotensi sebagai tempat penempelan primer dilakukan satu per satu. Kandidat primer yang diperoleh diuji dengan program PerlPrimer untuk memprediksi kendala yang akan muncul. Hasil Analisis secara in silicomenunjukkan bahwa ada 3 pasang primer PCR yang dapat digunakan untuk membedakan strain NTTB dari strain toksigenik,begitu juga strain non-toksigenikdari strain toksigenik maupun NTTB. Ketiga pasang primer PCR tersebut diprediksi dapat diaplikasikan dalam sebuah reaksi PCR multipleks. Strain NTTB akan menghasilkan 2 pita penanda, masing-masing 174 bp dan 517 bp atau 539 bp. Strain toksigenik akan menghasilkan 1 pita 174 bp sebagai penanda. Semntara itu, pada strain nontoksigenik tidak tampak adanya pita 174 bp, 517 bp maupun 539 bp. Kesimpulan Dengan demikian dapat disimpulkan bahwa primer baru untuk PCR konvensional yang berhasil didesain dalam penelitian ini, secara Bioinformatika dapat digunakan untuk identifikasi toksigenisitas bakteri penyebab difteri, termasuk membedakan strain NTTB dari strain toksigenik. Kata Kunci primer PCR, toksigenisitas, gen tox, difteri Korespondensi Sunarno no_nar@yahoo.com 544
2 Manually PCR Primer Designto Amplify thedtx Gene of the Bacteria Causing Diphtheria with DNA Sequences Homology Problem Sunarno, 1 Harly Novriani 2 1 The Biomedical and Basic Health Tecnology, Health Research and Development Centre, Jakarta 2 Resource Center and Balitbangkes Health Services, Jakarta Abstract Introduction PCR primer sequences determine the successfulness of polymerase chain reaction (PCR). Some software could be used for design of proper PCR primer sequences.nevertheless, the PCR primer design occasionally complicated by the sequences homology problem of target gene. The dtxor tox gene that encoding diphtheria toxin synthesis is an example of thegene with DNA sequences homology problem. This study targeted to get proper PCR primer for identification of bacterial toxigenicity by conventional PCR, included non-toxigenic tox gene bearing (NTTB) and toxigenic strains differentiation. Methods The PCR primer designed manually based on the sequences data of dtxgene and pseudogene of the bacteria causing diphtheria registered in GeneBank or the other scientific publishing. Twenty six sequences of dtxgene and 10 sequences of pseudogen alignedby BioEdit program. PCR primer candidate tested in silico by PerlPrimer program to predict the primerapplication onthe PCR processing. Result The study showed that 3 pairs of PCR primer could to distinguish NTTB strain from toxigenic strain as well as non-toxsigenic strain distinguish from toxigenicand NTTB strains. The 3 pairs of PCR primer were predicted could beapplied on the conventional multiplex PCR. NTTB strain marked by 2 bands (174 bp and 517 bp or 539 bp), whiletoxigenicstrain marked by 1 band (174 bp). In other hand, non-toxigenicstrain marked by no band on 174 bp, 517 bp, or 539 bp. Conclusions The study was success to design 3 pairs of PCR primer for conventional multiplex PCR application that could be used to identify the toxigenicity (toxigenic, non-toxigenic, and NTTB differentiation) of bacteria causing diphtheria properly. Keywords PCR primer, toxigenicity, tox gene, diphtheria Pendahuluan Sejak dikembangkan oleh Kary Banks Mullis tahun 1985, Polymerase Chain Reactin (PCR) telah menunjukkan peranan yang sangat besar dalam perkembanganilmu pengetahuan, khususnya Biologi Molekular. Saat ini, pemeriksaan PCR menjadi bagian yang tidak terpisahkan dari kegiatan rutin di laboratorium pelayanan maupun penelitian kesehatan. Serangkaian kelebihan yang dimiliki membuatnya menjadi pilihan utama atau alternatif pemeriksaan untuk diagnostik penyakit maupun tujuan lainnya. PCR cenderung banyak dipilih karena relatif lebih mudah dan cepat dengan sensitifitas dan spesifitaspemeriksaan yang sangat tinggi. 1,2 Salah satu faktor yang menentukan keberhasilan pemeriksaan PCR adalah ketepatan susunan primer PCR yang digunakan karena akan menentukan sensitifitas dan spesifisitas pemeriksaan. Primer PCR atau dikenal sebagai oligomer merupakan sepasang potongan pendek DNA untai tunggal (biasanya bp), terdiri dari forward primer (F) dan reverse primer (R)yang digunakan untuk inisiasi terjadinya proses amplifikasi DNA template pada proses PCR. Selain untuk inisiasi, primer PCRjuga digunakan untuk membatasi proses amplifikasi sehingga bisa ditentukan seberapa panjang produk PCR (amplikon) yang dihasilkan. Dengan demikian, setelah dilakukan elektroforesis, hasil amplifikasi dapat dibaca dengan benar. Untuk dapat mencapai tujuan tersebut maka sekuens primer PCR harus spesifik dan terletak pada daerah lestari (tidak ada mutasi) atau conserve sehingga tidak terjadi mismatch dan unmatch. Hibridisasi dan amplifikasi harus terjadi pada semua variasi sekuens DNA gen target dan sebaliknya tidak boleh terjadi hibridisasi dan amplifikasi pada tempat yang tidak diinginkan (bukan gen target). 3,4 Primer PCR dapat didesain menggunakan bantuan program komputer, baik online maupun offline, misalnya Primer BLAST, IDT, PerlPrimer, Primer3 dan lain sebainya. Primer PCR juga bisa didesain secara manual dengan tetap memperhatikan beberapa ketentuan yang berlaku. Penggunaan program komputer dapat mempermudah kita dalam merancang 545
3 primer secara cepat sesuai dengan kebutuhan, misalnya GC Clamp, Tm, panjang primer, panjang produk dan lain sebagainya. Akan tetapi, untuk beberapa kasus seperti pada gen dengan karakteristik khusus, misalnya homologi sekuens DNA yang sangat tinggi antar atau interspesies dan variasisekuens yang sangat tinggi intraspesies (target)menjadi hambatan tersendiri. Dalam hal ini, desain primer PCR secara manual bisa menjadi pilihan, kendatipada umumnya tetap membutuhkan bantuan program komputer untuk analisis lebih lanjut. 5,6,7,8 Salah satu gen yang memiliki karakteristik khusus adalah gen tox/dtx, penyandi sintesis toksin difteri padabakteri penyebab difteri (potentially toxigenic Corynebacteria), meliputi C.diphtheriae, C.ulcerans dan C.pseudotuberculosis.Gen dtx dikatakan spesial karena memiliki sekuens DNA yang sangat bervariasidiantara ketiganya, meskipun sama-sama mengkode sintesis toksin difteridan dapat menimbulkan gejala penyakit yang serupa. 9,10 Selain itu, gen dtx memiliki kemiripan sekuens DNA dengan pseudogene (gen dtxpada strain non-toxigenic tox gene bearing atau NTTB) yang terbukti tidak mampu mengkode sintesis toksin difteri, sebagaimana dikemukakan oleh Hall, et.al dan Zakikhany, et al. 11,12 Dalam hal ini, PCR untuk pemeriksaan difteri biasanya tetap akan mendeteksi pseudogene tersebut sebagai gen dtx sehingga akan ada perbedaan hasil antara pemeriksaan PCR yang berbasis genotip dan metode konvensional yang berbasis fenotip. 13 Penelitian ini bertujuan untukmendapatkan susunan primer PCR yang tepat dalam pemeriksaan toksigenisitas bakteri penyebab difteri dengan PCR konvensional. Primer PCR tersebut diharapkan dapat digunakan untuk membedakan gen dtxatau tox dari pseudogene strain NTTB.Hal ini perlu dilakukan untuk meminimalisasi perbedaan hasil PCR dengan metode konvensional sebagai gold standard. Metode Penelitian Ada 3 pasang primer PCR (3 forward dan 2 reverse)yang didesain pada penelitian ini untuk identifikasi toksigenisitas bakteri penyebab difteri secara detil. Sepasang primer digunakan untuk deteksi gen dtx atau tox (baik true maupun pseudogene )seperti halnya primer PCR yang sudah digunakan selama ini Dua pasang primer yang lain digunakan untuk membedakan gen dtx dari pseudogene. Primer PCR didesain secara manual berdasarkan data sekuens DNA gen dtxdan pseudogene C.diphtheriae, C.ulcerans, dan C.pseudotuberculosis yang terdaftar di GeneBank ( dan beberapa literatur lainnya. 11,12 Seluruh data yang dibutuhkan diunduh melalui jaringan internet. Alignment sekueans DNA dilakukan menggunakan program BioEdit. 18 Daerah spesifik untuk pseudogene (beda dengan gen dtx) diamati satu per satu agar dapat mendesain primer spesifik yang membedakannya dari gen dtx. Setelah ditemukan lokasi yang dapat digunakan untuk tempat penempelan primer, dilakukan desain kandidat primer PCR dengan menentukan panjang sekuens primer, panjang amplikon dan mengubah salah satu primer dengan sekuens reverse transcript. Kandidat pasangan primer yang diperoleh diuji dengan program perlprimer untuk menghitung besarnya ikatan primer dimer, adanya run, Tm primer dan lain sebagainya. 19 Hal yang sama dilakukan dalam desain primer untuk deteksi gen dtx secara umum. Pada akhirnya didapatkan 3 pasang primer PCR (3 forward dan 2 reverse) untuk menentukan apakah bakteri yang diperiksa bersifat nontoksigenik (tidak memiliki gen dtxdan tidak menghasilkan toksin), toksigenik (memiliki gen dtx dan menghasilkan toksin), atau NTTB (memiliki gen dtx tapi tidak menghasilkan toksin). Hasil Penelitian Sebanyak 26 sekuens gen dtx dan 10 sekuens pseudogene bakteri penyebab difteri yang terdaftar di GenBank maupun terpublikasi dalam jurnal berhasil dikumpulkan. Berdasarkan analisis sekuens DNA gen dtx dan pseudogene (data tidak ditampilkan), ada beberapa mutasi (substitusi dan delesi) basa nukleotida pada pseudogene. Mutasi-mutasi tersebut dapat dimanfaatkan sebagai referensi untuk mendesain primer PCR yang dapat membedakan gen dtx dari pseudogene dengan cara deteksi gen dtx tanpa pseudogene atau sebaliknya. Ada2 delesi yang ditemukan pada pseudogene, masing-masing basa ke-25 dan ke-55. Delesi basa ke-25 terlihat pada 4 dari 10 sekuens pseudogene,sementara delesi basa ke-55terlihat pada 6yang lain dari 10 sekuens pseudogene yang dianalisis. Mutasi berupa substitusi terlihat pada basa ke-60 (2 sekuens), ke-432 (1 sekuens), ke-651 (4 sekuens), ke-937 (4 sekuens), dan basa ke-1206 (4 sekuens). Diantara tempat yang sudah didapatkan tersebut, hanya delesi basa ke-25 dan ke-55 yang paling memungkinkan untuk membedakan seluruh pseudogene dari gen dtx. Berdasarkan kenyataan ini, basa ke-25 dan ke-55 dipilih untuk dijadikan target penempelan ujung 3 primer PCR. Permasalahan selanjutnya muncul karena jarak keduanya sangat dekat sehingga sulit untuk mendapatkan sepasang primer (forward dan reverse) dari kedua daerah tersebut. Selain itu, di sekitar lokasi basa tersebut tidak didapatkan daerah yang 100% lestari (conserve). Upaya yang paling memungkinkan untuk mendapatkan pasangan primer PCR adalah menggunakan skema 2 forward primer dan 1 reverse primer dengan panjang amplikon sedikit berbeda. Perbedaan panjang amplikon sekitar 30 bp dari 2 forward yang berbeda tersebut disamarkan dengan mendesain reverse primer yang terletak cukup jauh sehingga menghasilkan amplikon >500 bp. Perbedaan panjang amplikon 30 bp akan samar pada visualisasi hasil PCR di gel agarose.dalam hal ini, kelestarian sekuens tidak dijadikan prioritas pertama, dengan catatan masih bisa ditoleransi. 546
4 Kandidat pasang primer PCR yang diperoleh adalah sebagai berikut F1pseudo 5 -GCAGAAA(A G)CTGTTTGCGTCAT-3 F2pseudo 5 - GCGCTACTG(G T)GGATAGGGC-3 Rpseudo 5 -CTTAACGCTTTCGCCTGTTCC-3 Pada sekuens gen dtx, ketiga primer tersebut barada pada posisi basa ke-5 sampai dengan basa ke-25 untuk F1pseudo, basa ke-37 sampai dengan basa ke-55 untuk F2pseudo serta basa ke-554 sampai dengan basa ke-534 untuk Rpseudo. Panjang amplikon yang terbentuk adalah 517 bp dan 539 bp. Dua pasang kandidat primer yang terdiri dari 3 buah tersebut diuji menggunakan software PerlPrimeruntuk memprediksi masalah yang akan timbul jika diaplikasikan pada pemeriksaan. Ringkasan hasil analisis primer pseudogene dapat dilihat pada Tabel 1yang menunjukkan bahwa 2 pasangan primer pseudogene cukup baik sebagai kandidat primer PCR, meskipun salah satu GC content primer 63%(sebaiknya 40 % - 60 %). GC clampterdapatpada 5 basa ujung 3, panjang primer antara bp, Tm antara 55 oc 65 oc, panjang produk PCR 517 bp dan 539 bp yang akan samar bila diseparasi dengan gel elektroforesis. Selain itu, ikatan primer-dimer tertinggi adalah 5,27 kcal/mol. Ikatan tersebut tidak termasuk jenis 3 extensible sehingga diharapkan tidak mempengaruhi proses amplifikasi. Selain itu,beberapa literatur juga menyebutkan bahwa ikatan atau delta G sampai -7 kcal/mol, bahkan sampai -9 kcal/mol masih bisa dipakai untuk menjalankan sebuah reaksi PCR.20,21 Tabel 1. Ringkasan Hasil Analisis Primer pseudogene dengan Pearl Primer Forward 1 Forward 2 Reverse Panjang Produk Ikatan Primer dimer Run> 4 Repeats> 3 21 basa GC 47 % Tm 62,83 oc 19 basa GC 63 % Tm 62,99 oc 21 basa GC 52% Tm 62,61 oc 539 bp dan 517 bp Extensible primer-dimers tertinggi kcal/mol Non-extensible primer-dimers tertinggi kcal/mol Tidak ditemukan Tidak ditemukan Setelah primer untuk membedakan gen tox dan pseudogene diperoleh, desain primer PCR dilanjutkan untuk deteksi gen dtx secara keseluruhan. Dalam hal ini termasuk pseudogene yang akan dideteksi karena titik perbedaan kedua gen telah digunakan pada desain primer sebelumnya. Desain primer yang kedua ini bertujuan untuk membedakan antara strain non-toksigenik dengan strain toksigenik maupun NTTB. Alignment sekuens DNA gen dtx dan pseudogene sebagaimana terlihat pada Gambar 1 menunjukkan bahwa sangat sulit mendapatkan daerah yang 100% lestari diantara 3 spesies bakteri penyebab difteri. Gambar 1. Analisis Pasang Primer dtx dengan PerlPrimer Beberapa daerah lestari yang cukup panjang untuk tempat penempelan primer, seperti basa ke-757 sampai dengan ke784 dan basa ke-1141 sampai ke-1169 tidak memenuhi syarat sebagai tempat penempelan kandidat primer PCR yang baik. Hal ini dikarenakan pada daerah tersebut terdapat run dan GC content sangat rendah. Dua daerah yang pada akhirnya dipilih sebagai tempat penempelan kandidat primer adalah basa ke-1263 sampai dengan ke-1287 untuk forward primer dan basa ke-1436 sampai dengan basa ke-1410 untuk reverse primerdengan panjang amplikon 174 bp. Pada daerah tersebut terdapat mutasi (substitusi) basa, namun masih dapat ditoleransi. 547
5 Sekuens kandidat primer untuk deteksi gen dtx dan pseudogene secara keseluruhan adalah sebagai berikut Fdtx 5 -CAGTTGGAACACTGTTGAAGATTCG-3 Rdtx 5 -CCATTTACGGAAATATGAGTCTTGGAC-3 Gambaran analisis pasang primer dtx dengan software PerlPrimer dapat dilihat pada Gambar 1. Pada gambar 1 menunjukkan bahwa kedua primer tersebut cukup baik untuk diaplikasikan dalam pemeriksaan. Hal ini terlihat dari Tm primer yang berdekatan, panjang primer basa, dan GC content %. Risiko ikatan primer-dimer juga tidak ada yang lebih dari negatif dari -7 kcal/mol dan tidak ditemukan adanya run serta repeats. Tiga pasang (5 buah) primer PCR yang berhasil didesain dapat diuji coba dalam aplikasi PCR konvensional untuk identifikasi toksigenisitas bakteri penyebab difteri dengan teknik PCR multipleks.gambaran interpretasi hasil pemeriksaan PCR multipleks dapat dilihat pada Gambar 2. 1 kbp 900 bp 800 bp 700 bp 600 bp 500 bp 400 bp 300 bp 200 bp Gambar 2. M bp 517 bp Interpretasi Hasil Pemeriksaan PCR Multipleks Marker 100 bp (M), Strain NTTB (1), Strain NTTB (2), Strain Toksigenik (3), dan Strain Non-toksigenik (4). Gambar 2 menunjukkan adanya 4 interpretasi hasil dari aplikasi 3 pasang kandidat primer yang berhasil didesain. Pada strain NTTB akan terdeteksi 2 target primer PCR (pseudogene) di lokasi yang berbeda. Pada strain toksigenik akan terdeteksi 1 target primer PCR (gen dtx). Pada strain non-toksigenik tidak terdeteksi gen target. Dengan demikian dapat dibedakan ketiga jenis toksigenisitas bakteri tersebut dengan pemeriksaan PCR. Pembahasan Gen dtx merupakan penyandi produksi toksin difteri pada 3 spesies bakteri penyebab difteri yang dikenal dengan potentially toxigenic Corynebacteria. Gen ini dibawa oleh Corynephage yang masuk (terinsersi) ke dalam materi genetik bakteri. Pada Corynephage, tempat khusus untuk bergabungnya meteri genetik ini disebut dengan attp site, sedangkan pada bakteri disebut attb site. Dalam 1 strain bakteri dapat diinsersi oleh lebih dari 1 faga dan tidak semua faga tersebut membawa gen tox. Faga yang membawa gen tox disebut phage tox + dan yang tidak membawa gen tox disebut phage tox -. 22,23 Dalam menjalankan perannya, gen dtx diregulasi oleh gen lain dalam kromosom bakteri yang dikenal dengan gen dtxr dengan Fe sebagai ko-faktor.fe akan berikatan dengan protein dtxr yang akan menghambat sintesis toksin pada proses transkripsi. Meskipun demikian, kadar Fe bukanlah satu-satunya faktor yang mempengaruhi produksi toksin difteri.faktor lain, diantaranya kultur berulang di laboratorium, mutasi gen dan beberapa hal yang belum jelas mekanismenya terbukti dapat mempengaruhi produksi toksin difteri Penemuan pseudogene pada 4 isolat C.diphtheriae di Jepang oleh Hall, et.al. menjadi menarik. Hal ini karena keempatnya memiliki sekuens DNA yang sangat mirip dengan gen dtx, namunbersifat nontoksigenik. 11 Sebaliknya, meskipun beberapa sekuens gen dtx C.diphtheriae, C.ulcerans dan C.pseudotuberculosis bervariasi, sebagaimana terlihat pada Gambar 1, ketiganya mampu memproduksi toksin difteri (toksigenik) Oleh karena itu, desain primer PCR untuk amplifikasi seluruh variasi gen dtx dari ke-3 spesies potentially toxigenic Corynebacteriatersebut tanpa amplifikasi pseudogene cukup rumit. Selain variasi antar ke-3 spesies yang cukup tinggi, variasi antar strain dalam masing-masing spesies juga harus diperhatikan. Beberapa persyaratan yang perlu diperhatikan dalam desain primer PCR antara lain GC content 40 %-60%, Tm o C, GC Clamp pada 5 basa ujung 3, panjang primer bp, tidak ada hairpindan pengulangan (run dan repeat) lebih dari 4 basa. 3,4 Khusus untuk PCR multipleks, panjang masingmasing produk PCR harus dibuat sedemikian rupa sehingga bisa dibedakan satu sama lain. Ada beberapa masalah yang harus diperhatikan dengan kandidat primer pseudogene yang diperoleh bila menggunakan sekuens asli yang sama dengan sekuens pseudogene. Pada primer F1pseudo terdapat daerah palindromik yang berrisiko membentuk hairpin dan dapat mengganggu proses hibridisasi. Selain itu pada primer tersebut terdapat run (AAAA) yang sebaiknya dihindari pada desain primer PCR. Kedua masalah tersebut dapat diatasi dengan melakukan modifikasi sekuens dengan mengganti basa A menjadi basa G seperti terlihat dalam kurung. Pada primer F2pseudo juga terdapat run (GGGG) dan GC content sangat tinggi. Hal ini dapat menyebabkan terjadinya penempelan primer tidak pada 548
6 tempatnya (mismatch). Oleh karena itu salah satu basa G dimodifikasi menjadi basa T seperti terlihat dalam kurung. Pada sekuens DNA yang menjadi tempat penempelan ketiga pasang primer didapatkan beberapa mutasi basa, dengan kata lain bahwa daerah tersebut kurang conserve. Namun demikian, mutasi tersebut masih bisa ditoleransi karena umumnya hanya 1 basa dan tidak terletak pada ujung 3 primer. Mutasi pada ujung 3 primer akan menyebabkan kegagalan amplifikasi sekuens karena tidak terjadi elongasi atau pemanjangan. 30 Kesimpulan dan Saran Penelitian ini berhasil mendesain primer baru untuk PCR konvensional yang secara Bioinformatika dapat digunakan untuk identifikasi toksigenisitas bakteri penyebab difteri, termasuk membedakan strain NTTB dari strain toksigenik.uji yang dilakukan baru sebatas perhitungan dengan software Bioinformatika (in silico)sehingga masih membutuhkan uji lebih lanjut untuk aplikasi langsung di mesin PCR. Aplikasi PCR dengan primer baru membutuhkan optimasi prosedur yang disesuaikan dengan reagen maupun mesin yang digunakan. Ucapan Terima Kasih Ungkapan terima kasih kami sampaikan kepada seluruh pihak yang telah berperan dalam penelitian dan publikasi ini. Daftar Pustaka 1. Budiarto BR. Polymerase Chain Reaction (PCR) Perkembangan dan perannya dalam diagnostik kesehatan. BioTrends. 2015; 6(2) Sing A, Berger A, Schneider-Brachert W, Holzmann T, Reischl U. Rapid detection and molecular differentiation of toxigenic Corynebacterium diphtheriae and Corynebacterium ulcerans Strains by LightCycler PCR. J Clin Microbiol. 2011;49(7) Yuryev A. Editor. Methods in Molecular Biology PCR Primer Design. 2007; New Jersey Hummana Press. 4. Garibyan L & Avashia N. Research techniques made simple Polymerase Chain Reaction (PCR). J Invest Dermatol. 2013;133(3) e6.doi /jid Ye J, Coulouris G, Zaretskaya I, Cutcutache I, Rozen S and Madden TL. Primer-BLAST A tool to design target-specific primers for polymerase chain reaction. BMC Bioinformatics 2012, Patel NK & Prakash N. Principle and tools for primer design. Atmiya Spandan. 2013;1(1) Nakamura S, Masuda T, Mochizuki A, Konishi K, Tokumaru S, Ueno K and Yamaguchi T. Primer Design for Identifying economically Important Liriomyza Spesies (Deptera Agromyzidae) by Multiplex PCR. Mol. Eco. Resources. 2013; Srivastava GP, Hanumappa M, Kushwaha G, Nguyen HT and Dong X. Homolog-specific PCR Primer Design for Profiling Splice variants. Nucleic Acid Research. 2011; Sekizuka T, Yamamoto A, Komiya T, Kenri T, Takeuchi F, Shibayama K, Takahashi M, Kuroda M, and Iwaki M.Corynebacterium ulcerans 0102 carries the gene encoding diphtheria toxin on a prophage different from the C. diphtheriae NCTC prophage. BMC Microbiology. 2012; Komiya T, Seto Y, De Zoysa A, Iwaki M, Hatanaka A, Tsunoda A, Arakawa Y, Kozaki S, and Takahashi M. Two Japanese Corynebacterium ulcerans isolatesfrom the same hospital ribotype, toxigenicity and serum antitoxin totre. JMM. 2010; Hall AJ, Cassiday PK, Bernard KA, Bolt F, Steigerwalt AG, Bixler D, Pawloski LC, et.al. Novel Corynebacterium diphtheriae in Domestic Cats. Emerg Infect Dis. 2010; 16(4) Zakikhany K, Neal S, and Efstratiou. Emergence and molecular characterization of non-toxigenic tox gene-bearing Corynebacterium diphtheriae biovar mitis in the United Kingdom, Euro Surveill. 2014;19(22) Efstratiou A, Engler KH, Dawes CS, and Sesardic D. Comparison of Phenotypic and Genotypic Methods for Detection of Diphtheria Toxin among Isolates of Pathogenic Corynebacteria. J.Clin. Microbiol.1998;36(11) Torres LdeF. Ribeiro D, Hirata Jr R, Pacheco LG, Souza MC, dos Santos LS, dos Santos LS, Salah M, Costa MM, Ribeiro MG, Selim SA, Azevedo VA, Mattos-Guaraldi AL. Multiplex polymerase chain reaction to identify and determine the toxygenicity of Corynebacterium spp with zoonotic potenticl and an overview of human and animal infections. Mem Inst Oswaldo Cruz. 2013;108(3) Sunarno, Sariadji K, Wibowo HA. Potensi Gen dtx dan dtxr Sebagai Marker untuk Deteksi dan Pemeriksaan Toksigenisitas Corynebacterium diphtheriae. Bul.Penelit. Kesehat. 2013;41(1) Pimenta FP, Hirata R, Rosa ACP, Milagres LG and Mattos-Guaraldi AL. A multiplex PCR assay for simultaneous detection of Corynebacterium diphtheriae and differentiation between non-toxigenic and toxigenic isolates. JMM Schuhegger R, Lindermayer M, and Kugler R. Detection of toxigenic Corynebacterium diphtheriae and Corynebacterium ulcerans strains by a Novel Real-Time PCR.J Clin Microbiol. 2008;46(8) Hall T. BioEdit An important software for molecular biology. GERF Bulletin of Biosciences. 2011;2(1) Marshall OJ. PerlPrimer cross-platform, graphical primer design for standard, bisulphate and real-time PCR. Bioinformatics Appl Note. 2004;20(15) Abu-Almaali HM, Alkhatabi HA, Nasr-Allah HA, and Al-Khafaji ZM. Duplex PCR primer for detection of Helicobacter pylori DNA directly from gastric biopsy samples. Kerbala J Phar Sci 2012; Dwivedi B, Schmieder R, Goldsmith DB, Edwars RA, and Breitbart M. PhiSiGns an online tool to identify signature genes in phages and design PCR primers for examining phage diversity. BMC Bioinformatic. 2012; Sangal V & Hoskisson PA. Corynephages Infections of the Infector. In Burkovski A, Editor. Corynebacterium diphtheriae and Related Toxigenic Species Springer. http//libgen.org/ (Accessed 27 February 2015). 23. Seto Y, Komiya T, Iwaki M, Kohda T, Mukamoto M, Takahashi M and Kozaki S. Properties of Corynephage Attachment site and molecular epidemiology of Corynebacterium ulcerans isolated from humans and animals in Japan. Jpn. J. Infect. Dis. 2008; Mercant AT & Spatafora GA. A role for the DtxR family of metalloregulators in gram-positive pathogenesis. Molecular Oral Microbiology. 2014; Tao D Aquino JA, Tetenbaum-Novatt J, White A, Berkovitch, and Ringe D. Mechanism of metal ion activation of the diphtheria toxin repressor dtxr. PNAS. 2005;102(51) Holmes RK. Biology and Molecular Epidemiology of Diphtheria Toxin and the tox Gene. JID. 2000;181(Suppl 1)1S156 S Wagner KS, White JM, Lucenko I, Mercer D, Crowcroft NS, Neal S, and Efstratiou A. Diphtheria in the Postepidemic Period, Europe, EID. 2012;18(2) Dias AASO, Santos LS, Sabbadini PS, Santos CS, Silva FCJr, 549
7 Napoleao F, Nagao PE, Villas-Boas MHS, Hirata RJr, Guaraldi ALM. Corynebacterium ulcerans diphtheria an emerging zoonosis in Brazil andworldwide. Rev Saude Publica. 2011;45(6) Selim SA, Mohamed FH, Hessain AM, and Moussa IM. Immunological characterization of diphtheria toxin recovered from Corynebacterium pseudotuberculosis. Saudi J Biol Sci. 2016;23(2) Lorenz TC. Polymerase Chain Reaction Basic protocol plus troubleshooting and optimization strategies. J Vis Exp. 2012;e3998,doi /
Perbandingan Pemeriksaan Toksigenisitas secara Genotip dan Fenotip pada Beberapa Isolat Corynebacterium diphtheriae Penyebab Difteri di Indonesia
 Perbandingan Pemeriksaan Toksigenisitas secara Genotip dan Fenotip pada Beberapa Isolat Corynebacterium diphtheriae Penyebab Difteri di Indonesia Sunarno 1, Kambang Sariadji 2 2 Puslitbang Biomedis dan
Perbandingan Pemeriksaan Toksigenisitas secara Genotip dan Fenotip pada Beberapa Isolat Corynebacterium diphtheriae Penyebab Difteri di Indonesia Sunarno 1, Kambang Sariadji 2 2 Puslitbang Biomedis dan
DESAIN PRIMER. LAPORAN PRAKTIKUM disusun untuk memenuhi salah satu tugas mata kuliah Biologi Molekuler. oleh : Riani Ulfah
 DESAIN PRIMER LAPORAN PRAKTIKUM disusun untuk memenuhi salah satu tugas mata kuliah Biologi Molekuler oleh : Dhaifan Diza A 1303790 Anisa Suci S 1300904 Novia Rahayu A 1302152 Riani Ulfah 1300952 Shabrina
DESAIN PRIMER LAPORAN PRAKTIKUM disusun untuk memenuhi salah satu tugas mata kuliah Biologi Molekuler oleh : Dhaifan Diza A 1303790 Anisa Suci S 1300904 Novia Rahayu A 1302152 Riani Ulfah 1300952 Shabrina
BAB XII. REAKSI POLIMERISASI BERANTAI
 BAB XII. REAKSI POLIMERISASI BERANTAI Di dalam Bab XII ini akan dibahas pengertian dan kegunaan teknik Reaksi Polimerisasi Berantai atau Polymerase Chain Reaction (PCR) serta komponen-komponen dan tahapan
BAB XII. REAKSI POLIMERISASI BERANTAI Di dalam Bab XII ini akan dibahas pengertian dan kegunaan teknik Reaksi Polimerisasi Berantai atau Polymerase Chain Reaction (PCR) serta komponen-komponen dan tahapan
HASIL DAN PEMBAHASAN
 HASIL DAN PEMBAHASAN Amplifikasi ini membutuhkan primer spesifik (sekuen oligonukelotida khusus) untuk daerah tersebut. Primer biasanya terdiri dari 10-20 nukleotida dan dirancang berdasarkan daerah konservatif
HASIL DAN PEMBAHASAN Amplifikasi ini membutuhkan primer spesifik (sekuen oligonukelotida khusus) untuk daerah tersebut. Primer biasanya terdiri dari 10-20 nukleotida dan dirancang berdasarkan daerah konservatif
ABSTRAK. OPTIMASI AMPLIFIKASI BAGIAN GEN parc DENGAN METODE PCR PADA ISOLAT Salmonella typhi DARI RUMAH SAKIT IMMANUEL BANDUNG PERIODE 2006
 ABSTRAK OPTIMASI AMPLIFIKASI BAGIAN GEN parc DENGAN METODE PCR PADA ISOLAT Salmonella typhi DARI RUMAH SAKIT IMMANUEL BANDUNG PERIODE 2006 Hadi Sumitro Jioe, 2008. Pembimbing I : Ernawati Arifin Giri Rachman,
ABSTRAK OPTIMASI AMPLIFIKASI BAGIAN GEN parc DENGAN METODE PCR PADA ISOLAT Salmonella typhi DARI RUMAH SAKIT IMMANUEL BANDUNG PERIODE 2006 Hadi Sumitro Jioe, 2008. Pembimbing I : Ernawati Arifin Giri Rachman,
Penerapan Diagnostik Laboratorium pada Kasus Tersangka Positif Difteri pada Kejadian Luar Biasa di Kota Pontianak, Kalimantan Barat
 NaskahAsli Penerapan Diagnostik Laboratorium pada Kasus Tersangka Positif Difteri pada Kejadian Luar Biasa di Kota Pontianak, Kalimantan Barat Kambang Sariadji, Sunarno, Rudi Hendro Putranto Pusat Biomedis
NaskahAsli Penerapan Diagnostik Laboratorium pada Kasus Tersangka Positif Difteri pada Kejadian Luar Biasa di Kota Pontianak, Kalimantan Barat Kambang Sariadji, Sunarno, Rudi Hendro Putranto Pusat Biomedis
I. PENDAHULUAN. perempuan di dunia dan urutan pertama untuk wanita di negara sedang
 I. PENDAHULUAN Kanker serviks menduduki urutan kedua dari penyakit kanker yang menyerang perempuan di dunia dan urutan pertama untuk wanita di negara sedang berkembang (Emilia, dkk., 2010). Berdasarkan
I. PENDAHULUAN Kanker serviks menduduki urutan kedua dari penyakit kanker yang menyerang perempuan di dunia dan urutan pertama untuk wanita di negara sedang berkembang (Emilia, dkk., 2010). Berdasarkan
BAB 4 HASIL PERCOBAAN DAN BAHASAN. Oligonukleotida sintetis daerah pengkode IFNα2b sintetis dirancang menggunakan
 BAB 4 HASIL PERCOBAAN DAN BAHASAN Oligonukleotida sintetis daerah pengkode IFNα2b sintetis dirancang menggunakan program komputer berdasarkan metode sintesis dua arah TBIO, dimana proses sintesis daerah
BAB 4 HASIL PERCOBAAN DAN BAHASAN Oligonukleotida sintetis daerah pengkode IFNα2b sintetis dirancang menggunakan program komputer berdasarkan metode sintesis dua arah TBIO, dimana proses sintesis daerah
DESAIN PRIMER SECARA IN SILICO UNTUK AMPLIFIKASI FRAGMEN GEN rpob Mycobacterium tuberculosis DENGAN POLYMERASE CHAIN REACTION (PCR)
 Desain Primer secara in silico untuk Amplifikasi Fragmen Gen rpob Mycobacterium tuberculosis DESAIN PRIMER SECARA IN SILICO UNTUK AMPLIFIKASI FRAGMEN GEN rpob Mycobacterium tuberculosis DENGAN POLYMERASE
Desain Primer secara in silico untuk Amplifikasi Fragmen Gen rpob Mycobacterium tuberculosis DESAIN PRIMER SECARA IN SILICO UNTUK AMPLIFIKASI FRAGMEN GEN rpob Mycobacterium tuberculosis DENGAN POLYMERASE
STUDI HOMOLOGI DAERAH TERMINAL-C HASIL TRANSLASI INSCRIPTO BEBERAPA GEN DNA POLIMERASE I
 STUDI HOMOLOGI DAERAH TERMINAL-C HASIL TRANSLASI INSCRIPTO BEBERAPA GEN DNA POLIMERASE I T 572 MUL ABSTRAK DNA polimerase merupakan enzim yang berperan dalam proses replikasi DNA. Tiga aktivitas yang umumnya
STUDI HOMOLOGI DAERAH TERMINAL-C HASIL TRANSLASI INSCRIPTO BEBERAPA GEN DNA POLIMERASE I T 572 MUL ABSTRAK DNA polimerase merupakan enzim yang berperan dalam proses replikasi DNA. Tiga aktivitas yang umumnya
POTENSI GEN dtx DAN dtxr SEBAGAI MARKER UNTUK DETEKSI DAN PEMERIKSAAN TOKSIGENISITAS Corynebacterium diphtheriae
 Bul. Penelit. Kesehat, Vol. 41, No. 1, 2013: 1-10 POTENSI GEN dtx DAN dtxr SEBAGAI MARKER UNTUK DETEKSI DAN PEMERIKSAAN TOKSIGENISITAS Corynebacterium diphtheriae Sunarno *, Kambang Sariadji dan Holly
Bul. Penelit. Kesehat, Vol. 41, No. 1, 2013: 1-10 POTENSI GEN dtx DAN dtxr SEBAGAI MARKER UNTUK DETEKSI DAN PEMERIKSAAN TOKSIGENISITAS Corynebacterium diphtheriae Sunarno *, Kambang Sariadji dan Holly
AMPLIFIKASI GEN CYTOCHROME OXIDASE SUBUNIT I (COI) DARI SAMPEL SIRIP IKAN HIU DENGAN MENGGUNAKAN BEBERAPA PASANGAN PRIMER
 AMPLIFIKASI GEN CYTOCHROME OXIDASE SUBUNIT I (COI) DARI SAMPEL SIRIP IKAN HIU DENGAN MENGGUNAKAN BEBERAPA PASANGAN PRIMER (Amplification of Cytochrome Oxidase Subunit I (COI) Gene from Shark Fin Samples
AMPLIFIKASI GEN CYTOCHROME OXIDASE SUBUNIT I (COI) DARI SAMPEL SIRIP IKAN HIU DENGAN MENGGUNAKAN BEBERAPA PASANGAN PRIMER (Amplification of Cytochrome Oxidase Subunit I (COI) Gene from Shark Fin Samples
IDENTIFIKASI TEMUAN KONTAK POSITIF KASUS KEJADIAN LUAR BIASA DIFTERIA DI DKI JAKARTA
 IDENTIFIKASI TEMUAN KONTAK POSITIF KASUS KEJADIAN LUAR BIASA DIFTERIA DI DKI JAKARTA IDENTIFICATION OF POSITIVE CONTACTS FINDINGS OF DIPHTHERIA OUTBREAKS IN JAKARTA Kambang Sariadji*, Rudi HP, Sunarno,
IDENTIFIKASI TEMUAN KONTAK POSITIF KASUS KEJADIAN LUAR BIASA DIFTERIA DI DKI JAKARTA IDENTIFICATION OF POSITIVE CONTACTS FINDINGS OF DIPHTHERIA OUTBREAKS IN JAKARTA Kambang Sariadji*, Rudi HP, Sunarno,
DESAIN PRIMER UNTUK AMPLIFIKASI FRAGMEN GEN inha ISOLAT 134 MULTIDRUG RESISTANCE TUBERCULOSIS (MDR-TB) DENGAN METODE POLYMERASE CHAIN REACTION
 Cakra Kimia (Indonesian E-Journal of Applied Chemistry) DESAIN PRIMER UNTUK AMPLIFIKASI FRAGMEN GEN inha ISOLAT 134 MULTIDRUG RESISTANCE TUBERCULOSIS (MDR-TB) DENGAN METODE POLYMERASE CHAIN REACTION Luh
Cakra Kimia (Indonesian E-Journal of Applied Chemistry) DESAIN PRIMER UNTUK AMPLIFIKASI FRAGMEN GEN inha ISOLAT 134 MULTIDRUG RESISTANCE TUBERCULOSIS (MDR-TB) DENGAN METODE POLYMERASE CHAIN REACTION Luh
BAB 4 HASIL PERCOBAAN DAN PEMBAHASAN
 BAB 4 HASIL PERCOBAAN DAN PEMBAHASAN Sebelum melakukan PCR, terlebih dahulu dilakukan perancangan primer menggunakan program DNA Star. Pemilihan primer dilakukan dengan mempertimbangkan parameter spesifisitas,
BAB 4 HASIL PERCOBAAN DAN PEMBAHASAN Sebelum melakukan PCR, terlebih dahulu dilakukan perancangan primer menggunakan program DNA Star. Pemilihan primer dilakukan dengan mempertimbangkan parameter spesifisitas,
Direct Polymerase Chain Reaction: Sebuah Alternatif Metode Diagnostik Difteri Secara Cepat, Mudah dan Hemat
 88 Makara Seri Kesehatan, 203, 7(2): 88-94 Direct Polymerase Chain Reaction: Sebuah Alternatif Metode Diagnostik Difteri Secara Cepat, Mudah dan Hemat Sunarno,4 *, Aulia Rizki, Kambang Sariadji, Amarila
88 Makara Seri Kesehatan, 203, 7(2): 88-94 Direct Polymerase Chain Reaction: Sebuah Alternatif Metode Diagnostik Difteri Secara Cepat, Mudah dan Hemat Sunarno,4 *, Aulia Rizki, Kambang Sariadji, Amarila
Toksigenitas Corynebacterium diphtheriae Pada Sampel Kejadian Luar Biasa Difteri Tahun Menggunakan Elektes
 208 Artikel Penelitian Toksigenitas Corynebacterium diphtheriae Pada Sampel Kejadian Luar Biasa Difteri Tahun 2010 2015 Menggunakan Elektes Kambang Sariadji, Sunarno Abstrak Strain Corynebacterium diphtheriae
208 Artikel Penelitian Toksigenitas Corynebacterium diphtheriae Pada Sampel Kejadian Luar Biasa Difteri Tahun 2010 2015 Menggunakan Elektes Kambang Sariadji, Sunarno Abstrak Strain Corynebacterium diphtheriae
I. PENDAHULUAN 1.1 Latar Belakang
 I. PENDAHULUAN 1.1 Latar Belakang Penyakit Demam Berdarah Dengue (DBD) merupakan salah satu penyakit yang menjadi permasalahan utama di dunia. Penyakit ini disebabkan oleh virus Dengue yang jika tidak
I. PENDAHULUAN 1.1 Latar Belakang Penyakit Demam Berdarah Dengue (DBD) merupakan salah satu penyakit yang menjadi permasalahan utama di dunia. Penyakit ini disebabkan oleh virus Dengue yang jika tidak
DESAIN PRIMER SPESIFIK UNTUK MENGAMPLIFIKASI SEKUENSI GEN cfl (coronafacate ligase) PADA PATOGEN HAWAR BAKTERI YANG MENGINFEKSI KEDELAI SKRIPSI
 DESAIN PRIMER SPESIFIK UNTUK MENGAMPLIFIKASI SEKUENSI GEN cfl (coronafacate ligase) PADA PATOGEN HAWAR BAKTERI YANG MENGINFEKSI KEDELAI SKRIPSI Oleh : Riska Susilawati NIM. 081510501173 PROGRAM STUDI AGROTEKNOLOGI
DESAIN PRIMER SPESIFIK UNTUK MENGAMPLIFIKASI SEKUENSI GEN cfl (coronafacate ligase) PADA PATOGEN HAWAR BAKTERI YANG MENGINFEKSI KEDELAI SKRIPSI Oleh : Riska Susilawati NIM. 081510501173 PROGRAM STUDI AGROTEKNOLOGI
BAB IV HASIL DAN PEMBAHASAN. Deteksi genom virus avian influenza pada penelitian dilakukan
 30 BAB IV HASIL DAN PEMBAHASAN A. KONDISI OPTIMAL REAKSI AMPLIFIKASI Deteksi genom virus avian influenza pada penelitian dilakukan menggunakan primer NA. Primer NA dipilih karena protein neuraminidase,
30 BAB IV HASIL DAN PEMBAHASAN A. KONDISI OPTIMAL REAKSI AMPLIFIKASI Deteksi genom virus avian influenza pada penelitian dilakukan menggunakan primer NA. Primer NA dipilih karena protein neuraminidase,
ABSTRAK. OPTIMASI AMPLIFIKASI GEN flic DENGAN METODE PCR UNTUK DETEKSI Salmonella typhi GALUR INDONESIA
 ABSTRAK OPTIMASI AMPLIFIKASI GEN flic DENGAN METODE PCR UNTUK DETEKSI Salmonella typhi GALUR INDONESIA T. Robertus, 2007. Pembimbing I : Johan Lucianus, dr., M.Si. Pembimbing II : Ernawati Arifin Giri
ABSTRAK OPTIMASI AMPLIFIKASI GEN flic DENGAN METODE PCR UNTUK DETEKSI Salmonella typhi GALUR INDONESIA T. Robertus, 2007. Pembimbing I : Johan Lucianus, dr., M.Si. Pembimbing II : Ernawati Arifin Giri
Fakultas Biologi Unsoed
 TEKMK PCR oleh Drs. Agus Hery Susanto, M.S. staf pengajar Pendahuluan Teknik PCR (polymerase chain reaction) digunakan untuk menggandakan fragmen DNA (urutan basa nukleotida) tertentu secara invitro melalui
TEKMK PCR oleh Drs. Agus Hery Susanto, M.S. staf pengajar Pendahuluan Teknik PCR (polymerase chain reaction) digunakan untuk menggandakan fragmen DNA (urutan basa nukleotida) tertentu secara invitro melalui
I. PENDAHULUAN. 1.1 Latar Belakang. Demam Berdarah Dengue (DBD) merupakan salah satu penyakit infeksi
 1 I. PENDAHULUAN 1.1 Latar Belakang Demam Berdarah Dengue (DBD) merupakan salah satu penyakit infeksi yang dalam beberapa tahun ini telah menjadi permasalahan kesehatan di dunia. Penyakit DBD adalah penyakit
1 I. PENDAHULUAN 1.1 Latar Belakang Demam Berdarah Dengue (DBD) merupakan salah satu penyakit infeksi yang dalam beberapa tahun ini telah menjadi permasalahan kesehatan di dunia. Penyakit DBD adalah penyakit
Diphtheria-like Diseases, Zoonotic Diseases Similar to Difteri caused by Corynebacterium ulcerans that should be handle cautiousness
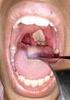 Review Jurnal Epidemiologi dan Penyakit Bersumber Binatang (Epidemiology and Zoonosis Journal) Vol. 5, No. 1, Juni 2014 Hal : 49-54 Penulis : 1. Kambang Sariadji 2. Sunarno 3. Rudi H.P Korespondensi: Pusat
Review Jurnal Epidemiologi dan Penyakit Bersumber Binatang (Epidemiology and Zoonosis Journal) Vol. 5, No. 1, Juni 2014 Hal : 49-54 Penulis : 1. Kambang Sariadji 2. Sunarno 3. Rudi H.P Korespondensi: Pusat
HASIL DAN PEMBAHASAN
 HASIL DAN PEMBAHASAN Virus Hepatitis B Gibbon Regio Pre-S1 Amplifikasi Virus Hepatitis B Regio Pre-S1 Hasil amplifikasi dari 9 sampel DNA owa jawa yang telah berstatus serologis positif terhadap antigen
HASIL DAN PEMBAHASAN Virus Hepatitis B Gibbon Regio Pre-S1 Amplifikasi Virus Hepatitis B Regio Pre-S1 Hasil amplifikasi dari 9 sampel DNA owa jawa yang telah berstatus serologis positif terhadap antigen
DAFTAR ISI DAFTAR TABEL... DAFTAR GAMBAR... DAFTAR LAMPIRAN...
 DAFTAR ISI Bab Halaman DAFTAR TABEL... DAFTAR GAMBAR... DAFTAR LAMPIRAN... ix x xii I II III PENDAHULUAN 1.1 Latar Belakang... 1 1.2 Identifikasi Masalah... 2 1.3 Tujuan Penelitian... 2 1.4 Kegunaan Penelitian...
DAFTAR ISI Bab Halaman DAFTAR TABEL... DAFTAR GAMBAR... DAFTAR LAMPIRAN... ix x xii I II III PENDAHULUAN 1.1 Latar Belakang... 1 1.2 Identifikasi Masalah... 2 1.3 Tujuan Penelitian... 2 1.4 Kegunaan Penelitian...
DAFTAR ISI Halaman HALAMAN JUDUL... i HALAMAN PENGESAHAN... KATA PENGANTAR... DAFTAR ISI... DAFTAR TABEL... DAFTAR GAMBAR... DAFTAR LAMPIRAN...
 DAFTAR ISI HALAMAN JUDUL... i HALAMAN PENGESAHAN... KATA PENGANTAR...... DAFTAR ISI... DAFTAR TABEL... DAFTAR GAMBAR... DAFTAR LAMPIRAN... INTISARI... ABSTRACT... PENDAHULUAN... 1 A. Latar Belakang...
DAFTAR ISI HALAMAN JUDUL... i HALAMAN PENGESAHAN... KATA PENGANTAR...... DAFTAR ISI... DAFTAR TABEL... DAFTAR GAMBAR... DAFTAR LAMPIRAN... INTISARI... ABSTRACT... PENDAHULUAN... 1 A. Latar Belakang...
METODE CEPAT EKSTRAKSI DNA Corynebacterium diphtheriae UNTUK PEMERIKSAAN PCR
 Bul. Penelit. Kesehat, Vol. 42, No. 2, Juni 2014: 85-92 METODE CEPAT EKSTRAKSI DNA Corynebacterium diphtheriae UNTUK PEMERIKSAAN PCR Sunarno 1,4*, Fauzul Muna 1, Nyoman Fitri 1, Amarila Malik 2, Anis Karuniawati
Bul. Penelit. Kesehat, Vol. 42, No. 2, Juni 2014: 85-92 METODE CEPAT EKSTRAKSI DNA Corynebacterium diphtheriae UNTUK PEMERIKSAAN PCR Sunarno 1,4*, Fauzul Muna 1, Nyoman Fitri 1, Amarila Malik 2, Anis Karuniawati
IDENTIFIKASI KERAGAMAN GEN Growth Hormone PADA DOMBA EKOR TIPIS SUMATERA
 SKRIPSI IDENTIFIKASI KERAGAMAN GEN Growth Hormone PADA DOMBA EKOR TIPIS SUMATERA Oleh: Astri Muliani 11081201226 PROGRAM STUDI PETERNAKAN FAKULTAS PERTANIAN DAN PETERNAKAN UNIVERSITAS ISLAM NEGERI SULTAN
SKRIPSI IDENTIFIKASI KERAGAMAN GEN Growth Hormone PADA DOMBA EKOR TIPIS SUMATERA Oleh: Astri Muliani 11081201226 PROGRAM STUDI PETERNAKAN FAKULTAS PERTANIAN DAN PETERNAKAN UNIVERSITAS ISLAM NEGERI SULTAN
POLYMERASE CHAIN REACTION (PCR)
 POLYMERASE CHAIN REACTION (PCR) Disusun oleh: Hanif Wahyuni (1210411003) Prayoga Wibhawa Nu Tursedhi Dina Putri Salim (1210412032) (1210413031) SEJARAH Teknik ini dirintis oleh Kary Mullis pada tahun 1985
POLYMERASE CHAIN REACTION (PCR) Disusun oleh: Hanif Wahyuni (1210411003) Prayoga Wibhawa Nu Tursedhi Dina Putri Salim (1210412032) (1210413031) SEJARAH Teknik ini dirintis oleh Kary Mullis pada tahun 1985
KATAPENGANTAR. Pekanbaru, Desember2008. Penulis
 KATAPENGANTAR Fuji syukut ke Hadirat Allah SWT. berkat rahmat dan izin-nya penulis dapat menyelesaikan skripsi yang beijudul "Skrining Bakteri Vibrio sp Penyebab Penyakit Udang Berbasis Teknik Sekuens
KATAPENGANTAR Fuji syukut ke Hadirat Allah SWT. berkat rahmat dan izin-nya penulis dapat menyelesaikan skripsi yang beijudul "Skrining Bakteri Vibrio sp Penyebab Penyakit Udang Berbasis Teknik Sekuens
BAB I PENDAHULUAN. Penggunaan mikroorganisme antagonis sebagai agen pengendali hayati
 BAB I PENDAHULUAN A. Latar Belakang Penggunaan mikroorganisme antagonis sebagai agen pengendali hayati memberikan harapan baru untuk pengendalian hama pertanian terutama fungi yang bersifat patogen. Secara
BAB I PENDAHULUAN A. Latar Belakang Penggunaan mikroorganisme antagonis sebagai agen pengendali hayati memberikan harapan baru untuk pengendalian hama pertanian terutama fungi yang bersifat patogen. Secara
4. HASIL DAN PEMBAHASAN
 29 4. HASIL DAN PEMBAHASAN 4.1 Karakteristik isolat bakteri dari ikan tuna dan cakalang 4.1.1 Morfologi isolat bakteri Secara alamiah, mikroba terdapat dalam bentuk campuran dari berbagai jenis. Untuk
29 4. HASIL DAN PEMBAHASAN 4.1 Karakteristik isolat bakteri dari ikan tuna dan cakalang 4.1.1 Morfologi isolat bakteri Secara alamiah, mikroba terdapat dalam bentuk campuran dari berbagai jenis. Untuk
MATERI DAN METODE. Kota Padang Sumatera Barat pada bulan Oktober Amplifikasi gen Growth
 III. MATERI DAN METODE 3.1 Waktu dan Tempat Pengambilan sampel darah domba dilakukan di Kecamatan Koto Tengah Kota Padang Sumatera Barat pada bulan Oktober 2012. Amplifikasi gen Growth Hormone menggunakan
III. MATERI DAN METODE 3.1 Waktu dan Tempat Pengambilan sampel darah domba dilakukan di Kecamatan Koto Tengah Kota Padang Sumatera Barat pada bulan Oktober 2012. Amplifikasi gen Growth Hormone menggunakan
INTERNAL PRIMER DESIGN FOR DIVERSITY STUDY OF THERMOSTABLE LIPASE GENE FRAGMENT FROM ENVIRONMENTAL SAMPLE ABSTRACT
 INTERNAL PRIMER DESIGN FOR DIVERSITY STUDY OF THERMOSTABLE LIPASE GENE FRAGMENT FROM ENVIRONMENTAL SAMPLE Nurhasanah 1,2), Santi Nurbaiti 1), Fida Madayanti 1), Akhmaloka 1) 1) Biochemistry Research Group,
INTERNAL PRIMER DESIGN FOR DIVERSITY STUDY OF THERMOSTABLE LIPASE GENE FRAGMENT FROM ENVIRONMENTAL SAMPLE Nurhasanah 1,2), Santi Nurbaiti 1), Fida Madayanti 1), Akhmaloka 1) 1) Biochemistry Research Group,
DAFTAR ISI. BAB I. PENDAHULUAN 1.1. Latar Belakang Rumusan Masalah Tujuan Penelitian Manfaat Penelitian...
 DAFTAR ISI SAMPUL DALAM... i LEMBAR PERSETUJUAN... ii PENETAPAN PANITIA PENGUJI... iii UCAPAN TERIMA KASIH... iv ABSTRAK... v ABSTRACT... vi DAFTAR ISI... vii DAFTAR TABEL... ix DAFTAR GAMBAR... x BAB
DAFTAR ISI SAMPUL DALAM... i LEMBAR PERSETUJUAN... ii PENETAPAN PANITIA PENGUJI... iii UCAPAN TERIMA KASIH... iv ABSTRAK... v ABSTRACT... vi DAFTAR ISI... vii DAFTAR TABEL... ix DAFTAR GAMBAR... x BAB
DETEKSI SPESIES PADA PRODUK OLAHAN BAKSO DENGAN MULTIPLEX-PCR
 DETEKSI SPESIES PADA PRODUK OLAHAN BAKSO DENGAN MULTIPLEX-PCR SKRIPSI Untuk memenuhi sebagian persyaratan guna memperoleh derajat Sarjana Peternakan di Fakultas Pertanian Universitas Sebelas Maret Program
DETEKSI SPESIES PADA PRODUK OLAHAN BAKSO DENGAN MULTIPLEX-PCR SKRIPSI Untuk memenuhi sebagian persyaratan guna memperoleh derajat Sarjana Peternakan di Fakultas Pertanian Universitas Sebelas Maret Program
(A) 530C-550C; (B) 560C, 570C, 580C, 600C; (C) 590C, 610C, 620C; (D)
 2 melawan mikroba. Peran flavonol dalam bidang kesehatan sebagai antiinflamatori, antioksidan, antiproliferatif, menekan fotohemolisis eritrosit manusia, dan mengakhiri reaksi rantai radikal bebas (Albert
2 melawan mikroba. Peran flavonol dalam bidang kesehatan sebagai antiinflamatori, antioksidan, antiproliferatif, menekan fotohemolisis eritrosit manusia, dan mengakhiri reaksi rantai radikal bebas (Albert
PERBANDINGAN POLA PITA AMPLIFIKASI DNA DAUN, BUNGA, DAN BUAH KELAPA SAWIT NORMAL DAN ABNORMAL ALFINIA AZIZAH
 PERBANDINGAN POLA PITA AMPLIFIKASI DNA DAUN, BUNGA, DAN BUAH KELAPA SAWIT NORMAL DAN ABNORMAL ALFINIA AZIZAH PROGRAM STUDI BIOKIMIA FAKULTAS MATEMATIKA DAN ILMU PENGETAHUAN ALAM INSTITUT PERTANIAN BOGOR
PERBANDINGAN POLA PITA AMPLIFIKASI DNA DAUN, BUNGA, DAN BUAH KELAPA SAWIT NORMAL DAN ABNORMAL ALFINIA AZIZAH PROGRAM STUDI BIOKIMIA FAKULTAS MATEMATIKA DAN ILMU PENGETAHUAN ALAM INSTITUT PERTANIAN BOGOR
Saintek Vol 5, No 6, Tahun 2010 POLYMERASE CHAIN REACTION (PCR) Zuhriana K.Yusuf
 Saintek Vol 5, No 6, Tahun 2010 POLYMERASE CHAIN REACTION (PCR) Zuhriana K.Yusuf Staf Pengajar Jurusan Kesehatan Masyarakat FIKK Universitas Negeri Gorontalo Abstrak (Polymerase Chain Reaction, PCR) adalah
Saintek Vol 5, No 6, Tahun 2010 POLYMERASE CHAIN REACTION (PCR) Zuhriana K.Yusuf Staf Pengajar Jurusan Kesehatan Masyarakat FIKK Universitas Negeri Gorontalo Abstrak (Polymerase Chain Reaction, PCR) adalah
ABSTRACT Development Method of Detection Contaminant Bacterial Pathogen Escherichia coli in Milk with Real-Time Polymerase Chain Reaction (RTi- PCR)
 ABSTRACT Development Method of Detection Contaminant Bacterial Pathogen Escherichia coli in Milk with Real-Time Polymerase Chain Reaction (RTi- PCR) By Amalia Masturotul M 09/283370/PA/12532 Detection
ABSTRACT Development Method of Detection Contaminant Bacterial Pathogen Escherichia coli in Milk with Real-Time Polymerase Chain Reaction (RTi- PCR) By Amalia Masturotul M 09/283370/PA/12532 Detection
BAB I PENDAHULUAN. rantai globin, yaitu gen HBA yang menyandi α-globin atau gen HBB yang
 BAB I PENDAHULUAN A. Latar Belakang Thalassemia merupakan kelainan genetik dengan pola pewarisan autosomal resesif yang disebabkan karena adanya mutasi pada gen penyandi rantai globin, yaitu gen HBA yang
BAB I PENDAHULUAN A. Latar Belakang Thalassemia merupakan kelainan genetik dengan pola pewarisan autosomal resesif yang disebabkan karena adanya mutasi pada gen penyandi rantai globin, yaitu gen HBA yang
Identifikasi mikroba secara molekuler dengan metode NCBI (National Center for Biotechnology Information)
 Identifikasi mikroba secara molekuler dengan metode NCBI (National Center for Biotechnology Information) Identifikasi bakteri pada saat ini masih dilakukan secara konvensional melalui studi morfologi dan
Identifikasi mikroba secara molekuler dengan metode NCBI (National Center for Biotechnology Information) Identifikasi bakteri pada saat ini masih dilakukan secara konvensional melalui studi morfologi dan
RED BIOTECHNOLOGY: SOLUSI PENANGANAN DIFTERI SEBUAH REVIEW
 RED BIOTECHNOLOGY: SOLUSI PENANGANAN DIFTERI SEBUAH REVIEW Muhammad Iqbal Filayani Tadris Biologi, Fakultas Tarbiyah dan Ilmu Keguruan, IAIN Tulungagung Muhammadiqbalfilayani16@gmail.com ABSTRAK Difteri
RED BIOTECHNOLOGY: SOLUSI PENANGANAN DIFTERI SEBUAH REVIEW Muhammad Iqbal Filayani Tadris Biologi, Fakultas Tarbiyah dan Ilmu Keguruan, IAIN Tulungagung Muhammadiqbalfilayani16@gmail.com ABSTRAK Difteri
BAB 4 HASIL PERCOBAAN DAN BAHASAN
 14 BAB 4 HASIL PERCOBAAN DAN BAHASAN Konfirmasi bakteri C. violaceum dan B. cereus dilakukan dengan pewarnaan Gram, identifikasi morfologi sel bakteri, sekuensing PCR 16s rdna dan uji kualitatif aktivitas
14 BAB 4 HASIL PERCOBAAN DAN BAHASAN Konfirmasi bakteri C. violaceum dan B. cereus dilakukan dengan pewarnaan Gram, identifikasi morfologi sel bakteri, sekuensing PCR 16s rdna dan uji kualitatif aktivitas
IDENTIFIKASI ISOLAT BAKTERI PENGHASIL ENZIM SELULASE DARI LIMBAH AMPAS TEBU BERDASARKAN ANALISIS HOMOLOGI GEN PENYANDI 16S rrna
 IDENTIFIKASI ISOLAT BAKTERI PENGHASIL ENZIM SELULASE DARI LIMBAH AMPAS TEBU BERDASARKAN ANALISIS HOMOLOGI GEN PENYANDI 16S rrna DYAH RATNA ARIPUTRI 2443009052 PROGRAM STUDI S1 FAKULTAS FARMASI UNIVERSITAS
IDENTIFIKASI ISOLAT BAKTERI PENGHASIL ENZIM SELULASE DARI LIMBAH AMPAS TEBU BERDASARKAN ANALISIS HOMOLOGI GEN PENYANDI 16S rrna DYAH RATNA ARIPUTRI 2443009052 PROGRAM STUDI S1 FAKULTAS FARMASI UNIVERSITAS
Penelitian akan dilaksanakan pada bulan Februari-Agustus 2010 di Laboratorium Zoologi Departemen Biologi, FMIPA, IPB.
 Kolokium Ajeng Ajeng Siti Fatimah, Achmad Farajallah dan Arif Wibowo. 2009. Karakterisasi Genom Mitokondria Gen 12SrRNA - COIII pada Ikan Belida Batik Anggota Famili Notopteridae. Kolokium disampaikan
Kolokium Ajeng Ajeng Siti Fatimah, Achmad Farajallah dan Arif Wibowo. 2009. Karakterisasi Genom Mitokondria Gen 12SrRNA - COIII pada Ikan Belida Batik Anggota Famili Notopteridae. Kolokium disampaikan
IDENTIFIKASI DNA BAKTERI MULTIRESISTEN GENUS STREPTOCOCCUS ( ISOLAT WK 45 ) DENGAN METODE PCR MENGGUNAKAN PRIMER UNIVERSAL 16S rrna
 IDENTIFIKASI DNA BAKTERI MULTIRESISTEN GENUS STREPTOCOCCUS ( ISOLAT WK 45 ) DENGAN METODE PCR MENGGUNAKAN PRIMER UNIVERSAL 16S rrna SKRIPSI Untuk memenuhi sebagian persyaratan Mencapai Derajat Sarjana
IDENTIFIKASI DNA BAKTERI MULTIRESISTEN GENUS STREPTOCOCCUS ( ISOLAT WK 45 ) DENGAN METODE PCR MENGGUNAKAN PRIMER UNIVERSAL 16S rrna SKRIPSI Untuk memenuhi sebagian persyaratan Mencapai Derajat Sarjana
ABSTRAK DAN EXECUTIVE SUMMARY PENELITIAN FUNDAMENTAL. TAHUN ANGGARAN 2014 (Tahun ke 1 dari rencana 2 tahun)
 Kode/Nama Rumpun Ilmu: 307/Ilmu Kedokteran Dasar dan Biomedis ABSTRAK DAN EXECUTIVE SUMMARY PENELITIAN FUNDAMENTAL TAHUN ANGGARAN 2014 (Tahun ke 1 dari rencana 2 tahun) KLONING DAN ANALISIS SEKUEN DBLβC2-VAR
Kode/Nama Rumpun Ilmu: 307/Ilmu Kedokteran Dasar dan Biomedis ABSTRAK DAN EXECUTIVE SUMMARY PENELITIAN FUNDAMENTAL TAHUN ANGGARAN 2014 (Tahun ke 1 dari rencana 2 tahun) KLONING DAN ANALISIS SEKUEN DBLβC2-VAR
PENGENALAN BIOINFORMATIKA
 PS-S1 Jurusan Biologi, FMIPA, UNEJ (2017) PENGENALAN BIOINFORMATIKA Oleh: Syubbanul Wathon, S.Si., M.Si. Pokok Bahasan Sejarah Bioinformatika Istilah-istilah biologi Pangkalan data Tools Bioinformatika
PS-S1 Jurusan Biologi, FMIPA, UNEJ (2017) PENGENALAN BIOINFORMATIKA Oleh: Syubbanul Wathon, S.Si., M.Si. Pokok Bahasan Sejarah Bioinformatika Istilah-istilah biologi Pangkalan data Tools Bioinformatika
HASIL DAN PEMBAHASAN Isolasi DNA Genomik Sengon
 HASIL DAN PEMBAHASAN Isolasi DNA Genomik Sengon DNA genomik sengon diisolasi dari daun muda pohon sengon. Hasil uji integritas DNA metode 1, metode 2 dan metode 3 pada gel agarose dapat dilihat pada Gambar
HASIL DAN PEMBAHASAN Isolasi DNA Genomik Sengon DNA genomik sengon diisolasi dari daun muda pohon sengon. Hasil uji integritas DNA metode 1, metode 2 dan metode 3 pada gel agarose dapat dilihat pada Gambar
DIAGNOSIS VIRUS PENYAKIT JEMBRANA (VPJ) BERBASIS ASAM NUKLEAT
 Prosiding Konferensi Ilmiah Veteriner Nasional (KIVNAS) ke-13 Palembang, 23-26 November 2014 DIAGNOSIS VIRUS PENYAKIT JEMBRANA (VPJ) BERBASIS ASAM NUKLEAT *Asmarani Kusumawati 1,2, Atik Ratnawati 1, Ida
Prosiding Konferensi Ilmiah Veteriner Nasional (KIVNAS) ke-13 Palembang, 23-26 November 2014 DIAGNOSIS VIRUS PENYAKIT JEMBRANA (VPJ) BERBASIS ASAM NUKLEAT *Asmarani Kusumawati 1,2, Atik Ratnawati 1, Ida
Identifikasi Gen Abnormal Oleh : Nella ( )
 Identifikasi Gen Abnormal Oleh : Nella (10.2011.185) Identifikasi gen abnormal Pemeriksaan kromosom DNA rekombinan PCR Kromosom waldeyer Kromonema : pita spiral yang tampak pada kromatid Kromomer : penebalan
Identifikasi Gen Abnormal Oleh : Nella (10.2011.185) Identifikasi gen abnormal Pemeriksaan kromosom DNA rekombinan PCR Kromosom waldeyer Kromonema : pita spiral yang tampak pada kromatid Kromomer : penebalan
I. PENGENALAN NATIONAL CENTRE FOR BIOTECHNOLOGY INFORMATION (NCBI)
 I. PENGENALAN NATIONAL CENTRE FOR BIOTECHNOLOGY INFORMATION (NCBI) A. PENDAHULUAN NCBI (National Centre for Biotechnology Information) merupakan suatu institusi yang menyediakan sumber informasi terkait
I. PENGENALAN NATIONAL CENTRE FOR BIOTECHNOLOGY INFORMATION (NCBI) A. PENDAHULUAN NCBI (National Centre for Biotechnology Information) merupakan suatu institusi yang menyediakan sumber informasi terkait
ABSTRAK. ISOLASI, OPTIMASI AMPLIFIKASI DAN KLONING GEN phoq PADA Salmonella typhi
 ABSTRAK ISOLASI, OPTIMASI AMPLIFIKASI DAN KLONING GEN phoq PADA Salmonella typhi Patrisia Puspapriyanti, 2008. Pembimbing I : Ernawati A.Girirachman, Ph.D. Pembimbing II : Johan Lucianus, dr., M.Si. Salmonella
ABSTRAK ISOLASI, OPTIMASI AMPLIFIKASI DAN KLONING GEN phoq PADA Salmonella typhi Patrisia Puspapriyanti, 2008. Pembimbing I : Ernawati A.Girirachman, Ph.D. Pembimbing II : Johan Lucianus, dr., M.Si. Salmonella
BAB IV HASIL DAN PEMBAHASAN. Sintesis fragmen gen HA Avian Influenza Virus (AIV) galur
 20 BAB IV HASIL DAN PEMBAHASAN A. KONDISI OPTIMAL REAKSI AMPLIFIKASI Sintesis fragmen 688--1119 gen HA Avian Influenza Virus (AIV) galur A/Indonesia/5/2005 dilakukan dengan teknik overlapping extension
20 BAB IV HASIL DAN PEMBAHASAN A. KONDISI OPTIMAL REAKSI AMPLIFIKASI Sintesis fragmen 688--1119 gen HA Avian Influenza Virus (AIV) galur A/Indonesia/5/2005 dilakukan dengan teknik overlapping extension
BAB I PENDAHULUAN. A. Latar Belakang. dkk., 2009; Martin dkk., 2009; Koppel dkk., 2011).
 BAB I PENDAHULUAN A. Latar Belakang Pada beberapa tahun terakhir, identifikasi spesies hewan menjadi perhatian utama karena semakin meningkatnya kesadaran masyarakat terhadap bahan atau komposisi makanan
BAB I PENDAHULUAN A. Latar Belakang Pada beberapa tahun terakhir, identifikasi spesies hewan menjadi perhatian utama karena semakin meningkatnya kesadaran masyarakat terhadap bahan atau komposisi makanan
MAKALAH GENETIKA PCR ( Polimerase Chain Reaction ) «apikde...
 http://apikdewefppundip201wordpress.com/2012/06/29/makalah-gene... 1 of 6 19/12/2012 23:43 APIKDEWEFPPUNDIP2011 Just another WordPress.com site MAKALAH GENETIKA PCR ( Polimerase Chain Reaction ) JUN 29
http://apikdewefppundip201wordpress.com/2012/06/29/makalah-gene... 1 of 6 19/12/2012 23:43 APIKDEWEFPPUNDIP2011 Just another WordPress.com site MAKALAH GENETIKA PCR ( Polimerase Chain Reaction ) JUN 29
AMPLIFIKASI GEN 18S rrna PADA DNA METAGENOMIK MADU DARI DESA SERAYA TENGAH, KARANGASEM DENGAN TEKNIK PCR (POLYMERASE CHAIN REACTION)
 AMPLIFIKASI GEN 18S rrna PADA DNA METAGENOMIK MADU DARI DESA SERAYA TENGAH, KARANGASEM DENGAN TEKNIK PCR (POLYMERASE CHAIN REACTION) SKRIPSI Oleh: SATRIYA PUTRA PRAKOSO NIM. 1208105013 JURUSAN KIMIA FAKULTAS
AMPLIFIKASI GEN 18S rrna PADA DNA METAGENOMIK MADU DARI DESA SERAYA TENGAH, KARANGASEM DENGAN TEKNIK PCR (POLYMERASE CHAIN REACTION) SKRIPSI Oleh: SATRIYA PUTRA PRAKOSO NIM. 1208105013 JURUSAN KIMIA FAKULTAS
4 Hasil dan Pembahasan
 4 Hasil dan Pembahasan Dalam bab ini akan dipaparkan hasil dari tahap-tahap penelitian yang telah dilakukan. Melalui tahapan tersebut diperoleh urutan nukleotida sampel yang positif diabetes dan sampel
4 Hasil dan Pembahasan Dalam bab ini akan dipaparkan hasil dari tahap-tahap penelitian yang telah dilakukan. Melalui tahapan tersebut diperoleh urutan nukleotida sampel yang positif diabetes dan sampel
HASIL DAN PEMBAHASAN. Amplifikasi Gen Pituitary-Specific Positive Transcription Factor 1 (Pit1) Exon 3
 HASIL DAN PEMBAHASAN Amplifikasi Gen Pituitary-Specific Positive Transcription Factor 1 (Pit1) Exon 3 Amplifikasi gen Pit1 exon 3 pada sapi FH yang berasal dari BIB Lembang, BBIB Singosari, BPPT Cikole,
HASIL DAN PEMBAHASAN Amplifikasi Gen Pituitary-Specific Positive Transcription Factor 1 (Pit1) Exon 3 Amplifikasi gen Pit1 exon 3 pada sapi FH yang berasal dari BIB Lembang, BBIB Singosari, BPPT Cikole,
KOMPARASI SEKUENS DNA PADA VIRUS H5N1 PADA HOST MANUSIA DAN BURUNG MENGGUNAKAN METODE DIAGRAM POHON
 KOMPARASI SEKUENS DNA PADA VIRUS H5N1 PADA HOST MANUSIA DAN BURUNG MENGGUNAKAN METODE DIAGRAM POHON DOSEN PEMBIMBING Prof. Dr. M. Isa Irawan, MT DR. rer. nat. Ir. Maya Shovitri, M.Si SITI FAUZIYAH NRP.1209201716
KOMPARASI SEKUENS DNA PADA VIRUS H5N1 PADA HOST MANUSIA DAN BURUNG MENGGUNAKAN METODE DIAGRAM POHON DOSEN PEMBIMBING Prof. Dr. M. Isa Irawan, MT DR. rer. nat. Ir. Maya Shovitri, M.Si SITI FAUZIYAH NRP.1209201716
BAB I PENDAHULUAN. Mycobacterium tuberculosis adalah bakteri patogen penyebab tuberkulosis.
 BAB I PENDAHULUAN 1.1 Latar Belakang Mycobacterium tuberculosis adalah bakteri patogen penyebab tuberkulosis. Secara umum penyebaran bakteri ini melalui inhalasi, yaitu udara yang tercemar oleh penderita
BAB I PENDAHULUAN 1.1 Latar Belakang Mycobacterium tuberculosis adalah bakteri patogen penyebab tuberkulosis. Secara umum penyebaran bakteri ini melalui inhalasi, yaitu udara yang tercemar oleh penderita
TINJAUAN PUSTAKA Sapi Perah Friesian Holstein
 TINJAUAN PUSTAKA Sapi Perah Friesian Holstein Sapi Friesian Holstein (FH) merupakan bangsa sapi yang paling banyak terdapat di Amerika Serikat, sekitar 80-90% dari seluruh sapi perah yang berada di sana.
TINJAUAN PUSTAKA Sapi Perah Friesian Holstein Sapi Friesian Holstein (FH) merupakan bangsa sapi yang paling banyak terdapat di Amerika Serikat, sekitar 80-90% dari seluruh sapi perah yang berada di sana.
TINJAUAN PUSTAKA. Ikan Lele Dumbo (Clarias gariepinus) Menurut Kottelat dkk., (1993), klasifikasi dari ikan lele dumbo adalah.
 TINJAUAN PUSTAKA Ikan Lele Dumbo (Clarias gariepinus) Menurut Kottelat dkk., (1993), klasifikasi dari ikan lele dumbo adalah sebagai berikut: Kingdom Filum Kelas Ordo Family Genus : Animalia : Chordata
TINJAUAN PUSTAKA Ikan Lele Dumbo (Clarias gariepinus) Menurut Kottelat dkk., (1993), klasifikasi dari ikan lele dumbo adalah sebagai berikut: Kingdom Filum Kelas Ordo Family Genus : Animalia : Chordata
DAFTAR ISI. Halaman ABSTRAK... i ABSTRACT... ii DAFTAR ISI... iii DAFTAR GAMBAR... vi DAFTAR TABEL... vii DAFTAR LAMPIRAN... viii
 DAFTAR ISI ABSTRAK... i ABSTRACT... ii DAFTAR ISI... iii DAFTAR GAMBAR... vi DAFTAR TABEL... vii DAFTAR LAMPIRAN... viii BAB I PENDAHULUAN... 1 A. Latar Belakang Penelitian... 1 B. Rumusan Masalah Penelitian...
DAFTAR ISI ABSTRAK... i ABSTRACT... ii DAFTAR ISI... iii DAFTAR GAMBAR... vi DAFTAR TABEL... vii DAFTAR LAMPIRAN... viii BAB I PENDAHULUAN... 1 A. Latar Belakang Penelitian... 1 B. Rumusan Masalah Penelitian...
ANALISIS PRIMER UNTUK AMPLIFIKASI PROMOTER inha MULTIDRUG RESISTANCE TUBERCULOSIS (MDR-TB) DENGAN METODE POLYMERASE CHAIN REACTION (PCR)
 ANALISIS PRIMER UNTUK AMPLIFIKASI PROMOTER inha MULTIDRUG RESISTANCE TUBERCULOSIS (MDR-TB) DENGAN METODE POLYMERASE CHAIN REACTION (PCR) I Gusti Ayu Agung Septiari 1 *, Putu Sanna Yustiantara 1,2, dan
ANALISIS PRIMER UNTUK AMPLIFIKASI PROMOTER inha MULTIDRUG RESISTANCE TUBERCULOSIS (MDR-TB) DENGAN METODE POLYMERASE CHAIN REACTION (PCR) I Gusti Ayu Agung Septiari 1 *, Putu Sanna Yustiantara 1,2, dan
DAFTAR ISI. Halaman HALAMAN PERSETUJUAN... iii PERNYATAAN... PRAKATA... INTISARI... ABSTRACT... DAFTAR ISI... DAFTAR TABEL... DAFTAR GAMBAR...
 DAFTAR ISI Halaman HALAMAN PERSETUJUAN... iii PERNYATAAN... PRAKATA... INTISARI... ABSTRACT... DAFTAR ISI... DAFTAR TABEL... DAFTAR GAMBAR... DAFTAR LAMPIRAN... DAFTAR SINGKATAN... v vi viii ix x xiii
DAFTAR ISI Halaman HALAMAN PERSETUJUAN... iii PERNYATAAN... PRAKATA... INTISARI... ABSTRACT... DAFTAR ISI... DAFTAR TABEL... DAFTAR GAMBAR... DAFTAR LAMPIRAN... DAFTAR SINGKATAN... v vi viii ix x xiii
KONSTRUKSI PRIMER UNTUK MENDETEKSI MUTASI GEN rpob Mycobacterium tuberculosis DENGAN METODE AMPLIFICATION REFRACTORY MUTATION SYSTEM (ARMS)-PCR
 KONSTRUKSI PRIMER UNTUK MENDETEKSI MUTASI GEN rpob Mycobacterium tuberculosis DENGAN METODE AMPLIFICATION REFRACTORY MUTATION SYSTEM (ARMS)-PCR Arif Sardi Biologi, UIN Ar-Raniry, Banda Aceh, Indonesia
KONSTRUKSI PRIMER UNTUK MENDETEKSI MUTASI GEN rpob Mycobacterium tuberculosis DENGAN METODE AMPLIFICATION REFRACTORY MUTATION SYSTEM (ARMS)-PCR Arif Sardi Biologi, UIN Ar-Raniry, Banda Aceh, Indonesia
HASIL DAN PEMBAHASAN
 HASIL DAN PEMBAHASAN Amplifikasi Gen GH Gen GH exon 3 pada kambing PE, Saanen, dan PESA (Persilangan PE dan Saanen) berhasil diamplifikasi menggunakan metode PCR (Polymerase Chain Reaction). Panjang fragmen
HASIL DAN PEMBAHASAN Amplifikasi Gen GH Gen GH exon 3 pada kambing PE, Saanen, dan PESA (Persilangan PE dan Saanen) berhasil diamplifikasi menggunakan metode PCR (Polymerase Chain Reaction). Panjang fragmen
PENGENALAN NCBI UNTUK ANALISIS DNA, PROTEIN DAN SENYAWA KIMIA OLEH: W I D O D O MIFTAKHUNNAFISAH
 PENGENALAN NCBI UNTUK ANALISIS DNA, PROTEIN DAN SENYAWA KIMIA OLEH: W I D O D O MIFTAKHUNNAFISAH LABORATORIUM BIOSISTEM FAKULTAS MATEMATIKA dan ILMU PENGETAHUAN ALAM UNIVERSITAS BRAWIJAYA MALANG 2010 Pengenalan
PENGENALAN NCBI UNTUK ANALISIS DNA, PROTEIN DAN SENYAWA KIMIA OLEH: W I D O D O MIFTAKHUNNAFISAH LABORATORIUM BIOSISTEM FAKULTAS MATEMATIKA dan ILMU PENGETAHUAN ALAM UNIVERSITAS BRAWIJAYA MALANG 2010 Pengenalan
UNIVERSITAS SEBELAS MARET FAKULTAS MATEMATIKA DAN ILMU PENGETAHUAN ALAM S I L A B U S
 UNIVERSITAS SEBELAS MARET FAKULTAS MATEMATIKA DAN ILMU PENGETAHUAN ALAM S I L A B U S JURUSAN : Biologi MATA KULIAH : Biologi Molekuler 1.1. Nama Mata Kuliah : Biologi Molekuler 1.2. Kode Mata Kuliah :
UNIVERSITAS SEBELAS MARET FAKULTAS MATEMATIKA DAN ILMU PENGETAHUAN ALAM S I L A B U S JURUSAN : Biologi MATA KULIAH : Biologi Molekuler 1.1. Nama Mata Kuliah : Biologi Molekuler 1.2. Kode Mata Kuliah :
BAB IV HASIL DAN PEMBAHASAN
 15 BAB IV HASIL DAN PEMBAHASAN 4.1 Analisis DNA 4.1.1 Ekstraksi DNA Ekstraksi DNA merupakan langkah awal dalam analisis molekuler. Masalah-masalah yang timbul dalam ekstraksi DNA merupakan hal yang penting
15 BAB IV HASIL DAN PEMBAHASAN 4.1 Analisis DNA 4.1.1 Ekstraksi DNA Ekstraksi DNA merupakan langkah awal dalam analisis molekuler. Masalah-masalah yang timbul dalam ekstraksi DNA merupakan hal yang penting
4 HASIL DAN PEMBAHASAN
 4 HASIL DAN PEMBAHASAN 4.1 Karakteristik Morfologi Pada penelitian ini digunakan lima sampel koloni karang yang diambil dari tiga lokasi berbeda di sekitar perairan Kepulauan Seribu yaitu di P. Pramuka
4 HASIL DAN PEMBAHASAN 4.1 Karakteristik Morfologi Pada penelitian ini digunakan lima sampel koloni karang yang diambil dari tiga lokasi berbeda di sekitar perairan Kepulauan Seribu yaitu di P. Pramuka
III. HASIL DAN PEMBAHASAN
 III. HASIL DAN PEMBAHASAN 3.1 HASIL 3.1.1 Isolasi Vibrio harveyi Sebanyak delapan isolat terpilih dikulturkan pada media TCBS yaitu V-U5, V-U7, V-U8, V-U9, V-U24, V-U27, V-U41NL, dan V-V44. (a) (b) Gambar
III. HASIL DAN PEMBAHASAN 3.1 HASIL 3.1.1 Isolasi Vibrio harveyi Sebanyak delapan isolat terpilih dikulturkan pada media TCBS yaitu V-U5, V-U7, V-U8, V-U9, V-U24, V-U27, V-U41NL, dan V-V44. (a) (b) Gambar
IDENTIFIKASI ISOLAT BAKTERI DARI PANTAI BANDEALIT JEMBER BERDASARKAN SEKUEN DNA PENGKODE 16S rrna SKRIPSI. Oleh Dina Fitriyah NIM
 IDENTIFIKASI ISOLAT BAKTERI DARI PANTAI BANDEALIT JEMBER BERDASARKAN SEKUEN DNA PENGKODE 16S rrna SKRIPSI Oleh Dina Fitriyah NIM 061810401071 JURUSAN BIOLOGI FAKULTAS MATEMATIKA DAN ILMU PENGETAHUAN ALAM
IDENTIFIKASI ISOLAT BAKTERI DARI PANTAI BANDEALIT JEMBER BERDASARKAN SEKUEN DNA PENGKODE 16S rrna SKRIPSI Oleh Dina Fitriyah NIM 061810401071 JURUSAN BIOLOGI FAKULTAS MATEMATIKA DAN ILMU PENGETAHUAN ALAM
BAB III METODOLOGI PENELITIAN. Langkah-langkah yang dilakukan pada penelitian ini adalah :
 BAB III METODOLOGI PENELITIAN Langkah-langkah yang dilakukan pada penelitian ini adalah : pengumpulan sampel data urutan nukleotida daerah Hipervariabel II (HVII) DNA mitokondria (mtdna) pada penderita
BAB III METODOLOGI PENELITIAN Langkah-langkah yang dilakukan pada penelitian ini adalah : pengumpulan sampel data urutan nukleotida daerah Hipervariabel II (HVII) DNA mitokondria (mtdna) pada penderita
BAB 1 PENDAHULUAN 1.1 Latar Belakang Masalah
 BAB 1 PENDAHULUAN 1.1 Latar Belakang Masalah Selulase merupakan salah satu enzim yang dapat dihasilkan oleh beberapa kelompok hewan yang mengandung bakteri selulolitik, tumbuhan dan beberapa jenis fungi.
BAB 1 PENDAHULUAN 1.1 Latar Belakang Masalah Selulase merupakan salah satu enzim yang dapat dihasilkan oleh beberapa kelompok hewan yang mengandung bakteri selulolitik, tumbuhan dan beberapa jenis fungi.
BAB I PENDAHULUAN A. Latar belakang
 BAB I PENDAHULUAN A. Latar belakang Senyawa D-tagatosa merupakan suatu monosakarida hasil isomerisasi dari D- galaktosa. Monosakarida ini telah ditetapkan sebagai material GRAS (Generally Recognized as
BAB I PENDAHULUAN A. Latar belakang Senyawa D-tagatosa merupakan suatu monosakarida hasil isomerisasi dari D- galaktosa. Monosakarida ini telah ditetapkan sebagai material GRAS (Generally Recognized as
2015 ISOLASI DNA PARSIAL GEN
 1 BAB I PENDAHULUAN A. Latar Belakang Penelitian Ikan gurame (Osphronemus merupakan salah satu ikan air tawar yang termasuk ke dalam infraclass Teleostei (Integrated Taxonomic Information System, 2012).
1 BAB I PENDAHULUAN A. Latar Belakang Penelitian Ikan gurame (Osphronemus merupakan salah satu ikan air tawar yang termasuk ke dalam infraclass Teleostei (Integrated Taxonomic Information System, 2012).
IDENTIFIKASI DAGING TIKUS PADA PRODUK ASAL HEWAN DENGAN MENGGUNAKAN TEHNIK POLIMERASE CHAIN REACTION (PCR)
 IDENTIFIKASI DAGING TIKUS PADA PRODUK ASAL HEWAN DENGAN MENGGUNAKAN TEHNIK POLIMERASE CHAIN REACTION (PCR) Srihanto, E.A, Setiaji, G, Rumpaka, R dan Firwantoni Balai Veteriner Lampung Jalan Untung Suropati
IDENTIFIKASI DAGING TIKUS PADA PRODUK ASAL HEWAN DENGAN MENGGUNAKAN TEHNIK POLIMERASE CHAIN REACTION (PCR) Srihanto, E.A, Setiaji, G, Rumpaka, R dan Firwantoni Balai Veteriner Lampung Jalan Untung Suropati
BAB I PENDAHULUAN. Mycobacterium tuberculosis. Bakteri ini pada umumnya menyerang paru-paru
 BAB I PENDAHULUAN 1.1 Latar Belakang Tuberkulosis (TB) adalah penyakit menular yang disebabkan oleh infeksi Mycobacterium tuberculosis. Bakteri ini pada umumnya menyerang paru-paru (pulmonary tuberculosis),
BAB I PENDAHULUAN 1.1 Latar Belakang Tuberkulosis (TB) adalah penyakit menular yang disebabkan oleh infeksi Mycobacterium tuberculosis. Bakteri ini pada umumnya menyerang paru-paru (pulmonary tuberculosis),
ANALISA HASIL TRANSFORMASI DENGAN MENGGUNAKAN PCR KOLONI DAN RESTRIKSI
 1 ANALISA HASIL TRANSFORMASI DENGAN MENGGUNAKAN PCR KOLONI DAN RESTRIKSI PENDAHULUAN Polimerase Chain Reaction (PCR) PCR adalah suatu reaksi invitro untuk menggandakan jumlah molekul DNA pada target tertentu
1 ANALISA HASIL TRANSFORMASI DENGAN MENGGUNAKAN PCR KOLONI DAN RESTRIKSI PENDAHULUAN Polimerase Chain Reaction (PCR) PCR adalah suatu reaksi invitro untuk menggandakan jumlah molekul DNA pada target tertentu
HASIL DAN PEMBAHASAN. DNA Genom
 IV. HASIL DAN PEMBAHASAN A. Isolasi DNA Metode isolasi dilakukan untuk memisahkan DNA dari komponen sel yang lain (Ilhak dan Arslan, 2007). Metode isolasi ini sesuai dengan protokol yang diberikan oleh
IV. HASIL DAN PEMBAHASAN A. Isolasi DNA Metode isolasi dilakukan untuk memisahkan DNA dari komponen sel yang lain (Ilhak dan Arslan, 2007). Metode isolasi ini sesuai dengan protokol yang diberikan oleh
BAB I PENDAHULUAN. A. Latar Belakang Penelitian. daging yang beredar di masyarakat harus diperhatikan. Akhir-akhir ini sering
 BAB I PENDAHULUAN A. Latar Belakang Penelitian Produk makanan olahan saat ini sedang berkembang di Indonesia. Banyaknya variasi bentuk produk makanan olahan, terutama berbahan dasar daging yang beredar
BAB I PENDAHULUAN A. Latar Belakang Penelitian Produk makanan olahan saat ini sedang berkembang di Indonesia. Banyaknya variasi bentuk produk makanan olahan, terutama berbahan dasar daging yang beredar
VII. UJI EKSPRESI GEN TcAP1 (APETALA1 KAKAO) PADA TANAMAN MODEL. Abstrak
 VII. UJI EKSPRESI GEN TcAP1 (APETALA1 KAKAO) PADA TANAMAN MODEL Abstrak Pada berbagai spesies termasuk kakao, gen AP1 (APETALA1) diketahui sebagai gen penanda pembungaan yang mengendalikan terbentuknya
VII. UJI EKSPRESI GEN TcAP1 (APETALA1 KAKAO) PADA TANAMAN MODEL Abstrak Pada berbagai spesies termasuk kakao, gen AP1 (APETALA1) diketahui sebagai gen penanda pembungaan yang mengendalikan terbentuknya
DAFTAR ISI DAFTAR SINGKATAN DAN LAMBANG
 DAFTAR ISI ABSTRAK... Error! ABSTRACT... Error! KATA PENGANTAR... Error! DAFTAR ISI... i DAFTAR SINGKATAN DAN LAMBANG... Error! BAB I PENDAHULUAN... Error! 1.1 Latar Belakang... Error! 1.2 Rumusan Masalah...
DAFTAR ISI ABSTRAK... Error! ABSTRACT... Error! KATA PENGANTAR... Error! DAFTAR ISI... i DAFTAR SINGKATAN DAN LAMBANG... Error! BAB I PENDAHULUAN... Error! 1.1 Latar Belakang... Error! 1.2 Rumusan Masalah...
HASIL DAN PEMBAHASAN. Amplifikasi Daerah D-loop M B1 B2 B3 M1 M2 P1 P2 (-)
 HASIL DAN PEMBAHASAN Amplifikasi Daerah D-loop Amplifikasi daerah D-loop DNA mitokondria (mtdna) pada sampel DNA sapi Bali, Madura, Pesisir, Aceh, dan PO dilakukan dengan menggunakan mesin PCR Applied
HASIL DAN PEMBAHASAN Amplifikasi Daerah D-loop Amplifikasi daerah D-loop DNA mitokondria (mtdna) pada sampel DNA sapi Bali, Madura, Pesisir, Aceh, dan PO dilakukan dengan menggunakan mesin PCR Applied
AKTIVITAS ANTIJAMUR BAKTERI ENDOFIT LAMUN TERHADAP JAMUR PATOGEN
 AKTIVITAS ANTIJAMUR BAKTERI ENDOFIT LAMUN TERHADAP JAMUR PATOGEN Oleh : AISA AZIZA AN NURIAH 26020110120055 Skripsi sebagai Salah Satu Syarat untuk Memperoleh Derajat Sarjana S1 pada Program Studi Ilmu
AKTIVITAS ANTIJAMUR BAKTERI ENDOFIT LAMUN TERHADAP JAMUR PATOGEN Oleh : AISA AZIZA AN NURIAH 26020110120055 Skripsi sebagai Salah Satu Syarat untuk Memperoleh Derajat Sarjana S1 pada Program Studi Ilmu
PRAKATA. Alhamdulillah syukur senantiasa penulis panjatkan kepada Allah swt., atas
 PRAKATA Alhamdulillah syukur senantiasa penulis panjatkan kepada Allah swt., atas segala nikmat dan karunia-nya, penulisan Tugas Akhir dengan judul Keragaman Genetik Abalon (Haliotis asinina) Selat Lombok
PRAKATA Alhamdulillah syukur senantiasa penulis panjatkan kepada Allah swt., atas segala nikmat dan karunia-nya, penulisan Tugas Akhir dengan judul Keragaman Genetik Abalon (Haliotis asinina) Selat Lombok
Bioteknologi Tanaman KULIAH V. PCR, Sekuensing. Dr. Jamsari, Prog. Studi Pemuliaan Tanaman Jurusan BDP-FPUA
 Bioteknologi Tanaman KULIAH V PCR, Sekuensing Dr. Jamsari, Prog. Studi Pemuliaan Tanaman Jurusan BDP-FPUA Copyright Statement: Dengan ini dinyatakan, bahwa seluruh material (teks, gambar, grafik dan seluruh
Bioteknologi Tanaman KULIAH V PCR, Sekuensing Dr. Jamsari, Prog. Studi Pemuliaan Tanaman Jurusan BDP-FPUA Copyright Statement: Dengan ini dinyatakan, bahwa seluruh material (teks, gambar, grafik dan seluruh
HASIL DAN PEMBAHASAN. Gambar 4. Hasil Amplifikasi Gen FSHR Alu-1pada gel agarose 1,5%.
 HASIL DAN PEMBAHASAN Amplifikasi Gen FSHR Alu-1 Amplifikasi fragmen gen FSHR Alu-1 dengan metode Polymerase Chain Reaction (PCR) dilakukan dengan kondisi annealing 60 C selama 45 detik dan diperoleh produk
HASIL DAN PEMBAHASAN Amplifikasi Gen FSHR Alu-1 Amplifikasi fragmen gen FSHR Alu-1 dengan metode Polymerase Chain Reaction (PCR) dilakukan dengan kondisi annealing 60 C selama 45 detik dan diperoleh produk
HASIL DAN PEMBAHASAN. pb M 1 2. pb M 1 2. pb M 1 2. (a) (b) pb M 1 2. pb M pb M 1 2. pb M (d) (e) (c)
 HASIL DAN PEMBAHASAN Amplifikasi dan Visualisasi DNA Endo-β- 1,4- glukanase C. curvignathus Amplifikasi DNA ekson 1 dan 5 CcEG menggunakan pasangan primer eksternal (Tabel 2) dan masing-masing menunjukkan
HASIL DAN PEMBAHASAN Amplifikasi dan Visualisasi DNA Endo-β- 1,4- glukanase C. curvignathus Amplifikasi DNA ekson 1 dan 5 CcEG menggunakan pasangan primer eksternal (Tabel 2) dan masing-masing menunjukkan
MATERI DAN METODE. Lokasi dan Waktu. Materi. Tabel 1. Jumah Sampel Darah Ternak Sapi Indonesia Ternak n Asal Sapi Bali 2 4
 MATERI DAN METODE Lokasi dan Waktu Penelitian dilaksanakan di Laboratorium Genetika Molekuler Ternak, Bagian Pemuliaan dan Genetika Ternak, Fakultas Peternakan, Institut Pertanian Bogor. penelitian ini
MATERI DAN METODE Lokasi dan Waktu Penelitian dilaksanakan di Laboratorium Genetika Molekuler Ternak, Bagian Pemuliaan dan Genetika Ternak, Fakultas Peternakan, Institut Pertanian Bogor. penelitian ini
Teknik-teknik Dasar Bioteknologi
 Teknik-teknik Dasar Bioteknologi Oleh: TIM PENGAMPU Program Studi Agroteknologi Fakultas Pertanian Universitas Jember Tujuan Perkuliahan 1. Mahasiswa mengetahui macam-macam teknik dasar yang digunakan
Teknik-teknik Dasar Bioteknologi Oleh: TIM PENGAMPU Program Studi Agroteknologi Fakultas Pertanian Universitas Jember Tujuan Perkuliahan 1. Mahasiswa mengetahui macam-macam teknik dasar yang digunakan
REPLIKASI DAN POLYMERASE CHAIN REACTION (PCR)
 REPLIKASI DAN POLYMERASE CHAIN REACTION (PCR) Debbie S. Retnoningrum Sekolah Farmasi, ITB Pustaka: 1. Glick, BR and JJ Pasternak, 2003, hal. 27-28; 110-120 2. Groves MJ, 2006, hal. 40 44 3. Brown TA, 2006,
REPLIKASI DAN POLYMERASE CHAIN REACTION (PCR) Debbie S. Retnoningrum Sekolah Farmasi, ITB Pustaka: 1. Glick, BR and JJ Pasternak, 2003, hal. 27-28; 110-120 2. Groves MJ, 2006, hal. 40 44 3. Brown TA, 2006,
TINJAUAN PUSTAKA. Elaeidobius kamerunicus Faust. (Coleoptera : Curculionidae) Kumbang ini mengalami metamorfosis sempurna (holometabola), yakni
 TINJAUAN PUSTAKA Elaeidobius kamerunicus Faust. (Coleoptera : Curculionidae) Kumbang ini mengalami metamorfosis sempurna (holometabola), yakni siklus hidupnya terdiri dari telur larva pupa imago. E. kamerunicus
TINJAUAN PUSTAKA Elaeidobius kamerunicus Faust. (Coleoptera : Curculionidae) Kumbang ini mengalami metamorfosis sempurna (holometabola), yakni siklus hidupnya terdiri dari telur larva pupa imago. E. kamerunicus
PENERAPAN METODE POLYMERASE CHAIN REACTION MENGGUNAKAN PRIMER 16E1 DAN 16E2 UNTUK. MENDETEKSI Escherichia coli DALAM BERBAGAI SAMPEL AIR
 PENERAPAN METODE POLYMERASE CHAIN REACTION MENGGUNAKAN PRIMER 16E1 DAN 16E2 UNTUK MENDETEKSI Escherichia coli DALAM BERBAGAI SAMPEL AIR ANGLIA PUSPANINGRUM 0304050082 UNIVERSITAS INDONESIA FAKULTAS MATEMATIKA
PENERAPAN METODE POLYMERASE CHAIN REACTION MENGGUNAKAN PRIMER 16E1 DAN 16E2 UNTUK MENDETEKSI Escherichia coli DALAM BERBAGAI SAMPEL AIR ANGLIA PUSPANINGRUM 0304050082 UNIVERSITAS INDONESIA FAKULTAS MATEMATIKA
BABm METODE PENELITIAN
 BABm METODE PENELITIAN 3.1 Jenis Penelitian Penelitian ini merupakan penelitian analitik dengan desain cross-sectioned, yaitu untuk mengetahui apakah terdapat perbedaan distnbusi genotipe dan subtipe VHB
BABm METODE PENELITIAN 3.1 Jenis Penelitian Penelitian ini merupakan penelitian analitik dengan desain cross-sectioned, yaitu untuk mengetahui apakah terdapat perbedaan distnbusi genotipe dan subtipe VHB
